최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 경북대학교 KyungPook National University |
|---|---|
| 연구책임자 | 황의욱 |
| 참여연구자 | 김익수 , 원용진 , 이준상 , 김사흥 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2018-12 |
| 과제시작연도 | 2018 |
| 주관부처 | 환경부 Ministry of Environment |
| 등록번호 | TRKO201900027532 |
| 과제고유번호 | 1485015635 |
| 사업명 | 생물자원발굴및분류연구(R&D) |
| DB 구축일자 | 2020-04-18 |
Ⅱ. 연구결과 및 정책적 제언
1. 유전다양성 분석 결과
1) 검붉은수지맨드라미
검붉은수지맨드라미는 멸종위기 II급 종으로서 지구온난화로 인해 발생하는 환경변화에 밀접한 영향을 받는 해양생물 중 하나이다. 검붉은수지맨드라미의 개체군 분포현황도 중요하지만 제주와 남해안 일대에서 서식하는 협소한 서식지로 인해 근친교배의 위험성은 없는지에 대한 유전적 건강도 평가가 필요하다. 본 연구에서는 검붉은수지맨드라미의 생태학적 특성 및 유전다양성 분석에 대한 비교 분석을 통해 국내 검붉은수지맨드라미의 유전적 건강성을 평가하고 종합
Ⅱ. 연구결과 및 정책적 제언
1. 유전다양성 분석 결과
1) 검붉은수지맨드라미
검붉은수지맨드라미는 멸종위기 II급 종으로서 지구온난화로 인해 발생하는 환경변화에 밀접한 영향을 받는 해양생물 중 하나이다. 검붉은수지맨드라미의 개체군 분포현황도 중요하지만 제주와 남해안 일대에서 서식하는 협소한 서식지로 인해 근친교배의 위험성은 없는지에 대한 유전적 건강도 평가가 필요하다. 본 연구에서는 검붉은수지맨드라미의 생태학적 특성 및 유전다양성 분석에 대한 비교 분석을 통해 국내 검붉은수지맨드라미의 유전적 건강성을 평가하고 종합적 고찰을 수행하고자 한다.
(가) 검붉은수지맨드라미 유전자 다양성 분석
국내 서식하는 검붉은수지맨드라미를 대상으로 4개 집단 14개체를 확보하였으며, microsatellites marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 모두 PIC>0.5 이상으로 모든 마커를 집단분석에 안정적으로 사용될 수 있음을 보여준다. 검붉은수지맨드라미의 집단별 유전적 다양성은 대체로 비슷한 수준이며, 이형접합자 관측치(HO)는 제주 숲섬(JJ-FS) 집단에 서 가장 낮은 수치가 계산되었다(HO=0.450~0.833). 근친계수(FIS) 분석에서도 모든 집단에 음(-)의 FIS 값이 관찰됨에 따라 심각한 유전적 감소가 이루어지는 상황은 아닌 것으로 판단된다.
(나) 집단구조 분석
유전적 분화정도에 대한 분석에서 전체 검붉은수지맨드라미 집단은 비교적 높은 수치가 계산되었으나, 집단 내 특이한 유전적 구조를 설명하기에는 유효집단의 수가 적어 어려움이 있다. 하지만, 제주 숲섬 집단의 경우 다른 집단과의 유전적 분화지수와 유전적 흐름지수, 주성분 분석(PCoA)에서 다소 분리된 집단으로서 별도의 유전적 구조를 가지는 것으로 판단된다. 따라서 향후 검붉은수지맨드라미에 대한 다양성 보전에 대한 정책 수립시 숲섬 개체군을 별도의 보존단위로 설정하는 등 새로운 검토가 필요하다.
(다) 보전 방안 및 유전자 정보 활용: 서식현황 및 유전자 다양성 분석을 통한 종합적인 종보전 고찰
본 연구에서는 국내에 서식하는 검붉은수지맨드라미 4개 집단 14개체를 대상으로 유전정보를 확보하였으며, 총 10개의 microsatellites 마커를 선별, PIC>0.5이상으로 높은 informativeness를 보여준다. 집단 간에 높은 유전적 분화지수(FST)가 계산되었으며, 특히 제주 숲섬 개체군이 다른 집단에 비해 유전적 거리가 큰 것으로 판단된 다. 대부분의 산호류의 북방한계선이 제주해역으로서 국내에서는 제주도에서만 분포하는 경우가 많다. 하지만 검붉은수지맨드라미의 경우, 북방한계선이 부산인근 해역까지 올라와 제주도와 남해안 연안에 분포한다. 검붉은수지맨드라미를 포함한 산호류의 분포양상을 살펴보면 남해안과 제주 해역의 분포상이 구분되는데, 본 연구 결과 검붉은수지맨드라미의 경우에도 제주 섶섬 집단을 제외하고는 유전적으로 유사한 양상을 보인다. 대부분의 산호류(법정 보호종)는 제주 남부지역(숲섬, 문섬, 범섬)에 집중적으로 서식하는데 다른 지역에 비해 2~3배 이상 많은 산호류가 서식, 우점한다. 또한 제주 남부 지역을 기점으로 제주난류가 시계방향으로 회전하며 산호류의 유생 이동에 영향을 미친다. 현재까지 알려진 바로는 제주 동부와 서부 지역의 생물분포상이 유사하고, 남부지역은 동부와 서부 가운데 위치함에도 불구하고 생물상에 차이가 있으며, 북부 지역이 가장 차이가 큰 것으로 보고된다.
해양생물은 수온뿐만 아니라 주변 지역의 해류의 영향에 따라 분포양상이 크게 달라진다. 제주 인근 해역으로 북상한 쿠로시오 해류에서 분지된 대마난류는 제주 동부를 지나 대마도 인근에서 이분화되어 부산 인근 해역으로 지나간다. 검붉은수지맨드라미의 경우 대마난류의 영향으로 제주에서 남해안(경남, 부산) 지역으로 서식 분포가 확산되었을 것으로 추정되며, 향후 지구온난화로 인해 수온이 상승한다면 동해안 지역으로 북상할 가능성이 있다(서해안의 경우, 갯벌로 인해 탁도가 높아 서식환경이 적합하지 않음). 산호류의 서식범위와 분포양상을 분석해보면 추자도와 관탈도 사이에서 남해안과 제주 해역의 2개 계군으로 분리되는데, 유전다양성 분석결과 검붉은수지맨드라미의 경우 조금 더 아래쪽인 성산포 인근에서 2개 유전적 lineage로 나누어진다.
이는 PCoA와 structure 분석에서도 동일한 결과를 확인하였다. 국내에 서식하는 검붉은수지맨드라미의 유전다양성 및 개체군 서식정보를 종합적으로 분석해보면, 인위적인 위협요인이 발견되지 않으며, 개체군이 안정적으로 서식하고 있고, 다년간의 서식지 현황을 조사결과, 개체군의 감소 추이가 발견되지 않는다. 또한 대마난류의 해류를 따라 분포하는 산호류의 특성상 남해안과 제주 해역에서 각각 2개 지점에 서식하는 개체군을 대상으로 유전다양성 분석을 수행하였으며, 집단간 높은 유전적 분화지수와 낮은 근친계수가 계산되어 유전적 감소현상이 발견되지 않고 안정적인 단계인 것으로 판단된다. 추자도와 관탈도 사이 해역을 중심으로 남해안과 제주 해역으로 2개 계군으로 나누어지는 산호류의 분포특성과는 달리 검붉은수지맨드라미의 성산포 인근 지점에서 분리되는 결과를 유전다양성 분석을 통해 확인하였다. 본 연구결과는 추후 동아시아 지역 검붉은수지맨드라미의 집단분석 및 범적 보호종 지정/해제 여부를 판단하는 기초자료로 활용할 수 있을 것으로 생각된다.
2) 자색수지맨드라미
자색수지맨드라미는 멸종위기 II급 종으로서 국내에서 흔히 발견되는 종은 아니었으나 2000년대 초반부터 서귀포시 주변 해역에서 안정적인 군락지를 형성하고 있다.
지난 20여 년간 개체군이 증가추세에 있으며, 이는 해수의 온도가 상승한 영향도 있지만 제주 남부지역의 경우 생태계 보호구역으로서 다른 지역에 비해 해양 생태계 보존 및 관리가 잘 이루어지고 있어 개체군이 증가된 것으로 예상된다. 하지만 국내 집단내에서도 최근 이입 후 개체수가 증가하였다면 협소한 서식지로 인한 근친교배의 위험성은 없는지에 대한 유전적 건강도 평가가 필요하다. 본 연구에서는 자색수지맨드라미의 생태학적 특성 및 유전다양성 분석에 대한 비교 분석을 통해 국내 자색수지 맨드라미의 유전적 건강성을 평가하고 종합적 고찰을 수행하고자 한다.
(가) 자색수지맨드라미의 유전자 다양성 분석
본 연구에서는 자색수지맨드라미를 대상으로 3개 집단 10개체를 확보하였으며, 10개의 microsatellites marker를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 모두 PIC>0.5 이상으로 모든 마커를 집단분석에 안정적으로 사용될 수 있음을 보여준다. 자색수지맨드라미의 집단별 유전적 다양성은 검붉은수지맨드라미와 대체로 비슷한 수준이며, 근친계수(FIS) 분석에서 모든 집단이 음(-)의 FIS 값이 관찰됨에 따라 심각한 유전적 감소가 이루어지는 상황은 아닌 것으로 판단된다.
(나) 집단구조 분석
전반적인 유전적 다양성 분석에서 보면, 제주지역의 자색수지맨드라미 집단은 3개의 서식지 모두 하나의 집단으로 볼 수 있으나 문섬 한개창 집단의 경우 다소 유전적 차이가 발견된다. 하지만 집단별로 유효개체수가 너무 적어서 집단 간의 분석이 유의성 검증이 어렵다고 판단된다. 문섬의 한개창과 새끼섬 집단은 지리적 거리가 다소 떨어져 있어서 다른 집단으로 판단되는데, 특이한 점은 새끼섬 집단이 숲섬집단과 유사도가 높은 것으로 계산되며, 실제로 두 집단간 유전적 분화지수(FST) 값이 0.099로 낮은 편이다. 유전적 분화도가 무시되는 <0.05 보다는 다소 높지만 새끼섬과 숲섬 간의 유전적 흐름이 어느 정도 발생한 것으로 보아, 향후 지속적인 모니터링이 필요할 것으로 판단된다.
(다) 보전 방안 및 유전자 정보 활용: 서식현황 및 유전자 다양성 분석을 통한 종합적인 종보전 고찰
자색수지맨드라미는 서식 범위가 협소하여 많은 개체군을 확보하는 데에는 어려움이 있는 산호류이지만 제주 남부지역에 우점하는 종으로서 남부 해역에 서식하는 자색수지맨드라미 개체군의 근친교배의 위험은 없는지에 대한 검증이 필요하다. 본 연구에서 제주 남부지역에 서식하는 자색수지맨드라미 개체군은 집단간 높은 유전적 분화도(FST=0.099~0.350)가 계산되며, 집단별 근친계수(FIS) 분석 결과에서도 모든 집단에서 음(-)의 값을 나타내며, 근친교배의 위험 또는 유전적 감소 현상은 없는 것으로 예측되어, 짧은 시간에 개체군이 급증한 것에 비해서는 유전적으로 매우 안정적인 상태를 취하고 있다. 문섬 지역에서 한개창과 새끼섬 집단은 지리적으로 다소 거리가 있어서 다른 개체군이라 판단하여 분석을 수행하였다. 특이한 점은 문섬 새끼섬의 자색수지맨드라미는 섶섬 집단의 자색수지맨드라미와 유전적으로 더 가까운 유전적 구조가 계산되었으며 문섬 한 개창 집단은 다른 지역에 비해 유전적으로 차이가 있는 것으로 확인된다. 따라서 문섬 한개창 집단에 대한 별도의 보존단위 지정 및 지속적인 유전적 모니터링이 필요하다.
3) 밤수지맨드라미
(가) 밤수지맨드라미의 유전자 다양성 분석
본 연구에서는 밤수지맨드라미를 대상으로 2개 집단 7개체를 확보하였으며, MS marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 모두 PIC>0.5 이상으로 모든 마커를 집단분석에 안정적으로 사용될 수 있음을 보여준다. 밤수지맨드라미의 집단별 유전적 다양성은 검붉은수지맨드라미와 대체로 비슷한 수준이며, 근친계수(FIS) 분석에서 모든 집단이 음(-)의 FIS 값이 관찰됨에 따라 심각한 유전적 감소가 이루어지는 상황은 아닌 것으로 판단된다. 하지만 숲섬 집단의 경우 거의 0에 가까운 –0.009의 수치가 계산되었다.
(나) 집단구조 분석
전반적인 유전적 다양성 분석에서 보면, 제주지역의 밤수지맨드라미 집단은 3개의 서식지 모두 하나의 집단으로 볼 수 있으나 문섬 집단의 경우 다른 집단에 비해 집중되어 있으며, 약간의 유전적 격리가 발견된다. 하지만 집단별로 유효개체수가 너무 적어서 집단 간의 분석이 유의성 검증이 어렵다고 판단된다.
(다) 보전 방안 및 유전자 정보 활용: 서식현황 및 유전자 다양성 분석을 통한 종합적인 종보전 고찰
밤수지맨드라미는 과거 남해안에서 관찰이 보고되었으나 최근 산호류 조사 연구 결과들이나 본 연구의 산호류 채집 조사에서도 남해안에서는 관찰되지 않았으며 지주 전역에서 발견되지만 대부분 남부지역에 집중적으로 분포한다. 과거에는 흔한 종이 아니었으나, 최근 수온상승으로 인해 매년 개체군을 확장되고 있어 지속적인 모니터링이 필요한 산호류이다. 본 연구에서 확보한 제주 문섬과 섶섬 개체군의 경우 유전적 분화도가 0.210으로 높은 수준을 유지하고 있으며, 집단별 근친계수(FIS) 분석 결과, 모든 집단에서 음(-)의 값을 나타내며, inbreeding의 위험 또는 극심한 유전적 감소 현상은 없는 것으로 예측된다. 하지만 0에 가까운 수치가 계산된 숲섬 집단의 경우 향후 지속적인 유전다양성 모니터링을 통해 변화추이에 대한 관찰이 필요하다.
4) 긴가지해송
(가) 긴가지해송의 유전자 다양성 분석
국내 서식하는 긴가지해송을 대상으로 3개 집단 14개체를 확보하였으며, microsatellites marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 모두 PIC>0.5 이상으로 모든 마커를 집단분석에 안정적으로 사용될 수 있음을 보여준다. 긴가지해송의 집단별 유전적 다양성은 대체로 비슷한 수준이며, 이형접합자 관측치(HO)는 부산 집단이 가장 낮았다(HO=0.6050~0.7750). 근친계수(FIS) 분석에서도 거문도 집단에 음(-)의 FIS 값이 관찰됨에 따라 심각한 유전적 감소가 이루어지는 상황은 아닌 것으로 판단된다.
(나) 집단구조 분석
유전적 분화정도에 대한 분석에서 전체 긴가지해송 집단은 비교적 높은 수치가 계산되었으나, 집단 내 특이한 유전적 구조를 설명하기에는 유효집단의 수가 적어 어려움이 있다. 하지만 이러한 경우 대부분이 멸종 위기종 또는 특산종에서 자주 발견되는 현상으로 분석에 기 사용한 긴가지해송 개체군은 집단 간 다소 격리되어 발생한 결과로 생각된다. 예외적으로 거문도와 부산의 2개 집단은 FST 수치가 다른 집단에 비해 극단적으로 낮은 값을 보여주는데, 이는 두 집단 간의 유전적 다양성이 낮고 최근 유전적 교류의 발생이 예상된다. 전반적인 유전적 다양성 분석에서 보면, 한국의 긴가지해송 집단은 3개의 서식지 모두 하나의 집단으로 볼 수 있었는데 이는 genotyping 분석, 주성분 분석(PCoA), Structure 분석 결과에서 모두 동일하게 지지하는 결론을 확인하였다. 다만, 집단별로 개체수가 너무 적어서 집단 간의 분석이 유의성 검증이 어렵다고 판단된다.
(다) 보전 방안 및 유전자 정보 활용
국내 3집단 14개체의 긴가지해송을 대상으로 유전다양성 분석을 수행하였으며, 전체 집단은 비교적 높은 유전적 분화 수치가 계산되었다. 이는 집단 내 특별한 유전적 구조를 설명하기에는 유효집단의 수가 적어서 명확하게 해석하기는 힘들지만, 보통 이러한 현상은 많은 멸종위기종이나 특정 지역에 국한하여 서식하는 특산종 등에서 자주 발견되는 현상이다. 하지만 거문도(GM) 집단과 부산(DD) 집단의 FST 값은 다른 집단에 비해 극단적으로 낮은 값을 보여준다(FST=0.008, RST=0.008). 낮은 FST 수치는 두 집단 간의 유전적 다양성이 낮고 최근 유전적 교류의 발생을 예상할 수 있다. 따라서 지속적인 유전적 모니터링을 통하여 남해안 해역의 거문도와 부산 인근 해역 집단의 유전적 흐름 정도를 파악하고, 유전적 교류를 통한 집단의 확장 여부에 대한 관찰도 추가적으로 필요하다.
5) 염주알다슬기
(가) 염주알다슬기의 유전자 다양성 분석
본 연구에서는 염주알다슬기를 대상으로 3개 집단 60개체를 확보하였으며, microsatellites marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 모두 PIC>0.5 이상으로 모든 마커를 집단분석에 안정적으로 사용될 수 있음을 보여준다. 염주알다슬기는 강원도 지역에만 국한하여 서식하는 한반도 고유종으로써 타 집단의 개체 확보는 불가능한 일이다. 본 연구에서는 특정 지역에만 서식하는 생물종의 특성상 유전다양성 감소 발생에 대한 우려가 있었다. 하지만 평균 대립인자 수도 3이상으로 평이하고, 집단별 근친계수(FIS) 분석 결과, 모든 집단에서 음(-)의 값을 나타내며, inbreeding의 위험 또는 유전적 감소 현상은 없는 것으로 예측된다.
(나) 집단구조 분석
전반적인 유전적 다양성 분석에서 보면, 염주알다슬기의 genotyping 분석 결과, 염주알다슬기의 유전다양성은 우려할 만한 수준은 아닌 것으로 판단되나, 2개의 genetic lineage가 확인되어, 추가적인 분석이 필요하다. 현재 염주알다슬기의 학명은 Melania nodifila 를 채택하여 사용하고 있으며(Worms, 2018), Koreanomelania nodifila 는 동종이명으로 간주하고 있다. 현재까지 국내 염주알다슬기의 아종 또는 신종이 보고될 가능성은 적을 것으로 판단되지만, 동종이명으로 기록된 2종에 대한 형태학적 분석 및 집단분석에 대한 종합적인 연구를 수행한다면 종 수준의 차이 여부에 대한 판단이 가능할 것으로 생각된다.
(다) 보전 방안 및 유전자 정보 활용
국내 염주알다슬기의 집단별 평균 대립인자의 수(Na)와 유효대립인자 수(NE)는 3개의 분석집단에서 각각 평균 3.567, 2.418로 비슷한 수준을 유지하고 있다. 이형접합자 예측치(HE)와 관측치(HO)는 각각 평균 0.710과 0.551로 계산되었다. 전체 집단에서 유전적 다양성 정도는 집단 간 큰 차이를 보이지는 않았지만 전반적으로 유전적으로 양호한 상황인 것으로 판단된다.
염주알다슬기는 현재 강원도 일대에서만 서식하는 것으로 알려진 한국 고유종이다. 서식지역이 강원도 인제, 영월, 평창지역으로 국한되어 있어서 지역적으로 유전적 차이가 크지 않고 집단별로 뚜렷한 유전적 구조도 확인되지 않는다. 염주알다슬기가 고유종이라 현재까지 동일종 또는 유사종에 대한 다양성 분석 지수가 보고된 바가 없다. 하지만 일반적으로 평균 대립인자 수(Na)가 하나에 불과하다면 해당 생물종 집단은 높은 근친교배율과 멸종 위험에 직면한 것으로 판단한다(Miller et al., 2013). 한국의 염주알다슬기의 경우 집단별로 3이상의 평균 대립인자수를 보유하고 있으며, 집단별 근친계수(FIS) 분석 결과, 모든 집단에서 음(-)의 값을 나타내며, inbreeding의 위험 또는 유전적 감소 현상은 없는 것으로 예측된다.
특이한 점은 집단간 유전적 구조는 확인되지 않았고 집단간 구분 없이 크게 2개의 그룹으로 나누어짐을 확인했다. 이는 한국의 염주알다슬기 집단 내에서 서로 다른 유전적 lineage가 존재하는 것을 시사한다. 하지만 신종 또는 미기록종에 대한 가능성을 타진해보기 위해서는 추가 개체군 확보 등 확장연구를 통한 추가 분석이 필요하다.
6) 울릉도달팽이
(가) 울릉도달팽이의 유전자 다양성 분석
본 연구에서는 울릉도달팽이를 대상으로 2개 집단 11개체를 확보하였으며, microsatellites marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 10개 마커 중에서 4개 마커에서 PIC>0.5 이상으로 informativeness를 확인하였으며 집단분석서 유의미하게 사용할 수 있을 것으로 판단된다. 울릉도달팽이는 울릉도 지역에만 국한하여 서식하는 한반도 고유종으로써 특정 지역에만 서식하는 생물종의 특성상 유전다양성 감소 발생에 대한 우려가 있었다.
분석 개체수가 적어서 평균 대립인자 수가 2개로 계산되었지만, 집단별 근친계수(FIS) 분석 결과, 모든 집단에서 음(-)의 값을 나타내며, inbreeding의 위험 또는 유전적감소 현상은 없는 것으로 예측된다.
(나) 집단구조 분석
전반적인 유전적 다양성 분석에서 보면, 울릉도의 울릉도달팽이 집단은 2개의 서식지 모두 하나의 집단으로 볼 수 있는데 이는 genotyping 분석 결과에서 동일하게 지지하는 결론을 확인하였다. 다만, 집단별로 개체수가 너무 적어서 집단 간의 분석이 유의성 검증이 어렵다고 판단된다.
(다) 보전 방안 및 유전자 정보 활용
본 연구에 사용된 울릉도달팽이는 총 11개체로서 유전다양성을 설명하기 위해서는 유효개체수가 부족하여 유의성을 검증하는 데에는 어려움이 있으나, 분석결과 울릉도 개체군은 모두 하나의 집단으로 판단된다. 근친계수 및 유전분화도 지수 분석에서 유전적 감소 현상이 발견되지 않았으며, 집단간 유전분화도 지수도 높게 계산되어 유전적으로 우려할 만한 상황은 아닌 것으로 생각된다. 하지만 국내 단일 지역에서만 서식하는 생물종으로서 급격한 환경변화를 예의 주시해야하며 지속적인 모니터링을 통해 개체군이 유지될 수 있는 보호정책이 필요하다.
7) 띠구슬다슬기
(가) 띠구슬다슬기의 유전자 다양성 분석
본 연구에서는 띠구슬다슬기를 대상으로 3개 집단 60개체를 확보하였으며, microsatellites marker 10개를 선별하고 개체별로 genotyping 분석 및 유전적 다양성 분석을 수행하였다. 선별된 마커 중에서 PIC>0.5 이상으로 계산된 마커는 8개이며, 이는 집단분석에 안정적으로 사용될 수 있음을 보여준다. 띠구슬다슬기는 강원도 지역에만 국한하여 서식하는 종으로서 타 집단의 개체 확보는 불가능한 일이다. 본 연구에서는 강원도 지역에만 서식하는 생물종의 특성상 유전다양성 감소 발생에 대한 우려가 있었다. 하지만 집단별 근친계수(FIS) 분석 결과, 모든 집단에서 음(-)의 값을 나타내며, inbreeding의 위험 또는 유전적 감소 현상은 없는 것으로 예측된다.
(나) 집단구조 분석
전반적인 유전적 다양성 분석에서 보면, 띠구슬다슬기 집단은 3개의 서식지 모두 하나의 집단으로 볼 수 있는데 이는 genotyping 분석 결과에서 동일하게 지지하는 결론을 확인하였다.
(다) 보전 방안 및 유전자 정보 활용
띠구슬다슬기는 한국 고유종으로 국내 중・북부 수계의 일부 상류 지역에서 발견된다. 단양지역의 모식산지는 파괴되어 서식개체를 발견할 수 없고 현재 강원도 영월지역의 동강 또는 서강 유역과 평창지역의 평창강 유역 주변에서 확인이 되는 것으로 알려져 있다. 본 연구에서는 영월 2집단과 정선 집단에서 각 20개체씩의 띠구슬다슬기를 확인하였으며, 집단간 유전다양성 분석을 수행하였다. 그 결과 집단간 분화지수나 근친지수가 양호한 수준으로서 유전적 감소현상이 확인되지 않는다. 영월 주천집단은 영월 북면 집단에 비해 정선 집단과 9이상의 유전적 흐름(Nm) 지수가 계산되었는데, 인접지역이지만 다른 담수생물의 유전적 분화도 지수와 비교했을 때 상대적으로 높은 수치이다. 이는 최근에 두 집단간 유전적 교류 현상이 발생했을 가능성을 시사한다.
8) 애기뿔소똥구리
애기뿔소똥구리는 주로 가축을 방목하는 목초지에 서식하며 전국에 고루 분포한다고 알려져 있지만 1970년대 이후 가축의 사육 환경이 바뀐 이래 급격한 개체군의 감소를 나타냈다. 그러나 최근에는 내륙 국립공원 지역을 중심으로 주로 목장지대에서 개체군이 지속적으로 증가하고 있다고 보고된 바 있다(국립공원관리공단 국립공원연구원 2013). 이에 본 연구진은 향후 애기뿔소똥구리의 관리방안을 위한 기초자료를 마련하고자 애기뿔소똥구리 고유의 유전자 표지 10개(Microsatellite, 초위성체) 및 4,132개(single nucleotide polymorphism, SNP, 단일염기 다형성)를 각각 분석해 국내에서 발생하는 애기뿔소똥구리 집단 간의 유전자 다양성 수준에 대해 비교·분석연구를 수행하였다.
(가) 기존 연구결과
애기뿔소똥구리에 대한 집단유전학적 연구는 mitochondrial DNA (COI, CytB)와 nuclear DNA (ITS2)를 통한 유전적 다양성 연구가 수행된 바 있는데(Kang et al. 2012) 미토콘드리아 유전자의 경우 COI은 5.02% 그리고 CytB는 4.62%로 곤충집단의 일반적인 염기서열 변이율보다 크다고 보고되었으나, 핵 영역의 경우 뚜렷한 구분이 없다고 보고되었다. COI과 CytB를 이용한 계통 및 Network 분석결과 우리나라 애기뿔소똥구리는 크게 두 개의 mitochondrial DNA 그룹이 존재함을 다시 확인하였으며 이들 두 개의 그룹은 지역별 분할은 없는 가운데 조사된 모든 집단에 공존한다고 보고되었다. Kang et al. (2012)의 연구에 더하여 Hwang et al. (2018)은 두 곳의 새로운 지역(굴업도, 제주도 해안동)과 기존 횡성 집단에 개체를 추가하여 총 7개 지역 (제주도 네 곳) 104개체에 대한 COI과 CytB 분석을 수행한 결과 집단과 시료의 확장에도 불구하고 Kang et al. (2012)의 연구결과와 큰 차이 없이 우리나라 애기뿔소똥구리는 크게 두 개의 mitochondrial DNA 그룹이 존재함을 다시 확인한 바 있다. 한편 Kang et al. (2012)의 연구결과 핵 영역 마커로 사용된 ITS2는 집단간 뚜렷한 구분이 없는 결과가 도출된 바 있다.
(나) 애기뿔소똥구리 유전자 다양성 분석
보다 심도 있는 핵 영역 분석을 위하여 2016년 microsatellite DNA 분석에 이어 올해 신규로 분석한 여수 화태도, 서산 및 기존 집단에 추가 개체를 망라하여 총 6개집단(서산은 4개체) 67개체에 대해 분석하였다. 그 결과 모든 집단은 빈도의 차이가 있을 뿐 두 개의 유전그룹이 집단내 공존한다는 면에서 mitochondrial DNA와 유사하다고 할 수 있다. 모든 집단(서산 포함)은 근친교배 지수가 음의 값(FIS = -0.250)이 확인되어 inbreeding의 가능성은 없는 가운데 가장 많은 개체가 포획된 제주도(20개체)와 그 다음 많은 개체를 이용한 횡성(12개체)이 가장 높은 유전자 다양성(HE= within-population gene diversity in the diploid data)을 나타냈다.
당해 연도 신규 분석한 SNP 마커결과 역시 횡성(0.0994)과 제주도(0.098) 집단이 가장 높은 유전자 다양성 수준을 보여 microsatellite DNA 분석결과와 일치하고 있는 실정이다. 이러한 결과는 국내에서 상대적으로 많은 개체의 애기뿔소똥구리가 채집되는 두 지역이 가장 높은 유전자 다양성을 보임으로 집단의 크기와 유전자의 크기가 상관관계가 있어 보인다. 아울러 두 집단에 비해 낮은 유전자 다양성을 나타내는 집단도 제주도와 횡성 집단과 비슷하게 microsatellite DNA의 경우 0.6정도의 다양성을 보이고 SNP의 경우 0.09정도의 다양성을 보임으로 국내 애기뿔소똥구리는 소수집단에서 나타나는 inbreeding, 낮은 유전적 다양성 등의 문제는 없는 것으로 유추된다. 이상의 mitochondrial DNA, microsatellite DNA 및 SNP 마커의 유전자 다양성 수준을 비교한 결과를 정리해보면 국내 애기뿔소똥구리는 작은 집단에서 나타날 수 있는 inbreeding (microsatellite DNA data)과 유전적 동질화(genetic homogeniety)로 인한 문제점은 없는 것으로 유추된다.
(다) 집단의 유전적 구조 분석
각 집단의 유전자 풀 다양성을 분석한 결과, 6개 집단은 각 최대 2개 (microsatellite) 및 4개(SNP)의 유전자 풀이 분포하고 있음을 확인했다. 그 중 제주도와 강원도 횡성 집단은 각 표지에서 상대적으로 많은 최대의 유전자 풀로 구성되어 있음을 나타냈다. 또한, 집단 간 유전적 거리에 따른 유전적 격리를 분석한 결과, 제주도와 강원도 횡성은 유전적으로 가까운 반면, 여수 화태도(초위성체)와 인천 굴업도 및 영광 안마도(단일염기 다형성)집단은 타 집단들과 상대적으로 먼 유전적 관계를 나타냈다. 이들 지역은 육지로부터 다소 격리된 섬 지역으로(굴업도는 인천으로부터 50여 km, 화태도는 여수로 부터 11 km 및 안마도는 육지로 부터 34 km), 지리적 격리를 원인으로 추정하였으나, 육지로부터 가장 멀리 있는 제주도의 경우 모든 분석에서 격리현상은 전혀 보이지 않을 뿐 아니라 본 연구에서 가장 높은 수준의 다양성을 보여 연근해 소형의 섬과 다른 상황이며, 추후 이를 참고하여 보전정책을 수립해야 할 것으로 판단하고 있다.
(라) 보전 방안 및 유전자 정보 활용
이상의 결과를 종합해볼 때 국내 발생하는 애기뿔소똥구리는 전반적으로 높은 유전자 다양성 보유로 인해 유전적 건강도가 양호한 편이며, 국내 애기뿔소똥구리는 유전적으로 작은 집단에서 나타날 수 있는 근친교배나 유전적 동질화로 인한 문제점은 없는 것으로 추정된다. 또한, 제주도와 강원도 횡성 집단의 다양성이 가장 높은 것은 상대적으로 타 집단에 비해 방목지가 많아 두 지역에서 많은 개체의 애기뿔소똥구리가 채집된 것에서 기인된 것으로 집단의 크기와 유전자 다양성의 크기 사이에 상관관계가 있음을 추정할 수 있다. 추가적으로 제주도와 강원도 등 목장 지대 주변에 개체수가 많다는 연구진의 관찰 결과와 내륙 국립공원 지역을 중심으로 개체군이 지속적으로 증가하고 있다는 보고 등과 부합하는 결과로 사료된다고 밝히고 있다. 이에 따라 본 연구결과, 애기뿔소똥구리는 집단유전학적 측면에서 멸종에 이를 정도의 어려움을 겪고 있지는 않은 것으로 유추하며, 이러한 유전분석 결과는 향후 멸종위기 야생생물 지위 평가 또는 보전정책 수립시 평가기준으로 설정할 수 있을 것으로 생각된다.
9) 은줄팔랑나비
은줄팔랑나비는 국내에서 멸종위기종으로 신규지정된 종으로 현재 이들의 서식지가 두 지역만 보고된 상황에서 각 개체군에 대한 유전적 다양성과 구조를 파악하는 것이 향후 종 보존과 함께 관리방안을 위한 기초자료로서 매우 중요하다. 본 연구에서는 그 기반을 마련하기 위해 현재 소수의 지역에서 발생하는 은줄팔랑나비의 유전자 다양성 조사 및 분석을 수행하였다.
(가) 은줄팔랑나비 유전자 다양성 분석
은줄팔랑나비 개체로 부터 NGS분석을 통해 12개의 microsatellite marker 선별하여 국내 발생보고된 2개 집단(강원도 인제군, 경상남도 밀양시)에 분포하고 있는 은줄팔랑나비 유전자 다양성 분석에 이용하였다. 마커별로 분석된 각 마커의 특징을 살펴보면 12개의 마커 중 6개 마커가 Hardy-Weinberg Equilibrium (HWE)을 위배되지 않았다. 또 1개 마커를 제외한 11개 마커가 0.5 이상의 평균 0.7838의 PIC 값을 가지는 것으로 조사되었다. 더 다양한 지역을 포함하여 각 지역별로 충분한 개체수의 유전정보를 수집한다면 마커의 효용성 및 활용도를 좀 더 높일 수 있을 것으로 판단된다.
은줄팔랑나비 지역별 개체군의 유전자 다양성은 전반적으로 밀양이 낮게 관찰되었는데 (HO = 0.746, HE = 0.67,) 음의 FIS (-0.086) 값이 확인됨에 따라 소수집단으로 부터 야기되는 근친교배가 일어나고 있지는 않은 것으로 판단된다. 그러나 현 제한된 개체만이 분석되었으므로 추후 추가 분석이 필요한 실정이다. 한편, 유전자 다양성이 상대적으로 높은 인제에서 양의 FIS 값이 관찰됨에 따라 다른 지역과의 교류가 적거나 없는 가운데 근친교배가 발생하고 있을 가능성이 높다고 사료된다.
(나) 집단구조 분석
은줄팔랑나비의 유전자형(Genotype)으로 집단구조 분석을 수행한 결과, 은줄팔랑나비 개체군들은 크게 3개의 유전적 구조를 형성하는데 인제와 밀양이 각각 다른 유전자 구조를 형성하고 있으며, 인제는 집단 내 두 개의 유전자 구조가 혼재하고 있었다. FST, RST 및 개체별 PCoA 분석결과 역시 인제와 밀양이 격리되는 양상을 보이며 PCoA 분석결과에서 인제는 집단 내 매우 넓은 분포를 보여 집단구조 분석결과에서 보인 두 유전적 구조와 일치하는 결과이다. 두 지역 간 지리적으로 격리됨에 따라 유전적으로도 격리현상을 겪고 있는 것으로 보여 지며, 특히 인제의 경우 집단 내 근친교배가 발생할 가능성이 높게 제시되는 가운데 유전적 구조 또한 두 그룹으로 나뉘는 결과를 보이며 차후 유전적 다양성 또한 감소되는 것이 아닌가 추론된다.
(다) 보전 방안 및 유전자 정보 활용
팔랑나비과의 돈무늬팔랑나비아과는 국내에 3속 6종이 보고되어있으며, 그 중 은줄팔랑나비가 속한 Leptalina 속은 전 세계적으로 은줄팔랑나비 1종만이 보고되어 해당 속의 유일한 종으로 유전자원으로서 높은 가치를 가지고 있음에도 불구하고 한국을 포함한 일본, 러시아 등 대부분의 은줄팔랑나비 발생지에서 개체수가 급감하며 멸종위기에 처한 상황이다. 은줄팔랑나비는 하천과 습지 주변의 초지에 주로 서식하는데, 국내에서는 하천 정비 등으로 인한 서식지 파괴로 개체수가 급감하였고, 현재는 습지보호지역 주변의 초지에서 주로 발생하고 있었다. 본 과제의 시료확보를 위한 채집결과, 당해 연도에 포획 및 신고한 2개체는 밀양시 단장면에 위치한 습지보호지역 주변의 초지에서 채집되었으며, 2016년 및 2017년에 채집되어 보관 신고한 개체들도 대부분이 습지 주변의 초지에서 발견 및 포획되었다. 또한 은줄팔랑나비는 북방계의 나비이며 타 북방계 나비의 분포변화와 유사하게 지구온난화에 따라 점차 높은 고도로 올라가며 서식지의 면적이 줄어드는 양상이 나타날 것이기 때문에 해당 종의 보전과 서식처 복원 등을 위한 집단의 유전적 다양성 조사 등의 과학적인 연구가 시급한 상황이다. 본 연구결과에서, 은줄팔랑나비 집단별 유전적 다양성 지수와 유전적 거리관련 분석결과(FST vs RST, PCoA)를 보면 현재의 유전자, 개체수 혹은 정보량 등의 부족으로 제한된 결과만이 제시됨에도 불구하고 모든 분석결과를 종합하였을 때 인제와 밀양은 물리적인 격리를 반영하는 유전적 격리가 존재하며 특히 인제의 경우 지속된 지리적 격리로 인한 근친교배 현상을 확인하였다. 아마 인제집단이 수적으로 많은 은줄팔랑나비가 발생함에도 양의 FIS값이 나온 것은 주변지역에 다른 개체군이 없어 인제집단만이 오랜기간 근친교배한 결과가 아닌가 생각된다. 그러므로 지속적인 근친교배를 방지하기 위해 유전적 격리를 보이는 밀양집단과 이식을 통한 유전적 다양성 증가 방안이 고려되어야 할 것으로 여겨진다. 그러나 보다 정확한 결과를 도출하기 위해 서식지의 환경과 더불어 심도있는 연구가 필요할 것으로 사료된다. 향후 밀양집단을 포함한 더 다양한 지역으로부터 더 많은 시료를 확보하여 각 지역별로 충분한 개체수의 유전정보 수집 등의 추가적인 조사가 수행된다면 각 집단에 대한 분명한 유전적 다양성 평가를 확인할 수 있을 것이며 이에 따라 다양성이 감소하고 있는 집단에 대한 보다 구체적인 보존 및 복원을 위한 관리방안을 제시할 수 있을 것으로 판단된다.
10) 좀뒤영벌
참호박뒤영벌은 국내 뒤영벌류 중 고유종으로 유전자원 연구를 위한 유전적 다양성 평가 등이 필요한 실정이나, 국내에서 소수 개체변이 발생하며 그 서식지 또한 확인이 용이하지 않아 실험 및 분석을 위한 충분한 개체 확보가 불가능한 상황이다. 이에 본 연구의 대상종인 참호박뒤영벌을 대신하여 근연종을 선정하고 이를 통해 참호박뒤영벌을 포함한 뒤영벌류의 다양성 분석과 보존방안을 유추하고자 하였다.
뒤영벌류 중 좀뒤영벌은 국내에 분포하는 대표적인 토종뒤영벌 중 하나로 전국적으로 분포하고, 방화식물의 범위도 가장 넓으며, 유전적 분석을 위한 충분한 개체 확보가 가능함에도 불구하고 호박벌, 삽포로뒤영벌 등 타 종보다 제한적으로 연구된 상황이며, microsatellite 개발 및 분석도 수행된 바 없다. 따라서 본 연구에서 토종뒤영벌로 연구가치가 충분한 좀뒤영벌을 근연종으로 선정하여 국내 전국에서 발생하는 좀뒤영벌 집단의 유전자 다양성 조사 및 분석을 수행하였다
(가) 좀뒤영벌 유전자 다양성 분석
좀뒤영벌 개체로 부터 NGS분석을 통해 10개의 microsatellite marker를 선별하여 국내 10개 집단(춘천, 영흥도, 정선, 울릉도, 공주, 상주, 군산, 화순, 창원, 제주도)에 분포하는 좀뒤영벌 유전자 다양성 분석에 이용하였다. 마커별로 분석된 각 마커의 특징을 살펴보면 10개의 마커 모두가 Hardy-Weinberg Equilibrium (HWE)을 위배되지 않으며, 모든 마커가 0.7 이상의 평균 0.8265의 PIC 값을 가지는 것으로 조사되어 대부분의 마커가 안정적으로 사용될 수 있음을 보여주었다. 더 다양한 지역으로부터 더 많은 시료를 확보하여 각 지역별로 유전정보가 수집된다면 마커의 효용성 및 활용도를 좀 더 높일 수 있을 것으로 판단된다.
좀뒤영벌 지역별 개체군은 대부분 이형접합자 관측치(HO)에서 더 높은 수준을 보였으나, 정선만이 관측치가 더 낮아 반대되는 양상을 보였다(HE = 0.722, HO = 0.699). 또한 FIS 값도 정선 집단을 제외한 나머지 지역은 모두 음의 FIS 값이 관찰됨에 따라 정선 집단은 근친교배가 일어나고 있을 가능성이 높으며, FST, RST, PCoA 및 집단구조분석 등 모든 분석결과 다소 이질적으로 격리된 결과를 나타내므로 다른 지역과의 교류가 적거나 없는 가운데 근친교배가 발생하고 있을 가능성이 높아 보인다. 좀뒤영벌의 COI 분석결과(Kim et al. 2009) 울릉도의 유전적 다양성이 낮게 분석된 것과 본 연구결과에서 울릉도의 다양성 및 대립인자 풍부도가 낮게 관찰되는 것은 울릉도는 섬으로 격리된 가운데 상대적으로 작은 개체군을 형성하고 있는 것으로 추론된다.
(나) 집단구조 분석
집단구조 분석 결과, 좀뒤영벌 개체군들은 크게 3개의 유전적 구조를 형성하고 있는 것으로 나타났으며 정선과 울릉도가 각각 나머지 지역과 격리되고, 남은 8개 지역은 매우 비슷한 패턴을 보이나 화순만 다소 다른 구조임을 확인하였다. FST, RST, 집단별 PCoA 및 개체별 PCoA 분석결과, 정선과 울릉도는 타 지역으로부터 격리되어 있음을 알 수 있어 유전적 구조분석 결과와 일치하였다. 이상의 결과는 울릉도의 경우 “Oceanic island”에 위치하는 지리적 특성이 반영된 결과로 여겨지며 정선의 경우 백두대간의 동쪽에 위치하는 정선의 지리적 위치가 이러한 격리현상을 유발한 것으로 여겨진다. 본 연구결과와 유사하게 호박벌(B. ignitus )에 대한 microsatellite 분석 결과, 태백으로부터 서북쪽에 위치한 사북은 mutation-drift equilibrium과 대립유전자 빈도 분포에서 타 집단과 유의하게 변형되었고 동시에 낮은 대립인자 풍부도를 보여주어 사북집단은 최근 병목현상을 경험하였다고 보고하였다. 즉 이는 강원도의 집단은 유전적 격리, 병목현상 등 각 집단마다 여러 가지 형태의 “진화”가 일어났을 것으로 추론된다. 이러한 추론은 정선집단에도 적용되어 현재와 같은 유전적 격리 및 근친교배가 발생되어왔을 것으로 추론되다. 또한 FST 및 집단구조 분석에서 화순이 정선과 울릉도 외에도 일부 지역(공주, 군산)과 유전적 격리를 보인 것은 기 보고된 COI 연구결과와 일치하나, 그 이유는 추가적인 연구가 필요한 것으로 여겨진다.
본 연구결과에서 처음으로 확인된 영흥도와 일부지역(공주, 군산, 창원)과 유전적 거리는 영흥도의 섬 지리적 특성이라고 추론된다. 그러나 제주도의 경우, 대립인자 수, 대립인자 풍부도, FST, RST, 집단구조 분석, PCoA 결과 내륙 지방과 큰 차이를 보이지 않았는데, 이는 과거 내륙과 지형적 격리가 일어날 때 충분한 유전적 다양성이 있는 개체가 남았으며, 다양한 집단을 수용할 수 있는 크기로 지리적인 격리현상에 따른 유전적 격리가 반영되지 않은 것으로 추론된다.
(다) 보전 방안 및 유전자 정보 활용
현 우리나라에서 전국적 분포를 보이는 뒤영벌류(Bombus )는 좀뒤영벌, 호박벌 정도이며 우수리뒤영벌이 경기도와 전라북도에 발생하는 정도이며 참호박뒤영벌, 황토색뒤영벌, 삽포로뒤영벌 등 대부분이 강원도 지역을 중심으로 발생하고 있는 실정이다. 분류학적으로 하나의 속에 속하는 그룹은 형태적 유사성과 함께 비슷한 습성이 있으며 실지 국내 발생 Bombus는 종간 유전적 분화가 크지 않은 점에 근거하여 그 기원이 최근 일 것으로 유추되고 있으며 일부 종은 실험실내 이종간 교배가 가능하다고 보고된 바 있다. 또 좀뒤영벌과 참호박뒤영벌처럼 일부 분포지역이 중복되는 종(예, 강원도)의 경우 한 종의 연구결과는 다른 종의 상황을 예측하는 참고자료로 활용 가능할 것이다. 이러한 상황 하에서 현 전국적 분포를 보이는 좀뒤영벌에 대한 집단 유전학적 연구는 매우 제한적 분포를 보이는 참호박뒤영벌은 물론 국내 발생 뒤영벌류의 종내 유전적 변이 및 구조 등에 대한 시사점을 제공할 것으로 예측된다. 즉, 집단유전학적 연구를 위한 개체 확보가 어려운 참호박뒤영벌을 대신하여 근연종인 좀뒤 영벌에 대한 분석 결과는 참호박뒤영벌 연구시 현 연구에서 개발된 마커를 동일 속의 종에 쉽게 적용할 수 있으므로 향후 충분한 개체가 확보되었을 경우 신속한 집단유전학적 연구에 활용될 수 있을 것이다. 또한 본 연구결과 및 기존 호박벌 연구결과, 강원도지역(정선)의 유전적 격리, 근친교배 결과는 참호박뒤영별에도 확인될 가능성이 높아 보이므로 향후 보전 정책의 수립 및 복원시 이들 지역에 대한 면밀한 분석을 통해 격리된 집단의 유전적 다양성 복원노력이 필요해 보일 것으로 보인다. 아울러 울릉도, 영흥도 등 섬 지역의 유전적 격리 현상은 좀뒤영벌은 물론 참호박뒤영벌에도 발생할 가능성이 높아 보이므로 물리적으로 격리된 집단의 복원시 유전적 격리의 극복방안에 대한 노력이 필요해 보인다. 지리적으로 가장 거리가 먼 제주도가 전혀 유전적 격리 현상을 보이지 않는 것은 우리나라에서 가장 큰 섬인 제주도의 풍부한 식생과 규모가 이러한 격리를 제한한 것으로 비록 참호박뒤영벌은 북방 분포를 보이는 종이긴 하나 뒤영벌류에 포함되는 유사종에 대한 참고사항으로 활용될 수 있을 것으로 판단된다.
2. 미토콘드리아 유전체 분석 결과
총 6종의 멸종위기 무척추동물을 대상으로(무척추동물 4종, 곤충 2종) 전체 미토콘드리아 유전체 염기서열을 결정하고, 대상종별로 근연 분류군의 미토콘드리아 유전정보를 이용하여 비교 분석하였다. 염주알다슬기와 거제외줄달팽이의 경우 비암호화 영역(noncoding) 내에 포함되는 repeat 시퀀스의 특이성으로 인해 sequencing 해독이 불가하여 nearly complete mtgenome 형태로 분석을 수행하였다. 염주알다슬기과 거제외줄달팽이의 repeat 서열은 3kb 이상일 것으로 예상되며, 짧은 repeat unit이 반복되는 양상으로 인해 sequence assembly에 어려움이 있었다.
3종의 절지동물(물거미, 은줄팔랑나비, 여름어리표범나비)는 평균 15,681bp의 전체 미토콘드리아 유전체 염기서열을 가지며, 물거미의 미토콘드리아 유전체 염기서열이 가장 길다(15,872bp). 이는 물거미 미토콘드리아 유전체 내에 2타입의 긴 repeat 서열에 의한 것으로 생각된다. Nearly complete mtgenome은 2종의 육산 패류(염주알다슬기, 거제외줄달팽이)가 해당되며, 특이하게도 기 보고된 염주알다슬기 mtgenome에서도 동일한 부위의 염기서열이 확보되지 않아 partial genome 상태로 보고되었다. 당해연도 미토콘드리아 유전체 분석에 이용된 연구대상종 중에서 가장 긴 염기서열을 확보한 종은 착생깃산호이다. 착생깃산호는 자포동물에 속하는 산호류로서 19,036bp의 염기서열이 분석되었다. 일반적으로 중생동물(Metazoa)의 미토콘드리아 유전체는 intron이 없는 컴팩트한 사이즈를 가지는 것이 특징이나, 자포동물의 경우 모든 유전자 사이에 intergenic region이 존재하고 MutS , msh1 과 같이 원핵 생물에서 확인되는 일부 유전자가 포함되어 있어서 상대적으로 긴 염기서열이 확인된다. 분석에 이용된 연구대상종의 미토콘드리아 유전자 정보는 모두 확인하였으며, 단백질암호화 유전자(PCGs)를 대상으로 각 대상 분류군의 근연그룹과 계통분석을 수행, 계통학적 위치를 확인하였다.
(출처 : 요약문 5p)
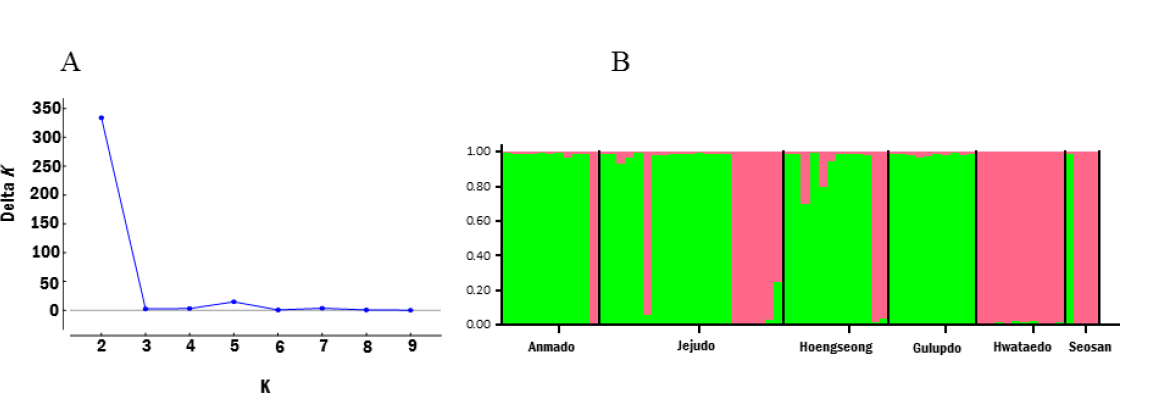 표
애기뿔소똥구리 6개 집단에 대한 유전적 집단구조(K =2) A, Plot of Delta K calculated with the formula Delta K = mean (|L"(K)|)/sd(L(K)), n = 68; B, Bar plot of estimated membership of each individual in K = 2 clusters. Black bars separate the ten population sample groups. Different colors represent different gene pools
표
애기뿔소똥구리 6개 집단에 대한 유전적 집단구조(K =2) A, Plot of Delta K calculated with the formula Delta K = mean (|L"(K)|)/sd(L(K)), n = 68; B, Bar plot of estimated membership of each individual in K = 2 clusters. Black bars separate the ten population sample groups. Different colors represent different gene pools
 표
애기뿔소똥구리 6개 집단에 대한 유전적 집단구조(K =2) A, Plot of Delta K calculated with the formula Delta K = mean (|L"(K)|)/sd(L(K)), n = 68; B, Bar plot of estimated membership of each individual in K = 2 clusters. Black bars separate the ten population sample groups. Different colors represent different gene pools
표
애기뿔소똥구리 6개 집단에 대한 유전적 집단구조(K =2) A, Plot of Delta K calculated with the formula Delta K = mean (|L"(K)|)/sd(L(K)), n = 68; B, Bar plot of estimated membership of each individual in K = 2 clusters. Black bars separate the ten population sample groups. Different colors represent different gene pools
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.