최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 국립농업과학원 National Institute of Agricultural Sciences |
|---|---|
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2015-02 |
| 과제시작연도 | 2014 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO201500010177 |
| 과제고유번호 | 1395035261 |
| 사업명 | 차세대바이오그린21 |
| DB 구축일자 | 2015-07-11 |
| DOI | https://doi.org/10.23000/TRKO201500010177 |
Ⅳ. 연구개발결과
1) 제1세부 : GM 작물의 안전성 평가 신기술 적용 연구
○ 형질전환체 위해요소 발굴 및 벼, 콩 근권 토양 지표미생물 동정
Bt 벼와 비타민E 강화 형질전환 콩 근권 토양 미생물을 대상으로 시기별 미생물 군집밀도와 미생물상 구조를 조사하였고 벼 및 콩 근권 토양 우점세균을 동정하였다.
○ 분자생물학적 방법에 의한 벼 및 콩 근권 토양 미생물 비교분석
Bt 벼와 비타민E 강화 형질전환 콩 근권 토양 미생물의 DGGE 및 pyrosequencing 등의 분자생물학적 방법을 통해 GM 과
Ⅳ. 연구개발결과
1) 제1세부 : GM 작물의 안전성 평가 신기술 적용 연구
○ 형질전환체 위해요소 발굴 및 벼, 콩 근권 토양 지표미생물 동정
Bt 벼와 비타민E 강화 형질전환 콩 근권 토양 미생물을 대상으로 시기별 미생물 군집밀도와 미생물상 구조를 조사하였고 벼 및 콩 근권 토양 우점세균을 동정하였다.
○ 분자생물학적 방법에 의한 벼 및 콩 근권 토양 미생물 비교분석
Bt 벼와 비타민E 강화 형질전환 콩 근권 토양 미생물의 DGGE 및 pyrosequencing 등의 분자생물학적 방법을 통해 GM 과 non-GM 토양의 미새물상 변화를 시기별로 조사한 결과 이들 간 유의성 있는 차이는 없는 것으로 분석됨.
○ Real-time PCR을 이용한 형질전환 벼 및 콩 유래 유전자의 토양지속성 분석
GM 작물 재배후 잔존물의 지속성에 대해서는 real-time PCR을 통해 분석한 결과수확 후에는 이들 유전자들이 토양내에 잔존하는 것으로 분석되었음.
○ 형질전환 벼 및 콩으로부터 토양미생물로의 수평이동성 여부 분석
Bt 벼와 비타민E 강화 형질전환 콩 근권 토양의 배양 가능한 미생물을 대상으로 형질전환체 유래 유전자의 수평이동성을 분석한 결과 형질전환 유전자는 검출되지 않았음
2) 제1협동 : GM 작물의 미생물상 분석 신기술 개발
○ 화본과 작물의 주요 내생세균(Paenibacillus polymyxa) 분자 마커 개발
벼 내생세균의 분자마커를 개발하여 GM 벼와 non-GM벼의 내생세균 변이 분석 결과 월동 전과 월동 후, 그리고 벼 생육기 동안 두 토양에서 P. polymyxa가 모두 검출되어 개체간의 큰 차이점을 보이지 않았음.
○ GM 작물 환경방출 안전성 확인
GMO 안전성 포장 내에 재배되고 있는 GM작물의 삽입유전자가 주변 환경으로 이동되는지 안전성 확인을 위해 다중 검출 마커 (18s rDNA, Zm-ubiquitin promoter, P35S, TpinII, Tnos, T35S, bar, hptII, nptII)를 이용하여 토양과 물 및 벼, 식물체 등에서 PCR 방법으로 확인한 결과, 2012년, 2013년, 2014년 세 지역 non-GM벼, 식물체, GM물, non-GM물에서는 GM작물의 삽입유전자가 발견되지 않았음. 토양에서는 터미널 (pinII, nos)이나 선택마커 (hptII, nptII)등은 미생물에서 분리된 유전자이므로 토양 분석을 통하여 PCR 산물이 나온 것으로 사료됨.
○ GM작물 재조합 운반체 DNA 염기서열 완결성 검증
GM작물실용화사업단과 중요 순위를 결정한 후, plasmid DNA 염기서열 분석을 수행결과, 2012년에는 pCAMBIA3301-GluCpro-gateway 외 22종 완료, 2013년-2014년에는 pPZP-GUBQ1-35sBar 외 32종 중 24종 완료 (9종 분석 불가). DNA 염기서열 분석이 완료된 재조합 운반체는 DNASTAR LaserGene 11 염기서열 분석 프로그램을 이용하여 기존의 DNA 염기서열 데이터와 상동성 분석을 수행. 유전자재조합운반체 중 68개의 삽입유전자의 단백질 알레르기성 검색 결과, 새로 발현된 단백질의 8개 아미노산 잔기와 이미 알러젠으로 알려져 있는 단백질 중 일치하는 아미노산 서열은 NAS2가 1개 존재하고, 새로 발현된 단백질의 80개 이상의 아미노산으로 이루어진 절편이 이미 알러젠으로 알려져 있는 단백질의3) 제2협동 : GM 작물의 영양성분 분석 신기술 개발
○ 단백질 분자구조 분석을 위한 분광 파장분석
bar gene이 삽입된 GM 작물로부터 PAT 단백질의 발현 여부를 확인하기 위해 GM 벼와 Non-GM 벼의 잎을 파괴하지 않고 그대로 FT-IR, FT-NIR, Raman spectroscopy를 이용하여 측정하고, PAT 단백질의 분광특성과 비교분석하였음
○ 분자구조 분석을 위한 복합분광 정성분석 모델개발
복합분광을 이용한 주요 영양성분 정량 예측 최적 모델 개발함
○ 분자구조 분석에 의한 동등성 평가 측정법 제시
콩의 경우에는 수분(4.7%), 회분(3.79%), 조지방(5.34%), 조단백질(3.04%), 탄수화물 (3.99%)의 예측 오차를 나타내어, 모든 영양성분을 예측함에 있어 5%이내의 오차를 나타내어 측정허용오차(5%)와 동등한 결과를 나타냄을 확인할 수 있었음. 아미노산과 35% 이상 상동성을 가지는 것은, OsGSBP 2개, Trsm 3개, AtABF3 9개, AvMaSp 13개, AP26 2개로 확인.
Cultivation of genetically modified (GM) crops has rapidly increased in the global agricultural area. However, cultivation of GM crops in the field evoked the concern of the possibility of unintentional consequences from transgenic plant into environment. In our present study, we have assessed the e
Cultivation of genetically modified (GM) crops has rapidly increased in the global agricultural area. However, cultivation of GM crops in the field evoked the concern of the possibility of unintentional consequences from transgenic plant into environment. In our present study, we have assessed the effects of GM rice and GM soybean on the surrounding soil microbial community. The effects of GM crops on the soil microbial community in its field of growth were assessed using a conventional culture technique and culture-independent molecular methods. Three replicate field plots were planted with a single GM and a non-GM counterpart. The soil microbial communities around these plants were compared using colony counting, denaturing gradient gel electrophoresis (DGGE), pyrosequencing and community level physiological profiling (CLPP) during the growing periods. The bacterial, fungal and actinomycetes population densities of the GM soils were found to be within the range of those of the non-GM cultivar. The DGGE banding patterns of the GM and non-GM soils were also similar, suggesting that the bacterial community structures were stable within a given month and were unaffected by the presence of a GM plant. Pyrosequencing data showed that the similarities of the bacterial community distribution at the phylum level were consistent with DGGE patterns. The substrate utilization pattern of GM and non-GM soil were quite similar for each time periods. These results indicate that soil microbial communities are unaffected by the cultivation of GM crops within the experimental time frame.
Genetically modified organisms (GMOs) can be defined as organisms in which the genetic material (DNA) has been altered in a way that does not occur naturally. The technology is often called "modern biotechnology" or "gene technology", sometimes also "recombinant DNA technology" or "genetic engineering". It allows selected individual genes to be transferred from one organism into another, also between non-related species [1]. Recently, the use of GM crops has stimulated worldwide debate about biosafety assessments, intellectual property, international trade, and ethical issues [2]. "Biosafety" term means the effects of GM crops and their products on human health and the environment. Paenibacillus polymyxa is known to be a plant-growth-promoting rhizobacterium [3]. The present study described a quantitative polymerase chain reaction (PCR) assay for the specific detection and quantitation of P. polymyxa using a primer pair based on the sequence of a membrance-fusion protein for the amplification of a 268 bp DNA fragment. This study reported that the qPCR-based method was applicable for the rapid and sensitive detection of P. polymyxa and can be used as an alternative method for agricultural soil monitoring. This study, to observe the possible differences between genetically modified (GM) and non-GM rice was carried out for biosafety assessment with P. polymyxa. Also, here we researched possible environmental risks that were related to gene flow from GM rice to agroecosystem using GMO detection primer sets containing promoters, terminators, and selection markers. Genetically modified (GM) rice lines have been cultivated in three GM-crop testing fields. As a step towards the development of reliable PCR methods for detecting GM-crops and the gene flow, we reported here the validation of GMO specific markers and marker for P. polymyxa specific membrane-fusion protein gene, using conventional PCR methods. No amplicons were observed when DNA samples from non-GM soils, waters and plants were used as amplified templates with GMO specific markers. These results indicate that the GMO specific markers can be used as PCR detection of GM crops and the gene flow.
While conventional chemical analysis methods for main nutrients such as moisture, crude protein, crude fat, ash, and carbohydrate content of grains require time-consuming, labor-intensive, and invasive pretreatment procedures, spectroscopic techniques can be used to measure a variety of nutrient components rapidly and non-destructively without supervision from experts once the instrument has been calibrated. The purpose of this study was to develop an optimal prediction model for determining moisture, crude protein, crude fat, ash, and carbohydrate content of genetically modified(GM) rice and soybeans using a spectroscopic techniques such as near infrared, Raman, and infrared spectroscopy method. Partial least square regression methods(PLSR) was the main algorithm used to obtain the prediction models for the nutrient components of rice and soybeans. In the case of soybeans, measurement errors for the moisture (4.7%), ash (3.79%), crude fat (5.34%), crude protein (3.04%) and carbohydrate (3.99%) were within 5% tolerance. This result showed an equivalent result as compared with the conventional method. In addition, the moisture (4.4%), crude protein (3.91%), carbohydrate (0.83%) of nutritional components for rice also indicated within 5% error, respectively. The result suggests that the spectroscopic techniques investigated in this study can be applied to the prediction of main nutrient components for rice and soybean.
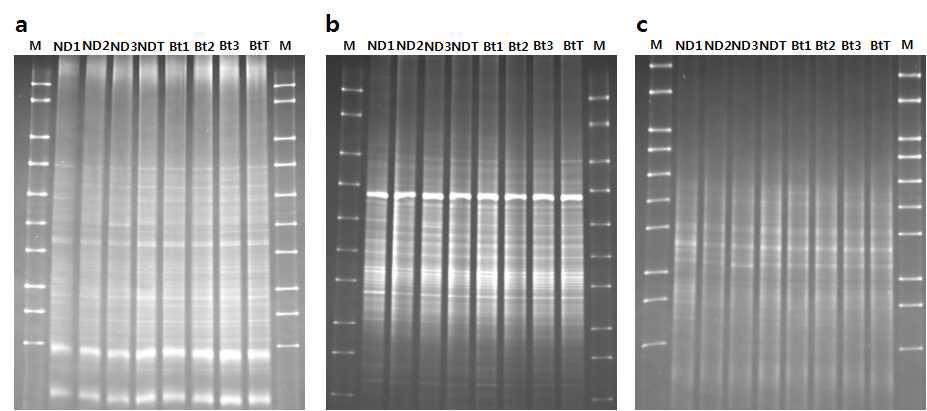 표
DGGE analysis of 16S rRNA V3(a), V4(b) and V6(c) region obtained after PCR amplification. DGGE profile for August (2012) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
표
DGGE analysis of 16S rRNA V3(a), V4(b) and V6(c) region obtained after PCR amplification. DGGE profile for August (2012) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
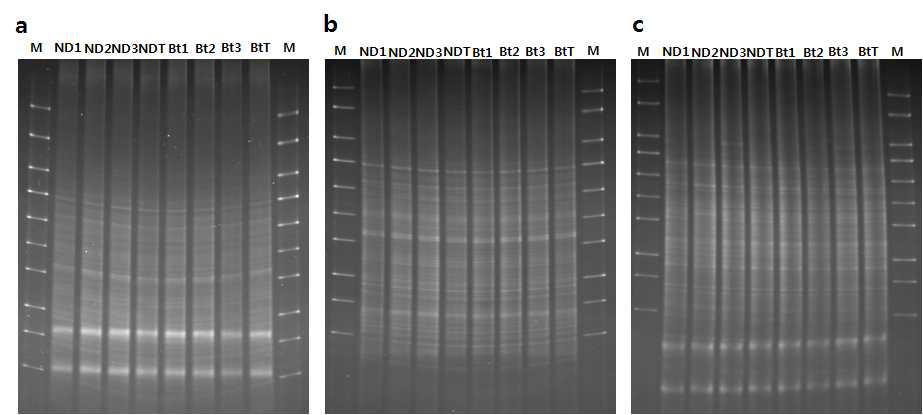 표
DGGE analysis of 16S rRNA V3 region obtained after PCR amplification with F352T and 519r primers. DGGE profile for June(a), August(b) and October(c) (2013) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
표
DGGE analysis of 16S rRNA V3 region obtained after PCR amplification with F352T and 519r primers. DGGE profile for June(a), August(b) and October(c) (2013) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
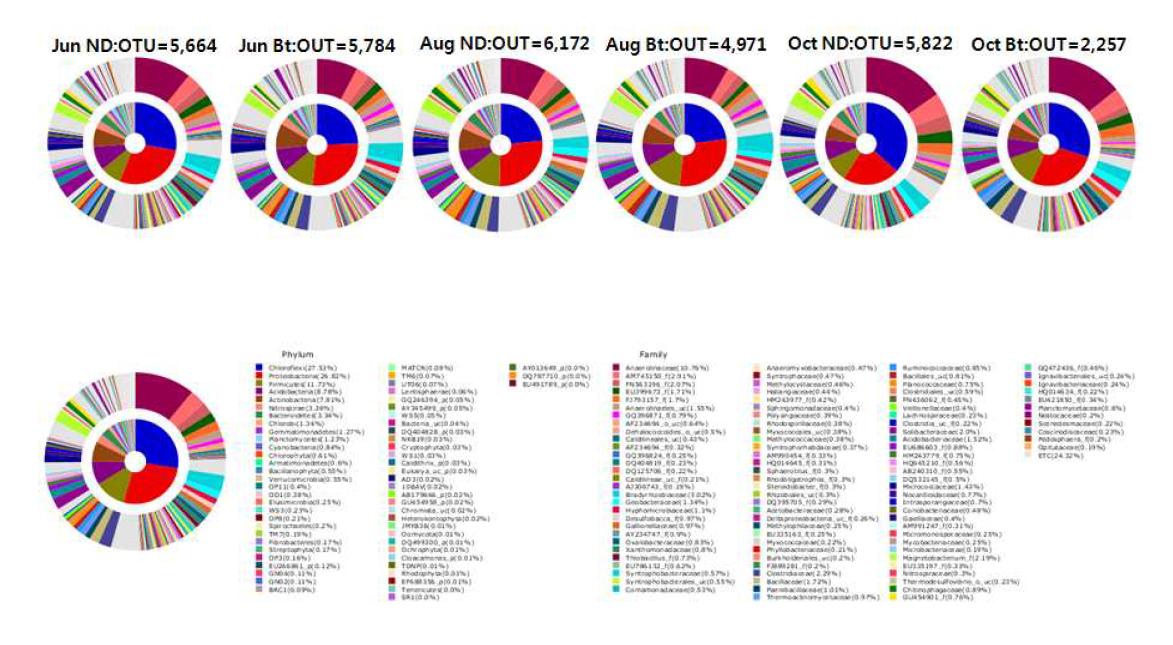 표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared(2012). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared(2012). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
 표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
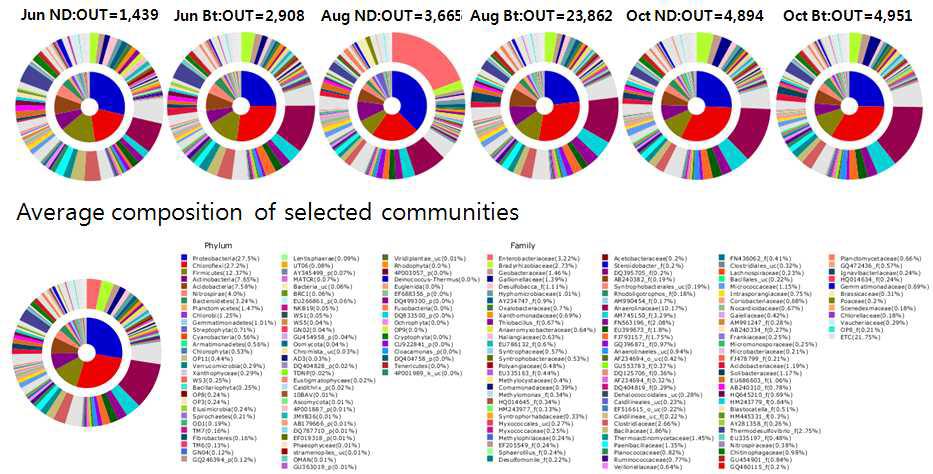 표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared (2013). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared (2013). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
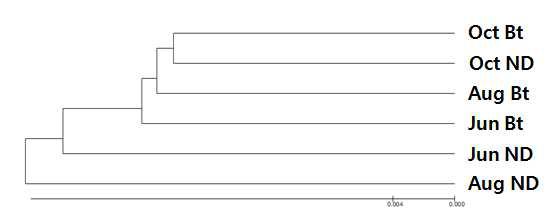 표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
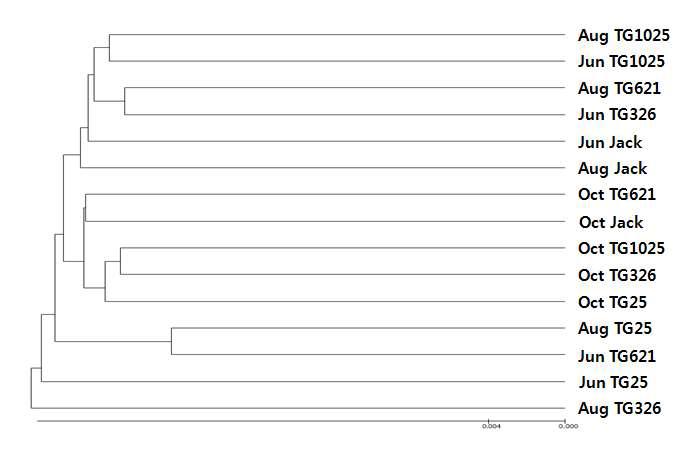 표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
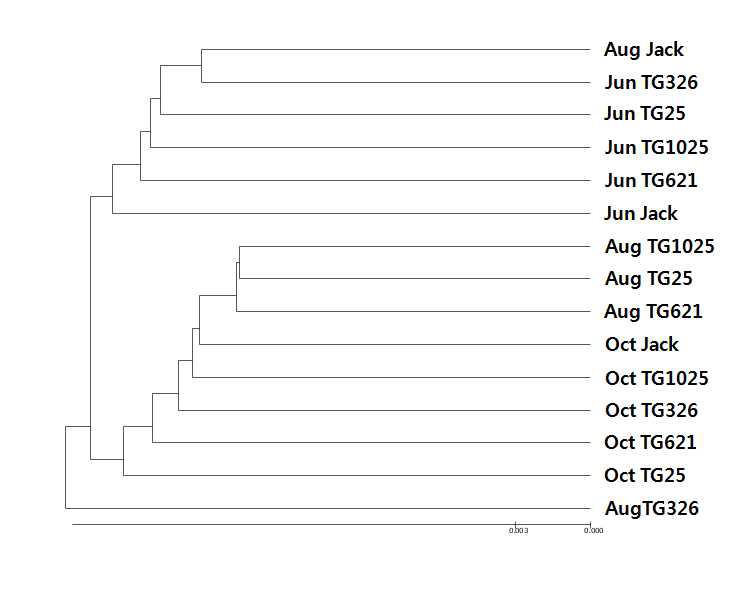 표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
 표
DGGE analysis of 16S rRNA V3(a), V4(b) and V6(c) region obtained after PCR amplification. DGGE profile for August (2012) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
표
DGGE analysis of 16S rRNA V3(a), V4(b) and V6(c) region obtained after PCR amplification. DGGE profile for August (2012) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
 표
DGGE analysis of 16S rRNA V3 region obtained after PCR amplification with F352T and 519r primers. DGGE profile for June(a), August(b) and October(c) (2013) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
표
DGGE analysis of 16S rRNA V3 region obtained after PCR amplification with F352T and 519r primers. DGGE profile for June(a), August(b) and October(c) (2013) in Nakdong and Bt rice. ND, Nakdong; Bt, Insect-resistant GM rice ; M, DGGE molecular weight marker; ND1, 2 Bt1, 2 &3 indicate independent Bt soil sample and BtT inducates mixed soil of Bt1, 2 & 3.
 표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared(2012). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared(2012). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
 표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
 표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared (2013). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
표
Double Pie charts of bacterial communities in Nakdong and Bt soil samples from each month were compared (2013). The inner pie indicates the phylum composition and the outer pie indicates the family composition of the bacterial communities. The names for each color appear below the figure. The nomenclature for each phylotype is based on the EzTaxon-e database
 표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Nakdong(ND) and Bt soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). JunND, Rhizosphere soil of Nakdong collected at June; JunBt, Rhizosphere soil of Bt collected at June, AugND, Rhizosphere soil of Nakdong collected at August AugBt, Rhizosphere soil of Bt collected at August; OctND, Rhizosphere soil of Nakdong collected at August; OctBt, Rhizosphere soil of Bt collected at October.
 표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2012). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
 표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
표
UPGMA dendrogram of 16S rRNA genes in the Jack and vitamin E ortified soybean soil based on OTUs sharing 97% similarity (Bray-Curtis distance) (2013). Ju nJack, Jun TG25, Jun TG326, Jun TG621 Aug Jack, Aug TG25, Aug TG326, Aug TG621 Oct Jack, Oct TG25, Oct TG326, Oct TG621 & Oct TG1025, Rhizosphere soil of Jack, TG25, TG326, TG621 and TG 1025 collected at October.
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.