최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 서울대학교 Seoul National University |
|---|---|
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2015-02 |
| 과제시작연도 | 2014 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO201500010205 |
| 과제고유번호 | 1395035373 |
| 사업명 | 차세대바이오그린21 |
| DB 구축일자 | 2015-07-11 |
| DOI | https://doi.org/10.23000/TRKO201500010205 |
Ⅳ. 연구개발결과
1. 유용유전자의 발굴 및 분리
○ 다수성 관여 유전자 발굴 동정: 우리나라의 녹색혁명을 이끈 통일벼의 유전체는 91.8%의 indica genome과 7.9%의 japonica genome, 0.3% unknown genome으로 구성되어 있고, SSR(simple sequence repeat), ORFs, GO(gene ontology) 등의 유전체를 구성하는 요소들도 indica-japonica 유전체의 구성비율과 유사한 비율로 통일벼를 구성하고 있었다. 벼의 수량에 영향을 미치는 것으로 알려진 s
Ⅳ. 연구개발결과
1. 유용유전자의 발굴 및 분리
○ 다수성 관여 유전자 발굴 동정: 우리나라의 녹색혁명을 이끈 통일벼의 유전체는 91.8%의 indica genome과 7.9%의 japonica genome, 0.3% unknown genome으로 구성되어 있고, SSR(simple sequence repeat), ORFs, GO(gene ontology) 등의 유전체를 구성하는 요소들도 indica-japonica 유전체의 구성비율과 유사한 비율로 통일벼를 구성하고 있었다. 벼의 수량에 영향을 미치는 것으로 알려진 sd1, qSW5, GHD7, GS3, Gn1a 등의 유전자들은 모두 indica 모 본에서 유래한 것으로 나타났다.
○ 인디카 유사 돌연변이체 (Indica-like mutant)의 특성 확인과 양적형질유전자좌(QTL) 분석: Indica-like mutnat는 간장이 길고, 가늘고 긴 종자형태를 가지며, 페놀반응과 염소산칼륨 저항성 시험에서 indica형 결과를 보였다. 8개의 농업형질을 조절하는 QTL을 확인하기 위해 두 F2 집단의 분자연관지도를 작성하였다. 21개의 M-QTL과 3개의 E-QTL이 Indica-like mutant/다산 집단에서 탐색되었다. Indica-like mutant/화청 집단에서는 17개의 M-QTL이 확인되었다. 그 중에서 6개의 M-QTL은 본 연구에서 새롭게 확인된 QTL이다. 두 집단에서 탐색된 총 34개의 QTL 중에서 6개는 본 연구에서 새롭게 확인한 QTL이다.
○ 감수분열 재조환 관련 유전자 및 교배조합에 따른 재조환율 변이 분석: 10개 벼 품종의 resequencing data에서 아종특이적 변이를 보이는 감수분열 재조환 관련 유전자 13개를 확인 하였다. 감수분열 재조환율 변이를 탐색하고, 재조환이 증가하는 계통을 육성하기 위해 indica, temperate japonica, 범친화성 품종들을 상호 교배하여 F1 30조합과 F2 집단 8개, 4개의 BC1F1 집단을 육성하였다. 감수분열 재조환 관련 유전자 8개의 과발현 형질전환이 japonica 벼에서 진행 중이다.
○ 종자 크기 조절 유전자에 대한 연구: 25개국에 고루 분포하는 218개 벼 품종을 대상으로 종자 크기 관련 유전자들의 haploype 조합의 분포와 종자 크기에 관여하는 7개 유전자 간의 관계에 대해 조사한 결과, qSW5 유전자가 종자 길이, 넓이, 길이대 넓이 비율에, GS6 유전자는 넓이와 길이대 넓이 비율에, GW8 유전자와 GS3 유전자는 천립중에 각각 통계적으로 유의하였다. 또한, 각 유전자의 haplotype 분포를 분석한 결과 japonica에서는 haplotype C가, indica에서는 haplotype U가 대다수인 경향을 보였으며, 이러한 분석결과를 토대로 종자의 크기를 예측할 수 있는 다중 회귀식을 개발했다.
○ 농업형질에 유용한 유전자들의 분리 동정: Sheathed Panicle 표현형 관여 유전자, Pseudo-vivipary 표현형 관여 유전자, 폐화수정계통의 인피결여 관여 유전자, 왜성 관여 (D-h)유전자, dwarf 13 유전자, Panicle Apical Abortion (PAA) 유전자, Early senescence 표현형 관여 유전자(es-k1, es-k2), 잎 반점 관여 유전자, 엽각 조절 및 초형 관여 유전자, 잎 말림(rolled leaf) 조절 유전자, 잎 형태 (narrow and rolled leaf) 조절 유전자, 이삭 기형(abnormal branching panicle) 관여 유전자, Big panicle 표현형 관여 유전자, 소립 종자(small round grain) 관여 유전자, Open-hull sterile spikelet 표현형 관여 유전자, split hull 관여 유전자 등 농업형질에 유용한 다수의 유전자들을 fine mapping하고 map-based cloning 방법으로 동정하였다.
2. 기능성 및 고품질 신형질벼 개발
○ 정상개체에 비해 배아의 크기가 커진 표현형을 갖는 ge-m 돌연변이체는 하나의 열성유전자에 의해 조절되며, mapping을 통해 3번 염색체의 S03p29096마커와 S03p29249마커 사이에 ge-m형질을 조절하는 유전자가 존재하는 것을 확인하였다. 또한, 배아미 품종 선발 및 육성을 위한 기초연구로 종자형태가 다양한 49개의 품종들에 대해 종자 및 배아의 형태적 특징을 조사한 결과 배아함몰도가 높은 품종일수록 배아의 유근과 근초가 배유에 좀 더 깊숙이 매몰되어 있음을 확인하였다.
3. 기후변화 적응 신형질벼 개발
○ 총 105개의 품종과 다산/TR22183 RIL 을 사용하여 2010년 수원, 2010년 상해, 2010년 IRRI우기, 2011년 수원, 2011년 상해, 2011년 IRRI 건기와 우기로 모두 7개 환경에서 간장, 수장, 수수, 영화수, 임실율, 백립중, 수량, 출수기 등을 조사하였다. 그 결과 유전자-환경 상호작용이 제일 많이 나타나는 지역은 2010년 상해였고 그 다음은 IRRI 2011년 건기였다. 농업형질 가운데서 수량과 임실은 유전자-환경의 영향을 각각 57%와 39% 로 제일 많이 받았으며, 지역으로는 수원에서 유전자-환경의 상호작용 영향을 다른 두 지역에 비하여 제일 적게 받았다. 또한 37개의 농업형질관련 QTL이 탐색되었으며 이중 몇 개는 다른 여러 지역에서도 탐색되였다.
4. 벼 일대잡종 품종 개발
○ 일대잡종에서 수당립수의 잡종강세에 관여하는 유전자들의 발현 양상 비교분석 및 자연변이 분석: 4개 모본들과 이들에서 유래한 5개 일대잡종조합을 대상으로 실험을 진행한 결과, 양친과 잡종세대에서 나타나는 24개 수당립수 결정 유전자들의 발현양상 차이는 조합별로 상이하게 나타났다. 특히 수당립수에서 초우성을 나타내는 밀양23/TN1조합에서는 2cm 이하 유수분얼 조직에서 13개 유전자들이 비상가적 발현양상을 나타내는 것으로 관찰되었다. 수당립수를 결정짓는 유전자들 내에서 우수한 표현형의 원인이 되는 haplotype과 SNP를 파악하기 위해 인디카, 자포니카, 통일형을 포함한 3개의 그룹으로 구성된 45개 벼 품종이 사용되었다. 벼의 수당립수 결정에 관여한다고 알려진 11개 유전자의 자연변이를 조사한 결과 총 125개의 SNP와 26개의 Indel 그리고 2개의 대립유전자가 관찰되었으며 이들은 총 55개의 haplotype을 구성하고 있었다. APO2, FON1, HD1, 그리고 LAX1의 유전자좌에 대한 중립성검정결과는 이들이 진화 과정 중 개체군축소 혹은 평형선택과정을 겪었음을 나타내었다. 일반선형모델 연관성 분석 결과를 통해 4개의 이삭형질과 유의하게 관련된 24개의 다형성 지역을 발견할 수 있었으며, 다중 선형 분석 결과 전체 다형성 지역 중 13 개만이 독립 변수로서 유의성을 나타내었고 이들을 통해 4개의 형질에 대해 0.49-0.84 사이의 설명력을 지닌 회귀 방정식을 추론할 수 있었다.
○ 고수량성을 나타내는 벼 일대잡종 모본의 선발을 위한 key-marker 개발 및 잡종강세 유발 유전자좌 분석: 수량관련 형질들에 대한 association 분석을 진행하여 각 형질과 유의하게 연관되어 있는 마커들을 선발하였다. 분석결과 천립중에서 1개, 수수에서 1개, 초장에서 3개, 이삭 당 영화 수에서 5개의 마커가 각 형질에 대해 유의한 연관관계를 보였으나 임실율, 생체중, 이삭 당 등숙립수와 유의한 상관을 보이는 마커는 존재하지 않았다. 밀양23/통88-7 집단의 RILs와 BC1F1s, mid-parent heterosis(MPH) 집단에서 동정된 대부분의 수량 잡종강세 QTL 및 예상수량 잡종강세 QTL은 영화수, 임실률, 간장 잡종강세 QTL과 같은 위치에서 동정되었으며 수량 잡종강세 QTL 단독으로 존재하는 경우도 관찰되었다. 수량 QTL의 전체표현형에 대한 기여도(PVE)는 RILs에서 65.3%, BC1F1s에서 28.8%, MPH에서 46.6%를 나타냈으며, 예상수량의 PVE 값은 RILs에서 52.2%, BC1F1s에서 44.8%, MPH에서 48.1%를 나타냈다.
○ 잡종불임 및 편이분리 관여 유전자좌 분석: 통일형 인디카품종인 다산벼(이하 D)와 자포니카 품종인 일품벼(이하 I)의 교배조합서 유래된 2개의 F2집단과 8개의 BC1F1집단을 사용하여총 15개의 임실율 관연 유전자좌를 동정하였으며 F2집단과 BC1F1집단에서는 8개의 유전자좌가 동정되고 BCF1집단에서는 14개의 유전자좌가 동정되었다. 12개의 염색체에 위치한 STS마커를 이용하여 두 F2 집단의 편이분리 양상에 대한 분석을 진행한 결과, ID 집단에서 50% 이상의 편이분리 현상을 나타낸 염색체로는 3번 염색체 (87.5%), 5번 염색체 (100%), 11번 염색체(66.7%), 12번 염색체 (71.4%)로 나타났으며 DI집단에서 50%이상의 편이분리 현상을 나타나는 염색체로는 3번 염색체(87.5%), 5번 염색체 (100%), 11번 염색체 (66.7%), 12번 염색체(71.4%)로 나타났다. 전체적으로, 45개 (43.7%) 및 41개 (40.2%)의 loci가 ID 및 DI 집단에서 각각 멘델에 법칙에 벗어나 있었다. 두 집단에서의 편이 분리는 주로 Indica 품종인 다산 allele의 증가로 인하여 발생되었다.
Results
1. Isolation and identification of useful genes
○ Identification of high yield related genes: Analyses revealed that 91.8% of the Tongil genome originated from the indica parents and 7.9% from the japonica parent. Copy numbers of SSR motifs, ORF gene distribution throughout the whole g
Results
1. Isolation and identification of useful genes
○ Identification of high yield related genes: Analyses revealed that 91.8% of the Tongil genome originated from the indica parents and 7.9% from the japonica parent. Copy numbers of SSR motifs, ORF gene distribution throughout the whole genome, gene ontology (GO) annotation, and some yield-related QTLs or gene locations were also comparatively analyzed between Tongil and parental varieties. Each genetic factor was transferred from the parents into Tongil rice in amounts that were in proportion to the whole genome composition. The yield-related genes such as sd1, Gn1a, Ghd7, GS3, qSW5, and GW2 were came from the indica parents.
○ Identification of quantitative trait loci for agronomic traits in two rice populations derived from a cross with a wide compatibility line: The Indica-like mutant had tall culm length, slender grain shape and indica type of phenol reaction and KClO3 resistance. Two molecular linkage maps of two F2 populations were constructed for QTL analysis of 8 agronomic traits. Twenty one M-QTLs and 3 E-QTLs were identified in Indica-like mutant/Dasan population. In Indica-like mutant/Hwacheong population, 17 M-QTLs were detected. Of the total 34 QTLs found in the two F2 populations, 6 QTLs were newly identified in this study.
○ Identification of meiotic recombination related genes and detection of meiotic recombination variation: Thirteen subspecies specific meiotic recombination related genes were identified in resequencing data of 10 rice cultivars. For detection of meiotic recombination variation and development of hyper-recombinogenic line, 30 combinations of F1, 8 F2 populations and 4 BC1F1 populations were developed using indica, temperate japonica and wide compatibility varieties. The transformation for overexpression of meiotic recombination related 8 genes were conducting in japonica rice.
○ Regional distribution of haplotype combination and a relationship among grain-size related genes: The study was focused on the distribution of haplotype combination and a relationship between seven genes (GS3, GW2, qSW5, GS6, GW8, GS5, and TGW6). A total of 218 rice germplasms originated from 25 countries were used for genotyping of favorable alleles. Our result suggests that qSW5 play an important role in grain length, grain width, and length to width ratio, GS6 does in grain width and length to width ratio, and both GW8 and GS3 do in 1000-grain weight. For the haplotype distribution, group C is common in most japonica and group U is common in indica. To improve the molecular breeding of rice, we have developed a multiple regression equation to predict the grain size.
○ Isolation of agronomic trait related genes through map-based approach:
Agronomically useful genes were isolated through map-based cloning as listed below; Sheathed panicle related gene, Pseudo-vivipary related gene, Cleistogamy related gene, Dwarf related gene (D-h), Dwarf 13 gene, Panicle Apical Abortion (PAA) related gene, Early Senescence related gene (es-k1, es-k2), Spotted leaf related gene, Leaf angle related gene, Rolled leaf related gene, Narrow and rolled leaf related gene, Abnormal branching panicle related gene, Big panicle related gene, Small round grain related gene, Open-hull sterile spikelet related gene, Split hull related gene.
2. Development of new rice varieties with functionality and high quality
○ The phenotype of ge-m mutant, enlarged embryo, is controlled by single recessive gene. It was confirmed that GE-M gene is located between S03p29096 and S03p29249 on chromosome 3. Because embryo size of ge-m mutant represent more suitable for embryo-retaining polished rice than that of others, it is very promising breeding material. In a similar purpose, we observed embryo dent of 49 commercial varieties and analyzed the relationship among embryo dent, grain size, and shape. As a result, it is confirmed that the higher embryo dent varieties had more deeply embedded embryonic shoot and radicle into endosperm.
3. Development of new rice varieties adaptable for global climate change
○ A total of 105 rice cultivars and a set of recombinant inbred lines(RILS) derived from Dasanbyeo(indica)/TR22183(japonica) crosses were used to study the genotype X environment interactions and QTL analysis for high temperature in rice across several environments. Those plant materials were grown in the three locations which showed seven diverse environments including Suwon (Korea) during 2010 and 2011 rice growing seasons, Shanghai (China) during 2010 and 2011 growing seasons, and IRRI (Philippines) during 2010 growing season, 2011 wet season and 2011 dry season. Eight important agronomic traits including days to heading(DTH), culm length(CL), panicle length(PL), panicle number per plant(PN), spikelet number per panicle(SN), spikelet fertility(SF), 100-grain weight(GW), and grain yield(GY) were measured. The largest environment effect on spikelet fertility was detected in Shanghai2010 compared to that of in IRRIDS2011. Among the evaluated traits, SF and GY showed a high G × E interaction with the mean value of 57% and 39%, respectively suggesting the genotype stability of these two traits were unstable in different traits. The data also revealed that the lowest environment effect was detected in Suwon, followed by Shanghai and IRRI. For the traits measured in multiple environments, 37 QTLs were detected in which some of the QTLs were detected in at least two environments. Of these, six QTLs were detected for days to heading, six for culm length, four for panicle length, three for panicle number, four for spikelet number, seven for grain weight, three for grain yield and four for spikelet fertility.
4. Development of inter-subspecific hybrid rice
○ Analysis of expression and natural variation for genes associated with number of spikelets per panicle in hybrid rice: Four inbred varieties and five F1 derived from these parents were used in this study in order to compare expression level of genes related to number of spikelets per panicle. Difference of expression patterns of 24 genes between parents and F1 was varied according to the cross combination. In particular, M23/TN1 combination, which exhibited over-dominance for number of spikelets per panicle, showed non-additive expression pattern of 13 genes in young panicle meristem which smaller than 2cm. To detect favorable haplotype and SNP within gene sequences which determine number of spikelets per panicle, 45 rice cultivars which consisted to 3 groups including indica, japonica, and tongil were used in this study. A total of 125 SNP, 26 Indel, and 2 alleles were detected in 11 genes related to number of spikelets per panicle. In addition, Fifty-five haplotypes were constructed based on these polymorphisms. Neutrality tests revealed that population subdivision event or balancing selection occurred in locus of APO2, FON1, HD1, and LAX1. Based on the result of GLM association analysis, 25 sites were significantly related with the 4 panicle traits. Thirteen significant sites were significant as independent variables and estimated regression equations could predict the phenotype with r2 of 0.49 – 0.84, performing multiple linear regression analysis.
○ Development of key-markers for predicting yield performance and QTL analysis of heterosis in F1 hybrids: To find the key markers for predicting heterosis, we perform association study using TASSEL software. To perform association study, 7 agronomic traits (PH, Plant height; PN, panicle number; SPP, Spikelet number Per Panicle; FNP, Filled grain number per panicle; SSR, Seed setting rate; TGW, 1000 grain weight; WPP, Weight per plant) were measured for 253 hybrid line, and the 384 SNP genotype data of their parental lines were generated by BeadXpress. As a result, we could get several candidate key markers.
○ QTL analysis for hybrid fertility and their association with female and male sterility in rice: Ten mapping populations comprised of two reciprocal F2 and eight BC1F1 populations generated from the cross between Ilpumbyeo (japonica) and Dasanbyeo (indica) were used to identify QTLs and to interpret the gametophytic factors involved in hybrid fertility or sterility between two subspecies. Frame maps were constructed using a total of 107 and 144 STS markers covering 12 rice chromosomes in two reciprocal F2 and eight BC1F1 populations, respectively. A total of 15 main-effect QTLs and 17 significant digenic-epistatic interactions controlling spikelet fertility (SF) were resolved in the entire genome map of F2 and BC1F1 populations. Among detected QTLs responsible for hybrid fertility, four QTLs, qSF5.1 and qSF5.2 on chromosome 5, qSF6.2 on chromosome 6, and qSF12.2 on chromosome 12, were identified as major QTLs since they were located at corresponding positions in at least three mapping populations. Loci qSF5.1, qSF6.1 and qSF6.2 were responsible for both female and male sterility, whereas qSF3.1, qSF7 and qSF12.2 affected the spikelet fertility only through embryosac factors, and qSF9.1 did through pollen factors.
 표
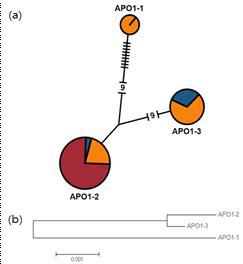
APO1 coding region으로 예측된 Haplotype network 와 Phylogenetic tree (a)haplotype network. 원의 크기는 45개 품종들 중 해당 haplotype에 속하는 품종들의 상대적 인 빈도를 나타내며, 빨간색은 자포니카, 주황색은 인디카, 파란색은 통일형 그룹을 나타낸다. 원사이에 존재하는 선은 염기치환이벤트의 수를 의미하며, 대쉬기호의 수는 분석대상 내에 존 재하지 않다고 추정된 중간형을 나타낸다.(b)Neighbor-joining method를 통해 그려진 phylogetetic tree.
표
APO1 coding region으로 예측된 Haplotype network 와 Phylogenetic tree (a)haplotype network. 원의 크기는 45개 품종들 중 해당 haplotype에 속하는 품종들의 상대적 인 빈도를 나타내며, 빨간색은 자포니카, 주황색은 인디카, 파란색은 통일형 그룹을 나타낸다. 원사이에 존재하는 선은 염기치환이벤트의 수를 의미하며, 대쉬기호의 수는 분석대상 내에 존 재하지 않다고 추정된 중간형을 나타낸다.(b)Neighbor-joining method를 통해 그려진 phylogetetic tree.
 표
APO1 coding region으로 예측된 Haplotype network 와 Phylogenetic tree (a)haplotype network. 원의 크기는 45개 품종들 중 해당 haplotype에 속하는 품종들의 상대적 인 빈도를 나타내며, 빨간색은 자포니카, 주황색은 인디카, 파란색은 통일형 그룹을 나타낸다. 원사이에 존재하는 선은 염기치환이벤트의 수를 의미하며, 대쉬기호의 수는 분석대상 내에 존 재하지 않다고 추정된 중간형을 나타낸다.(b)Neighbor-joining method를 통해 그려진 phylogetetic tree.
표
APO1 coding region으로 예측된 Haplotype network 와 Phylogenetic tree (a)haplotype network. 원의 크기는 45개 품종들 중 해당 haplotype에 속하는 품종들의 상대적 인 빈도를 나타내며, 빨간색은 자포니카, 주황색은 인디카, 파란색은 통일형 그룹을 나타낸다. 원사이에 존재하는 선은 염기치환이벤트의 수를 의미하며, 대쉬기호의 수는 분석대상 내에 존 재하지 않다고 추정된 중간형을 나타낸다.(b)Neighbor-joining method를 통해 그려진 phylogetetic tree.
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.