최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 국립농업과학원 National Institute of Agricultural Sciences |
|---|---|
| 연구책임자 | 윤웅한 |
| 참여연구자 | 한장호 , 김태호 , 남상식 , 양정욱 , 이형운 , 설영주 , 이태호 , 윤성원 , 이근표 , 정재철 , 이행순 , 김호수 , 박세연 , 왕지 , 커칭보 , 곽상수 , 지창윤 , 진룡 , 김차영 , 정유정 , 안철한 , 박지혜 , 편장원 , 기수진 , 김소영 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2018-02 |
| 과제시작연도 | 2017 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO201800043093 |
| 과제고유번호 | 1395050531 |
| 사업명 | 포스트게놈신산업육성을위한다부처유전체사업(농진청) |
| DB 구축일자 | 2018-11-24 |
| 키워드 | 고구마.유전체.차세대염기 서열분석.전사체.정보종합화.sweetpotato.genome.NGS.transcriptom.database. |
| DOI | https://doi.org/10.23000/TRKO201800043093 |
< 제 1세부 >
가. 2배체 고구마 Mx23Hm 유전체 해독(4% Mb)
나. 2배체 고구마 Mx23Hm 유전체 정보 분석: 유전자 수 37,000개
다. 6배체 고구마 Xushu 18 유전체 해독(1.83 Gb)
라. 6배체 고구마 Xushu 18 유전체 정보 분석
마. 고구마 거대 유전체 조립 및 비교 유전체 해석
바. 고구마 엽록체 및 미토콘드리아 유전체 구조해석 및 정보분석
사. 국내 고구마(전미, 주황미, 신자미) 특성 평가 및 유전체 구조 해독
< 제1협동 ><
< 제 1세부 >
가. 2배체 고구마 Mx23Hm 유전체 해독(4% Mb)
나. 2배체 고구마 Mx23Hm 유전체 정보 분석: 유전자 수 37,000개
다. 6배체 고구마 Xushu 18 유전체 해독(1.83 Gb)
라. 6배체 고구마 Xushu 18 유전체 정보 분석
마. 고구마 거대 유전체 조립 및 비교 유전체 해석
바. 고구마 엽록체 및 미토콘드리아 유전체 구조해석 및 정보분석
사. 국내 고구마(전미, 주황미, 신자미) 특성 평가 및 유전체 구조 해독
< 제1협동 >
가. 6배체 고구마 Xushu 18 표준전사체 정보 분석
나. 6배체 고구마 Xushu 18 환경스트레스 특이적 유전자 정보분석
다. 6배체 고구마 Xushu 18 조직별 특이적 유전자 정보분석
라. 고구마 스트레스 특이적 유전자 상호네트워크 분석
마. 국내 6배체 고구마 전미, 주황미, 신자미 표준전사체 정보 분석
바. 국내 6배체 고구마 특이적 유전자 정보 분석
(출처 : 보고서 요약서 3p)
Purpose&Contents
This research goal is genome sequencing of sweetpotato genome and transcriptom using the NGS. We also utilize the genome information of sweetpotato genome for the isolation of unique sweetpotato genes and provide genome information to the researchers.
Results
〈 Project
Purpose&Contents
This research goal is genome sequencing of sweetpotato genome and transcriptom using the NGS. We also utilize the genome information of sweetpotato genome for the isolation of unique sweetpotato genes and provide genome information to the researchers.
Results
〈 Project 1 >
- For the genome sequencing of diploid sweetpotato Mx23Hm, De novo whole genome assembly was conducted with 58.19 Gb PacBio reads using the HGAP 2.0 assembler. As a result, total number of contigs was 650, N50 scaffold length was 5.361 Mb, and total size of scaffold was 496.316 Mb. Gene prediction was made by evidenced gene model and predicted gene model pipelines.
- Also, the whole genome sequencing of hexaploid sweetpotato Xushu 18 was performed using Illumina and PacBio sequencing platforms. De novo whole genome assembly with 181.5 Gb PacBio reads (69.8X) of hexaploid Xushu 18 was performed. We performed genome analysis of three domestic sweetpotato varieties.
〈 Project 2 〉
- For the reference transcriptome of hexaploid sweetpotato Xushu 18, hybrid assembly using Hiseq, Miseq and Isoform seq (from PacBio RSII and Sequel platform) was conducted. Final 63,922 reference transcriptome for Xushu 18 was constructed and this information was used for genome annotation in Project 1.
- The stress responsive and tissue specific expressed gene information were analysed and there network relation was analysed.
- The reference transcriptome for Korean sweetpotato cultivar (Jeonmi, Juhwangmi, Sinjami) was constructed using PacBio Isoform sequencing
Expected Contribution
The results of the sweetpotato genome sequences will be constructed in the form of DB and will provide information to the researchers and contribute for the isolation of genes.
(출처 : Summary 5p)
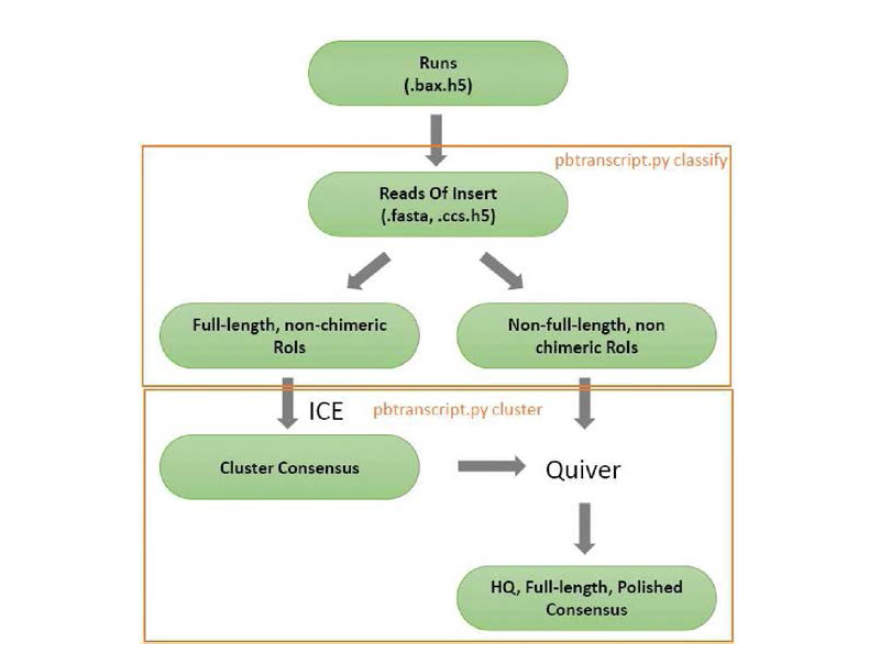 표
PacBio Isoform sequencing basic protocol. Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyA tail detection. The output sequences are stripped of primers and polyA tails and re-oriented. Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length
표
PacBio Isoform sequencing basic protocol. Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyA tail detection. The output sequences are stripped of primers and polyA tails and re-oriented. Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length
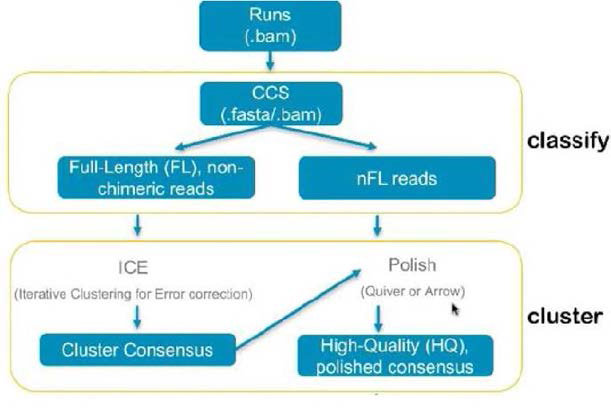 표
Pacbio Sequel isoform seqeuencing analysis protocol SMRTLink5 0 Sequel IsoSeqclassify Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyAtail detection The output sequences are stripped of primers and polyAtails and re-oriented Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length and transcript length, which may be anywhere between 85-100 SMRTLink5 0 Sequel IsoSeqlCE and Quiver on - 187 - cluster Time and memory-intensive isoform-level clustering algorithm that outputs high-quality consensus transcript sequences Every output sequence is an isoformconsensus that is the consensus of many different reads that are considered by the algorithm to be the same isoform Quiver is used to generate the consensus and the associated consensus QVs are used to estimate how good the final consensus accuracy is Based on the Quiver estimated accuracy and user parameter (Default accurate), the consensus sequences are categorized as HQ (high-quality, above or user-defined cutoff) and LQ (low-quality) http //pacb com
표
Pacbio Sequel isoform seqeuencing analysis protocol SMRTLink5 0 Sequel IsoSeqclassify Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyAtail detection The output sequences are stripped of primers and polyAtails and re-oriented Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length and transcript length, which may be anywhere between 85-100 SMRTLink5 0 Sequel IsoSeqlCE and Quiver on - 187 - cluster Time and memory-intensive isoform-level clustering algorithm that outputs high-quality consensus transcript sequences Every output sequence is an isoformconsensus that is the consensus of many different reads that are considered by the algorithm to be the same isoform Quiver is used to generate the consensus and the associated consensus QVs are used to estimate how good the final consensus accuracy is Based on the Quiver estimated accuracy and user parameter (Default accurate), the consensus sequences are categorized as HQ (high-quality, above or user-defined cutoff) and LQ (low-quality) http //pacb com
 표
PacBio Isoform sequencing basic protocol. Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyA tail detection. The output sequences are stripped of primers and polyA tails and re-oriented. Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length
표
PacBio Isoform sequencing basic protocol. Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyA tail detection. The output sequences are stripped of primers and polyA tails and re-oriented. Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length
 표
Pacbio Sequel isoform seqeuencing analysis protocol SMRTLink5 0 Sequel IsoSeqclassify Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyAtail detection The output sequences are stripped of primers and polyAtails and re-oriented Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length and transcript length, which may be anywhere between 85-100 SMRTLink5 0 Sequel IsoSeqlCE and Quiver on - 187 - cluster Time and memory-intensive isoform-level clustering algorithm that outputs high-quality consensus transcript sequences Every output sequence is an isoformconsensus that is the consensus of many different reads that are considered by the algorithm to be the same isoform Quiver is used to generate the consensus and the associated consensus QVs are used to estimate how good the final consensus accuracy is Based on the Quiver estimated accuracy and user parameter (Default accurate), the consensus sequences are categorized as HQ (high-quality, above or user-defined cutoff) and LQ (low-quality) http //pacb com
표
Pacbio Sequel isoform seqeuencing analysis protocol SMRTLink5 0 Sequel IsoSeqclassify Separates Reads Of Insert reads into full-length and non-full-length based on primer and (optionally) polyAtail detection The output sequences are stripped of primers and polyAtails and re-oriented Each output sequence represents exactly one read from a single ZMW (single molecule) and accuracy for each read varies depending on raw read length and transcript length, which may be anywhere between 85-100 SMRTLink5 0 Sequel IsoSeqlCE and Quiver on - 187 - cluster Time and memory-intensive isoform-level clustering algorithm that outputs high-quality consensus transcript sequences Every output sequence is an isoformconsensus that is the consensus of many different reads that are considered by the algorithm to be the same isoform Quiver is used to generate the consensus and the associated consensus QVs are used to estimate how good the final consensus accuracy is Based on the Quiver estimated accuracy and user parameter (Default accurate), the consensus sequences are categorized as HQ (high-quality, above or user-defined cutoff) and LQ (low-quality) http //pacb com
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.