최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 강원도보건환경연구원 Gangwon Institute of Health and Environment |
|---|---|
| 연구책임자 | 임은주 |
| 참여연구자 | 고은미 , 이은경 , 이정선 , 류은정 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2019-12 |
| 과제시작연도 | 2019 |
| 주관부처 | 보건복지부 [Ministry of Health & Welfare(MW)(MW) |
| 과제관리전문기관 | 질병관리본부 Korea Center for Diease Control and Prevention |
| 등록번호 | TRKO202000029211 |
| 과제고유번호 | 1465028463 |
| 사업명 | 감염병관리기술개발연구(R&D) |
| DB 구축일자 | 2020-09-05 |
| 키워드 | 원헬스.항생제 내성균.ESBL 대장균.One-Health.Antimicrobial resistant bacteria.ESBL E. coli. |
숙주-환경 내 항생제 내성균 조사연구를 위해, 2017~2019년까지 도내에서 발생한 설사환자의 대변검체, 식중독 관련 식품검체, 하천수 및 하수처리장수 등 환경검체에서 항생제 내성균을 분리하여 항생제 내성양상 및 내성유전자 특성을 확인하였고 MLST 및 PFGE법을 활용하여 내성주 간의 상관성을 분석하였다.
설사환자의 대변 5,033건, 식품 788건, 환경 466건 등 총 6,287건의 검체에서 항생제 내성연구용역 대상균 1,216주를 분리하였으며, 항생제 감수성 검사를 통해 내성주 976주(대장균 797, 폐렴간균
숙주-환경 내 항생제 내성균 조사연구를 위해, 2017~2019년까지 도내에서 발생한 설사환자의 대변검체, 식중독 관련 식품검체, 하천수 및 하수처리장수 등 환경검체에서 항생제 내성균을 분리하여 항생제 내성양상 및 내성유전자 특성을 확인하였고 MLST 및 PFGE법을 활용하여 내성주 간의 상관성을 분석하였다.
설사환자의 대변 5,033건, 식품 788건, 환경 466건 등 총 6,287건의 검체에서 항생제 내성연구용역 대상균 1,216주를 분리하였으며, 항생제 감수성 검사를 통해 내성주 976주(대장균 797, 폐렴간균 112, 살모넬라균 32, 황색포도알균 35)를 확인하였다.
대장균과 폐렴간균은 항생제별 내성양상이 유사하였는데, β-Lactam계 항생제인 Penicillin계와 Cephem계 항생제에 높은 내성을 보였고 non-β-Lactam계 항생제인 Ciprofloxacin, Trimethoprime-sulfamethoxazole에도 높은 내성을 보였다. 그러나 Carbapenem계 항생제의 경우 대장균(1.0~1.2%)에 비해 폐렴간균(7.1~10.6%)에서 높은 내성을 보였다. 살모넬라균은 ampcillin과 tetracycline의 내성률이 각각 55.8%, 50%로 가장 높았고, Cephem계 항생제인 cefoxitin에도 17.3%의 내성을 보였다. 황색포도알균은 cefoxitin 내성률이 68.8%로 가장 높았고, erythromycin과 clindamycin도 각각 52.1%, 35.4%의 내성을 보였다. 또한 살모넬라균 5주, 대장균 8주와 폐렴간균 3주에서는 Colistin 내성도 확인되었다.
내성유전자 실험 결과, ESBL 생성주는 총 677주(대장균 570주, 폐렴간균 99주, 살모넬라균 8주)였으며, 90% 이상이 blaCTX-M 내성유전자를 가지고 있었고 주요 유전자형은 CTX-M-14형과 CTX-M-15형이었다. PABL 생성주는 대장균 38주와 폐렴간균 5주였으며, 주요 유전형은 CMY-2형(62.8%)과 DHA-1형(37.2%)이었고, carbapenemase 생성주는 대장균 6주와 폐렴간균 9주로 주요 유전형은 NDM-5(66.6%), KPC-2(33.3%)였다.
Methicillin 내성 황색포도알균 33주는 모두 mecA형이었으며, SCCmec II형 21주, IV형 12주였다.
ESBL 대장균 중 β-lactam계의 6계열 항생제에 내성을 보이는 198주의 MLST 분석 결과, 40가지 유형이 확인되었으며 ST131이 34.1%(61주)로 가장 주요한 유형이었다. 또한 ESBL 대장균 198주 중 춘천에서 분리된 114주에 대한 PFGE 분석 결과, 임상 및 환경에서 분리된 내성주 중에서 유사도가 87.9%이상으로 높으면서 항생제 내성양상, CTX-M 유전형, MLST 유형이 유사하거나 동일한 균(12주)을 확인하여 사람-환경 간 내성균 전파 가능성에 대한 근거자료를 확보하였다.
본 연구를 통해, 강원도 내 항생제 내성균의 분포를 확인하였고 차세대 내성균 진단 및 항생제 개발에 활용할 수 있는 다수의 내성균을 확보하였으며, 내성주의 항생제 감수성 및 유전자 특성에 대한 기초자료를 확보함으로써 국가 항생제 관리를 위한 내성 데이터베이스 구축에 일조하였다.
(출처 : 요약문 4p)
To investigate antibiotics resistant bacteria in the host and the environment, we isolated antibiotic-resistant bacteria from clinical, food and environmental samples in Gangwon-do from 2017 to 2019.
A total of 6,287 samples were collected, including 5,033 clinical samples, 788 food samples,
To investigate antibiotics resistant bacteria in the host and the environment, we isolated antibiotic-resistant bacteria from clinical, food and environmental samples in Gangwon-do from 2017 to 2019.
A total of 6,287 samples were collected, including 5,033 clinical samples, 788 food samples, and 466 environmental samples. The antibiotic-resistant strains isolated from them are 976, including 797 of E. coli, 112 of K. pneumoniae, 32 of Salmonella spp, and 35 of S. aureus using antimicrobial susceptability test.
The antibiotic resistance patterns of E. coli and K. pneumoniae were similar.
It showed the high resistance rates to β-lactam group as well as non β-lactam group. However, K. pneumoniae(7.1~10.6%) had more resistant to carbapenems than E. coli(1.0~1.2%). We found high resistance rates in Salmonella spp. for ampicillin(55.8%) and tetracyclin(50.0%) and in S. aureus for cefoxitin(68.8%).
Additionally, 16 strains of colistin-resistant bacteria were isolated, including 5 of Salmonella spp., 8 of E. coli and 3 of K. pneumoniae.
We identified a total of 677 ESBL producing strains, of which more than 90% had blaCTX-M gene and the major genotypes are CTX-M-14 and CTX-M-15. 43 of PABL-producing bacteria(38 of E. coli and 5 of K. pneumoniae) were identified and the major genotypes were CMY-2(62.8%). Carbapenemase-producing strains were 6 of E. coli and 9 of K. pneumoniae and the major genotypes of carbapenemase were NDM-5(66.6%). Within 33 MRSA isolates, 21 strains were SCCmec type Ⅱ and 12 strains were SCCmec type Ⅳ.
We performed to MLST analysis on 198 strains having resistance to six classes of β-lactams in ESBL-producing E. coli, and ST131 was the most dominant type with 34.1%. As a result of performing PFGE analysis on 114 of ESBL-producing E. coli isolated in Chuncheon, 12 strains isolated from clinical and environmental samples were confirmed with more than 87.9% similarity. It was obtained that the evidence on the possibility of propagation of resistant bacteria between human and environments.
In this study, we confirmed the distribution of antibiotic resistant bacteria in Gangwon-do and isolated a large amount of resistant bacteria that can be used for diagnosis of next-generation resistant bacteria and for development of antibiotics. By obtaining characteristics to the antimicrobial resistant bacteria, it fairly contributed to the establishment of database for the management of antibiotics in the country.
(출처 : SUMMARY 5p)
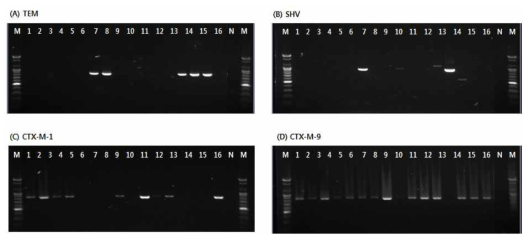 표
Detection of amplified ESBL gene products for blaTEM(A), blaSHV(B), blaCTX-M-1(C) and blaCTX-M-9(D) from antimicrobial resistant E. coli strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~16: ESBL-producing strains isolated from clinical and environmental samples, Lane N: Negative control
표
Detection of amplified ESBL gene products for blaTEM(A), blaSHV(B), blaCTX-M-1(C) and blaCTX-M-9(D) from antimicrobial resistant E. coli strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~16: ESBL-producing strains isolated from clinical and environmental samples, Lane N: Negative control
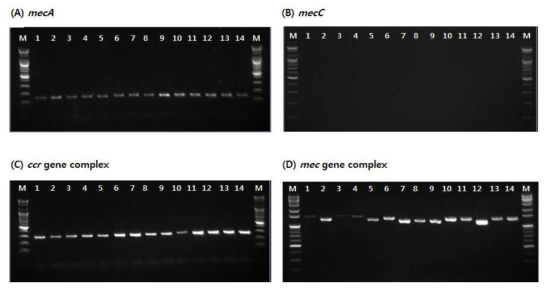 표
Detection of amplified methicillin resistance gene products for mecA(A), mecC(B), ccr gene complex(C) and mec gene complex(D) from methicillin resistant strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~14: methicillin resistant strains isolated from clinical samples, N: Negative control
표
Detection of amplified methicillin resistance gene products for mecA(A), mecC(B), ccr gene complex(C) and mec gene complex(D) from methicillin resistant strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~14: methicillin resistant strains isolated from clinical samples, N: Negative control
 표
Detection of amplified ESBL gene products for blaTEM(A), blaSHV(B), blaCTX-M-1(C) and blaCTX-M-9(D) from antimicrobial resistant E. coli strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~16: ESBL-producing strains isolated from clinical and environmental samples, Lane N: Negative control
표
Detection of amplified ESBL gene products for blaTEM(A), blaSHV(B), blaCTX-M-1(C) and blaCTX-M-9(D) from antimicrobial resistant E. coli strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~16: ESBL-producing strains isolated from clinical and environmental samples, Lane N: Negative control
 표
Detection of amplified methicillin resistance gene products for mecA(A), mecC(B), ccr gene complex(C) and mec gene complex(D) from methicillin resistant strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~14: methicillin resistant strains isolated from clinical samples, N: Negative control
표
Detection of amplified methicillin resistance gene products for mecA(A), mecC(B), ccr gene complex(C) and mec gene complex(D) from methicillin resistant strains isolated in 2018. * Lane M: 100bp DNA ladder, Lane 1~14: methicillin resistant strains isolated from clinical samples, N: Negative control
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.