최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 경상대학교 산학협력단 GyeongSang National University |
|---|---|
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2015-02 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO201500010725 |
| DB 구축일자 | 2015-07-11 |
Ⅳ. 연구개발결과
1. 새싹보리와 신선초의 유용대사체 발굴 및 대사체 Flow 규명
○ 새싹보리에서의 주요 활성대사체인 폴리코사놀 9종을 발굴하고 생육시기별 폴리코사놀 대사체의 Flow 규명을 완성하였다.
폴리코사놀의 함량은 발아 후 5일 (109.7mg/100g)부터 10일 (343.7mg/100g)까지는 급격히 증가하다가 그 이후 점차 감소함 (J. Agric. Food Chem. 2013, 1117-1123).
○ 새싹보리의 생육시기별 AMPK 활성을 검정하고, AMPK의 활성이 대사체의 Flow와 밀접한
Ⅳ. 연구개발결과
1. 새싹보리와 신선초의 유용대사체 발굴 및 대사체 Flow 규명
○ 새싹보리에서의 주요 활성대사체인 폴리코사놀 9종을 발굴하고 생육시기별 폴리코사놀 대사체의 Flow 규명을 완성하였다.
폴리코사놀의 함량은 발아 후 5일 (109.7mg/100g)부터 10일 (343.7mg/100g)까지는 급격히 증가하다가 그 이후 점차 감소함 (J. Agric. Food Chem. 2013, 1117-1123).
○ 새싹보리의 생육시기별 AMPK 활성을 검정하고, AMPK의 활성이 대사체의 Flow와 밀접한 관계가 있음을 규명함. 또한 헥사코사놀(C26)이 주요 활성 대사체임을 밝힘.
○ 신선초 활성대사체의 분리 분석 및 식물체 부위별 활성대사체 함량을 정량 분석함.
신선초의 활성 대사체를 동시 분석할 수 있는 MRM법을 최초로 완성하여 각 부위별 대사체 함량평가에 성공함 (Food Chemistry. 2014, 20-27).
○ 신선초의 2차대사체의 각 부위별 주성분 분석과 각 부위별 주요 대사체의 변화와 특징을 규명함. 잎, 줄기, 뿌리 등 부위에 따라 대사체가 선택적으로 분포함.
2. 면역활성 제어 대사체 발굴 및 기전 규명
○ ADS에 의한 면역활성 기전 규명
- 약 40여개의 작물 유래 대사체를 대상으로 면역활성 및 제어에 관한 생물활성을 스크리닝 하여 ADS 선발
○ PPARγ 리간드 타겟 Th17 세포 활성 억제
- 본 연구를 통해 Th17 세포 제어에 대한 분자 타겟으로 PPARγ 리간드를 제시하였으며, Th17 면역제어 대사체 발굴 시스템을 구축하였음
○ CpG ODN과 liposome complex(Lipoplex)를 이용한 항암 치료 검증 및 종양환경 평가 시스템 구축
- Lipoplex의 종양내 투여는 종양치료 효과를 나타냄: 다양한 투여경로중 종양내 투여만이 치료효과를 나타냈으며, 종양 치료효과는 NK세포와 CD8T세포 의존적이었음.
3. 유용대사체 관련 단백체 발굴 및 네트워크 구축
가. 식물체 잎 및 종자의 과발현 단백질 제거 기술 개발
○ 콩잎에서 과발현 되는 주요 단백질인 루비스코를 제거하는 기술인 Protamine sulfate 침전법을 이용하여, 식물체 잎의 저발현 단백질들을 분석할 수 있는 기술을 개발하였다.
○ 또한 PSP method의 경우, 식물의 종에 국한되지 않고 다양한 종류의 식물체 잎에 적용되는 것을 확인하였다. (Proteomics, 2013, 2176-2179)
○ 그리고 콩 종자에서의 경우, PSP method를 이용하여 단백질을 추출할 경우 콩 종자 내에 과발현되는 주요 저장 단백질들이 제거되는 것을 확인하였다. (Proteomics, 2015, DOI: 10.1002/pmic.201400488)
나. 서로 다른 종피색을 가지는 종자의 단백질 분석 및 유기화합물 생합성 경로 유전자 분석
○ 만리콩, 만리콩 mutant의 개화 발달 단게에 따른 종피의 색차이를 보이는 것에 대한 분석으로 단백질의 발현 패턴 비교를 실시하였다.
○ 또한 각 콩 종자와 꼬투리의 phenylpropanoid 유전자들이 flowering 후 5주가 경과하였을 때 만리콩 mutant와 비교하여 만리콩에서 보다 높게 발현이 됨을 semi-qunatitative RT-PCR 분석을 통하여 확인하였다. (Proteomics. 2015, DOI: 10.1002/pmic.201400453)
4. 식물대사 네트워크 및 Flow 조절을 통한 유용대사체 생산기술 개발
가. 고구마 유래 IbMYB1a 유전자 과발현 안토시아닌 고함유 형질전환식물체 개발 및 분석
○ 3종류의 프로모터(35S, SPO, SPWP2) 조절하에 고구마 유래 IbMYB1a 유전자 과발현 형질전환식물체(애기장대, 담배, 알팔파)를 개발하였다. IbMYB1a-OX 형질전환식물체는 잎과 줄기 등에서 높은 함량의 자색의 안토시아닌 색소를 축적하였으며, 이러한 안토시아닌은 HPLC 분석을 통하여 시아니딘 계열의 안토시아닌으로 확인되었다. 또한 IbMYB1a 유전자 발현에 의하여 안토시아닌 생합성에 관련된 구조 유전자들의 발현이 증가됨을 RT-PCR 분석을 통하여 관찰하였다. 특히 3종류의 다른 프로모터 조절하에 IbMYB1a 유전자 과발현 형질전환 담배식물체는 각기 다른 안토시아닌 함량과 표현형을 보였다. SPO-M, SPA-M, 35S-M 순으로 안토시아닌 축적 함량이 높았으며 안토시아닌 축적 함량이 최고 높은 SPO-M 식물체는 식물생장에 장애를 보였으며 때로는 stunt 표현형을 나타내기도 하였다. 이러한 결과는 고구마 유래 IbMYB1a 전사인자 발현이 이종식물체(애기장대, 담배, 알팔파)에서도 안토시아닌 생합성 유전자들의 전사발현을 유도하고 식물체에 안토시아닌 축적을 유도함을 보여준다.
나. 안토시아닌 고함유 담배식물체와의 교배를 통한 레스베라트롤 유도체 고함유 교배담배식물체 개발
○ 대황 유래 RpSTS 및 포도유래 VrROMT 유전자 과발현 형질전환식물체(35S-STS-OX, 35S-ROST-OX: 애기장대, 담배)를 개발하고 식물체 잎에서 물질분석을 수행한 결과 아주 낮은 함량의 레스베라트롤 유도체(trans-resveratrol, trans-piceid)가 확인되었다. 이것은 아마도 페닐프로파노이드 대사생합성 중간 대사체(precursors) 공급(flow)이 충분하지 않아서 스틸벤 화합물 생성까지 전달되지 못하기 때문인 것으로 생각된다. 따라서 페닐프로파노이드 대사생합성 중간 대사체 공급을 증진시키기 위해서 35S-STS-OX (35S-S) 및 35S-ROST-OX (35S-RS) 담배 식물체와 안토시아닌 고함유 식물체(SPO/SPAIbMYB1a-OX: SPO-M, SPA-M)를 상호 교배(cross-pollination)를 수행하였다. 상호 교배를 수행하였을 때 웅성불임의 표현형을 보이던 35S-S 및 35S-RS 담배 식물체는 정상적으로 종자를 맺는 표현형으로 회복되어졌다. 교배 식물체를 일차적으로 kanamycin 과 basta 항생제 배지에서 선발하고 어린잎에서의 안토시아닌 색소 생성여부를 통하여 교배 담배식 물체를 선발하였다(F1 세대). Western blot 분석으로 STS 유전자 과발현 우수 식물체를 선발하였으며, 최종적으로 선발된 교배 담배식물체(분홍)는 35S-S 및 35S-RS 식물체(연한 분홍)보다는 꽃 색깔이 진하였으며 SPO/SPA-M 안토시아닌 고함유 담배 식물체의 꽃 색깔(진한 분홍) 보다는 옅은 색깔의 표현형을 나타내었다. 잎에서도 교배 담배식물체(35S-S/-RS x SPO/SPA-M)는 SPO/SPA-M 보다는 낮지만 높은 안토시아닌 축적을 나타내었다. 이러한 교배 담배식물체를 이용하여 HPLC 및 LC-MS 분석을 수행하였을 때 식물체의 잎 조직뿐만 아니라 줄기, 꽃, 뿌리 조직에서도 상당히 높은 양의 레스베라트롤 유도체(trans-piceid, cis-piceid, piceid methyl ether, resveratrol methyl ether O-hexoside, etc) 들이 생성됨을 알 수 있었다. 이러한 결과는 생합성 유전자 과발현에 의해 레스베라트롤 생성량을 높이기 위해서는 대사생합성 중간 대사체 공급이(flow) 원활히 이뤄져야함을 나타내는 것으로 IbMYB1a 유전자 발현을 통하여 페닐프로파노이드 대사생합성 중간대사체 공급이 증진되었음을 나타낸다. 실지로 교배 담배식물체에서 PAL, C4H 유전자와 같은 페닐프로파노이 생합성관련 유전자들의 발현이 IbMYB1a 유전자 과발현에 의하여 증진됨을 RT-PCR 분석을 통하여 알 수 있었다.
다. 에테폰 처리한 콩잎 전사체 분석 및 이소플라본 생합성관련 유전자 발현 분석 및 생합성 조절 후보 MYB 전사인자 발굴
○ 제1세부과제 연구팀과 협동연구를 통하여 에테폰을 2~3개월된 콩 식물체에 처리하였을 때 잎 조직에서 이소플라본 화합물(daidzin, genistin, malonyldaidzin, malonylgenistin.) 함량이 크게 증가됨을 관찰하였다. 이러한 결과를 바탕으로 이소플라본 생합성 핵심 조절인자를 발굴하고자 에테폰 처리한 콩잎을 사용해서 전사체(RNA-seq) 분석 및 RT-PCR 분석을 통하여 유전자 발현이 증가되어진 이소플라본 생합성 유전자(CHS, CHI, IFS, FMaT, F7GT) 및 MYB 전사인자를 탐색하고 최종적으로 6종류의 콩 유래 MYB 전사인자(GmMYB12a, GmMYB75, GmMYB84, GmMYB108, GmMYB140, GmMYB156)를 분리하였다. 이러한 6종의 MYB 전사인자에 대한 최적의 식물발현벡터 시스템을 구축하고 현재 MYB 유전자 과발현 형질전환식물체를 개발 중에 있다.
5. BNIT기술 이용 유용 기능성 물질 개발
○ 가수분해 효소와 나노물질을 결합한 신규 다기능성 나노하이브리드바이오 촉매를 개발하고 이를 이용하여 항염제의 일종인 paracetamol의 전합성이 가능하다는 것을 증명함.
○ 줄기세포 분화를 유도하는 식물 대사체를 발굴하기 위해 p19 cell에 reporter를 넣은 분화검증 assay system를 확립하고 이를 통해 줄기세포를 심근세포로 유도하는 식물대사체를 발굴하고 그 활성을 측정하였음.
Ⅳ. Results and Application
1. Identification of valuable metabolite in barley sprout, A. keiskei and their metabolite flow
○ Main bioactive metabolites in barley sprout, nine policosanols were completely identified and their metabolite flow according to growth stage was elucidated.
Metaboli
Ⅳ. Results and Application
1. Identification of valuable metabolite in barley sprout, A. keiskei and their metabolite flow
○ Main bioactive metabolites in barley sprout, nine policosanols were completely identified and their metabolite flow according to growth stage was elucidated.
Metabolite flow showed that the amounts of policosanols in the barley dramatically increased between 5 days and 10 days post-sprouting and then levels fell back down at 20 days (J. Agric. Food Chem. 2013, 1117-1123).
○ AMPK was activated significantly by the hexane extract of barley sprouts. This AMPK activation emerges across the growth stage of the sprout, becoming most significant 10days post-sprouting.
○ The principal metabolites within A. keiskei were isolated, enabling us to quantify the metabolites within different parts of the plant.
The specific quantification of metabolites was accomplished by multiple reaction monitoring(MRM) using a quadruple tandem mass spectrometer (Food Chemistry. 2014, 20-27).
○ We have undertaken an in-depth quantitative analysis of the phenolic metabolites within an important functional food stuff. The distribution of these metabolites varied significantly across the different components of plant.
2. Evaluation of valuable metabolites as valuable lead compounds
○ Validation of immune modulatory activity of secondary metabolite, 6-acetonyl-5,6-dihydrosanguinarine (ADS).
: Although derivatives of saguinarine were known as immune suppressor, ADS showed strong immune stimulatory activity to mouse macrophage cell line, RAW264.7. in terms of cell death, apoptosis and autophagy.
○ Suggestion of Th17 modulation using PPAR-gamma agonist
○ Tumor regulation using primary metabolite, CpG DNA-Liposome complex
3. Proteomic network of functional metabolic related proteins in crops
A. Depletion of abundant plant Rubisco protein using the protamine sulfate precipitation method (Proteomics. 2013 Jul;13(14):2176-2179. IF=3.96 ).
- Ribulose-1,5-bisphosphate carboxylase/oxygenase (RuBisCO) is the most abundant plant leaf protein, hampering deep analysis of the leaf proteome. Here, we describe a novel protamine sulfate precipitation (PSP) method for the RuBisCO depletion. For this purpose, soybean leaf total proteins were extracted using the Tris-Mg/NP-40 extraction buffer. Obtained clear supernatant was mixed with PS, followed by 13% SDS-PAGE analysis of total, PS-supernatant and -precipitated proteins. In a dose-dependent experiment, 0.1% (w/v) PS was found to be suitable for precipitating RuBisCO large and small subunits (LSU and SSU). Western-blot analysis confirmed no detection of RuBisCO LSU in PS-supernatant. Application of this method to Arabidopsis, rice, and maize leaf proteins showed results similar to soybean. Furthermore, 2-DE analyses of PS-treated soybean leaf displayed enriched protein profile for PS-supernatant over total proteins. Randomly-selected enriched 2-D spots were successfully assigned for their protein identity by MALDI-TOF-TOF-MS. Hence, the PSP method is: (i) simple, fast, economical, and reproducible for RuBisCO precipitation from the plant leaf sample; (ii) applicable to both dicot and monocot plants; and (iii) suitable for down-stream in-depth proteomics analysis.
B. Protamine sulfate precipitation method depletes abundant plant seed-storage proteins: A case study on legume plants (Proteomics, 2015, DOI: 10.1002/pmic.201400488)
- Depletion of abundant proteins is one of the effective ways to improve detection and identification of low-abundance proteins. Our previous study showed that protamine sulfate precipitation (PSP) method can deplete abundant ribulose-1,5-bisphosphate carboxylase/oxygenase (RuBisCO) from leaf proteins and is suitable for their in-depth proteome investigation. In this study, we provide evidence that the PSP method can also be effectively used for depletion of abundant seed-storage proteins (SSPs) from the total seed proteins of diverse legume plants including soybean, broad bean, pea, wild soybean, and peanut. The 0.05% PS was sufficient to deplete major SSPs from all legumes tested except for peanut where 0.1% PS was required. SDS-PAGE, Western blotting and 2DE analyses of PS-treated soybean and peanut seed proteins showed enriched spots in PS-supernatant than total proteins. Coefficient of variation percentage (%CV) and principal component analysis of 2DE spots support the reproducibility, suitability, and efficacy of the PSP method for quantitative and comparative seed proteome analysis. MALDI-TOF-TOF successfully identified some protein spots from soybean and peanut. Hence, this simple, reproducible, economical PSP method has a broader application in depleting plant abundant proteins including SSPs in addition to RuBisCO, allowing discussion for comprehensive proteome establishment and parallel comparative studies in plants.
C. Comparative investigation of seed coats of brown- versus yellow-colored soybean seeds using an intergrated proteomics and metabolomics approach (Proteomics. 2015 DOI: 10.1002/pmic.201400453. IF=3.96).
- Seed coat (testa) color is an important attribute determining consumption of soybean seeds. Soybean cultivar Mallikong (M) has yellow seed coat while its naturally mutated cultivar (Mallikong mutant, MM), develops brown seed-coat color upon maturation. Here, we used integrated proteomics (2DE) and metabolomics approach to investigate seed coats of M and MM during seed development (4 through 6 weeks after flowering). Morphologically, M and MM manifested differences only in testa and hilum colors. 2DE quantitative profiling of total proteins from three developmental stages of seed coats coupled with MALDI-TOF/TOF analysis resulted in identification of 172 differentially abundant protein spots in MM compared with M. Of 172 spots, 62 and 105 spots showed increased and decreased protein abundance in MM compared with M, respectively; 5 protein spots were detected only in MM. Overall, proteins involved in primary metabolism had decreased protein abundance in MM, suggesting energy in MM might be utilized for proanthocyanidin biosynthesis via secondary metabolic pathways. Total isoflavone content and individual isoflavone components (daidzin, glycitin, genistin, mal-daidzin, and mal-glycitin) were significantly lower in MM than M. We propose that low isoflavones level in MM may offer a high substrate for proanthocyanidin production and consequently brown seed coat in MM.
4. Development of platform technology for production of useful metabolites by controlling plant metabolic networks and flow
A. Development of transgenic plants expressing IbMYB1a with high levels of anthocyanin accumulation
○ We identified IbMYB1a gene from the purple-fleshed sweetpotato (Ipomoea batatas L. cv. Sinzami). We generated transgenic Arabidopsis, tobacco, and alfalfa plants expressing the IbMYB1a gene under the control of CaMV 35S promoter, and the sweetpotato SPO and SWPA2 promoters. Overexpression of IbMYBa in transgenic plants (Arabidopsis, tobacco, alfalfa) produced enhanced anthocyanin pigmentation in leaves and stems of transgenic plants. In addition, HPLC analysis revealed that IbMYB1a expression led to the production of cyanidin-based anthocyanins in all transgenic plants, as occurs in the purple leaves of sweetpotato (cv. Sinzami). RT-PCR analysis showed that IbMYB1a expression induced up-regulation of several structural genes in the anthocyanin biosynthetic pathway. In particular, expression of IbMYB1a under the control of these three different promoters led to a remarkable variation in anthocyanin pigmentation in tobacco leaves. The anthocyanin contents of the leaves of the SPO-IbMYB1a-OX (SPO-M) line were higher than those of the SWPA2-IbMYB1a-OX (SPA-M) and 35S-IbMYB1a-OX (35S-M) lines. High levels of anthocyanin pigments negatively affected plant growth in the SPO-M lines, resulting delayed growth and, occasionally, a stunted phenotype. Our results indicate that IbMYB1a positively controls the expression of multiple anthocyanin biosynthetic genes and anthocyanin accumulation in heterologous plants.
B. Development of transgenic plants with enhanced resveratrol derivatives by cross-pollinating 35S-STS-OX lines to IbMYB1a-OX transgenic plants with high levels of anyhocyanin accumulation
○ For production of stilbene compounds by use the STS and ROMT genes, we previously generated transgenic plants (Arabidopsis, tobacco) expressing the RpSTS and VrROMT genes under the control of 35S promoter. By HPLC and LC-MS analysis, we found the low-level production of trans-resveratrol or trans-piceid in 35S-STS-OX and 35S-ROST-OX transgenic both Arabidopsis and tobacco plants. Thus, to improve the production of resveratrol derivatives in plants, we generated transgenic pollination plants (F1, F2) by cross-pollinating the 35S-STS-OX (35S-S) or 35S-ROST-OX (35S-RS) plant (♀) with the SPO/SWPA2-IbMYB1a-OX (SPO-M or SPA-M) transgenic tobacco plants (♂). Cross-pollinated plants (F1) were initially selected on MS media supplemented with kanamycin and basta antibiotics, and then they were screened by checking anthocyanin accumulation in the leaves of transgenic plants. Western blot analysis suggested that (35S-S or 35S-RS) x SPO-M cross-pollinated plants (F1) exhibited higher levels of RpSTS transgene expression than (35S-S or 35S-RS) x SPA-M. This result may be resulted from the higher content of anthocyanin pigments in SPO-M than SPA-M lines. We found that 35S-S x SPO/SPA-M cross-pollinated plants exhibited increased flower color (pink) compared to 35S-S and 35S-RS plants (light pink) but reduced flower color compared to SPO-M and SPA-M plants (dark pink). In leaves, 35S-S x SPO/SPA-M cross-pollinated plants showed decreased accumulation of anthocyanin pigments compared to SPO-M and SPA-M plants. Furthermore, by HPLC and LC-MS analysis, we found that 35S-S x SPO/SPA-M cross-pollinated plants (F2) produced significantly increased production of resveratrol derivatives (trans-piceid, cis-piceid, piceid methyl ether, resveratrol methyl ether O-hexoside, etc) in leaves, stems, flowers, and roots. These results suggest that cross-polination of STS-OX plants with IbMYB1a-OX could increase metobolic flow (metabolic precursors) into stilbenoid biosynthesis thanks to IbMYB1a expression and thus induce enhanced production of resveratrol derivatives. In deed, we noted that up-regulation of phenylpropanoid biosynthetic genes such as PAL and C4H was observed in 35S-S x SPO/SPA-M cross-pollinated tobacco plants.
C. Expression analysis of structural genes and its regulatory MYB genes in isoflavonoid biosynthetic pathways by RNA-seq and RT-PCR using 2~3-month-old soybean plants treated with ethephon
○ In cooperation with the 1st subproject group (Dr. Park), we found that ethephon application stimulated high levels of isoflavones in the leaves, such as daidzin, genistin, malonyldaidzin, and malonylgenistin. Based on this result, we attempted to isolate key regulatory transcription factors (MYB) controlling isoflavonoid biosynthetic pathways in soybean. By RNA-seq and RT-PCR analysis, we confirmed that ethephon application on soybean plants resulted in increased expression levels of isoflavone biosynthetic genes, such as CHS, CHI , IFS, FMaT, and F7GT. Moreover, six candidate MYB genes (GmMYB12a, GmMYB75, GmMYB84, GmMYB108, GmMYB140, GmMYB156) were also induced by treatment of ethephon. We identified six MYB genes using homology-based RT-PCR from soybean leaves treated with ethephon. We are currently generating transgenic Arabidopsis and soybean plants to find key regulatory MYB genes involved in isoflavonoid biosynthetic pathways of soybean.
5. Development of useful functional materials using BNIT fusion technology
○ A new multi-functional nanobiohybrid catalysts have been synthesized by combinding arylesterase and platinum nanoparticles. We demonstrated the efficacy of this catalyst by proving that this can be effectively used for the synthesis of paracetamol, an anti-inflammatory drug.
○ To explore the plant metabolites that induce stem cell differentiation, we develop cell based reporter assay system using p19 cells. Using this system, we identify the several pant metabolites which showed the activity of stem cell differentiation into cardiomyocytes.
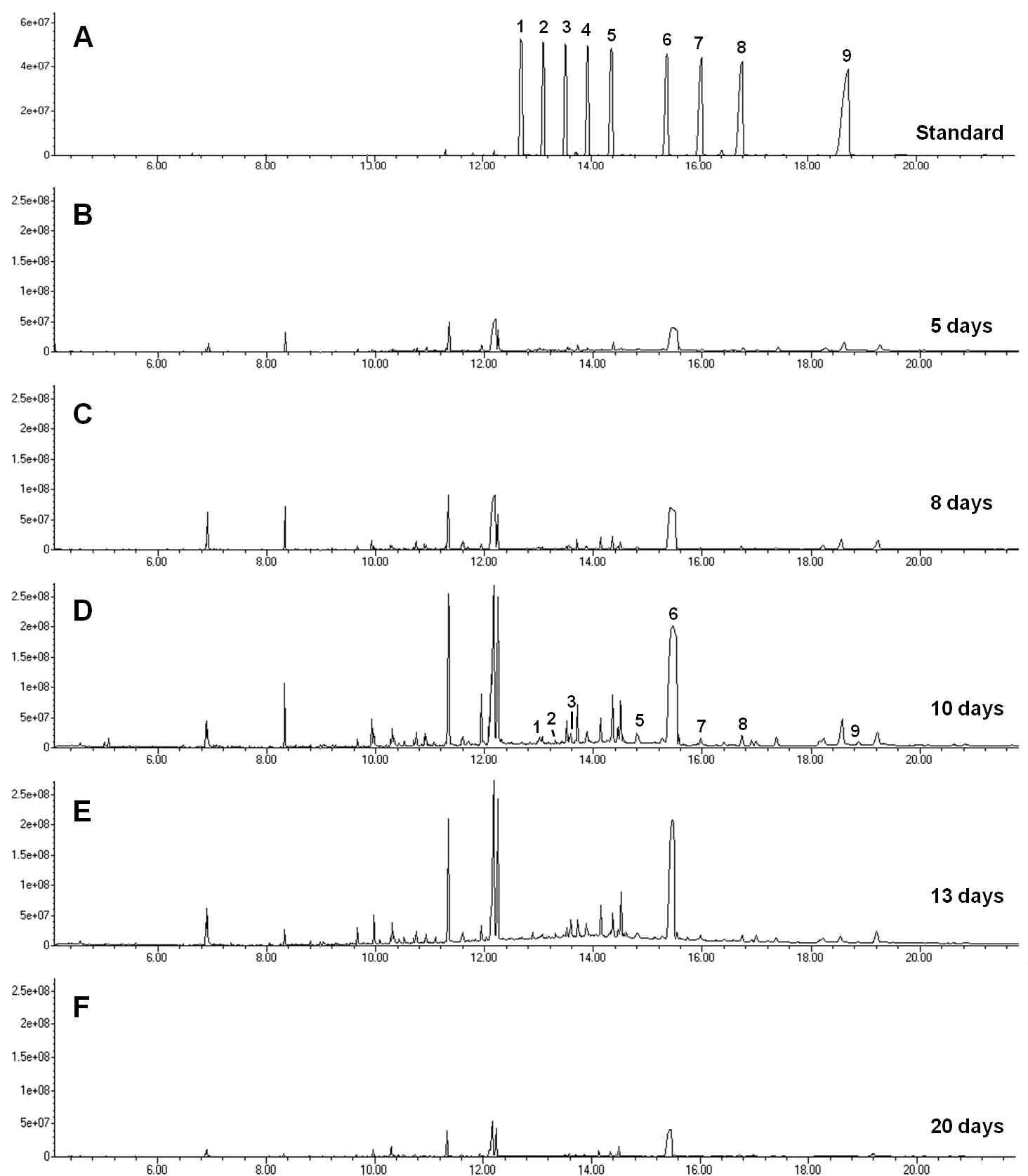 표
Total ion chromatogram (TIC) generated using gas chromatography with single quadrupole mass system (A) authentic policosanols-TMS derivatives, Peaks: 1, C20; 2, C21; 3, C22; 4, C23; 5, C24; 6, C26; 7, C27; 8, C28; and 9, C30. (B–F) TMS derivatized extracts of barley sprouts (B, extract of 5 days; C, extract of 8 days; D, extract of 10 days; E, extract of 13 days; F, extract of 20 days, respectively).
표
Total ion chromatogram (TIC) generated using gas chromatography with single quadrupole mass system (A) authentic policosanols-TMS derivatives, Peaks: 1, C20; 2, C21; 3, C22; 4, C23; 5, C24; 6, C26; 7, C27; 8, C28; and 9, C30. (B–F) TMS derivatized extracts of barley sprouts (B, extract of 5 days; C, extract of 8 days; D, extract of 10 days; E, extract of 13 days; F, extract of 20 days, respectively).
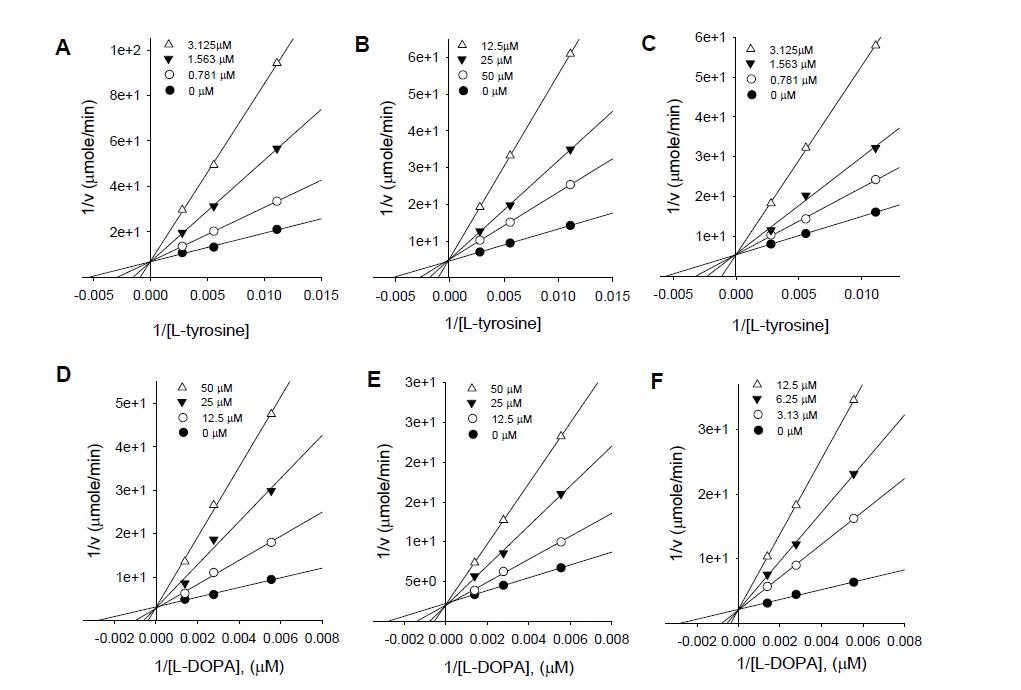 표
Lineweaver-Burk plots for the inhibition of the monophenolase and diphenolase activitiesof tyrosinase by compounds 1, 2, 3. In the presence of different concentrations of compounds for curves from bottom to top were (A) for monophenolase of 1;(B) for monophenolase of 2;(C) for monophenolase of 3;(D) for diphenolase of 1;(E) for diphenolase of 2;(F) for diphenolase of 3.
표
Lineweaver-Burk plots for the inhibition of the monophenolase and diphenolase activitiesof tyrosinase by compounds 1, 2, 3. In the presence of different concentrations of compounds for curves from bottom to top were (A) for monophenolase of 1;(B) for monophenolase of 2;(C) for monophenolase of 3;(D) for diphenolase of 1;(E) for diphenolase of 2;(F) for diphenolase of 3.
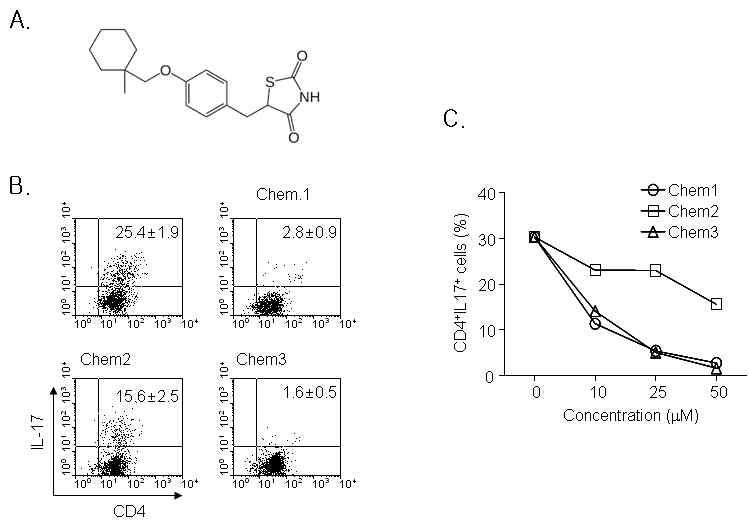 표
PPARg ligands inhibts Th17 cells differentiation (A) Structure of Chem 1. Naïve CD4+ Tcells were purified anddifferentiated into Th17 cells with or without 25mM of ciglitazone, rosiglitazone, and troglitazone. After 4 days, IL-17 producing CD4+ were analyzed using FACS. (B) Data from IL-17-producing cells with various concentrations of PPARg ligands was shown. One-way ANOVA was used for statistical analysis (p<0.01).
표
PPARg ligands inhibts Th17 cells differentiation (A) Structure of Chem 1. Naïve CD4+ Tcells were purified anddifferentiated into Th17 cells with or without 25mM of ciglitazone, rosiglitazone, and troglitazone. After 4 days, IL-17 producing CD4+ were analyzed using FACS. (B) Data from IL-17-producing cells with various concentrations of PPARg ligands was shown. One-way ANOVA was used for statistical analysis (p<0.01).
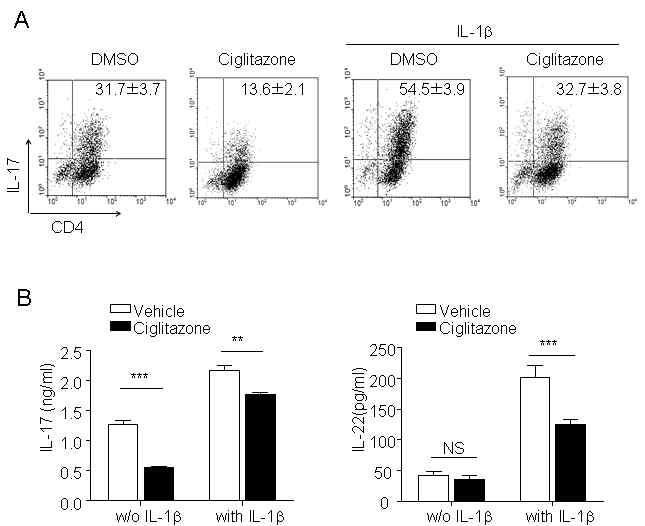 표
Ciglitazone inhibited the enhancement of Th17 differentiation induced by IL-1b. Naïve CD4+ T cells were differentiated to Th17 in the presence or absence of IL-1b for 4 days. To test whether PPARg ligand inhibits IL-1b-mediated Th17 differentiation, 25 mM ciglitazone was added at the differentiation medium. On day 4, cells were harvested for CD4 and IL-17 staining (A), and cell supernatant was used for determination of IL-17 and IL-22 using ELISA (B). Statistically significant differences are indicated by asterisks (**, p<0.01; ***, p<0.001).
표
Ciglitazone inhibited the enhancement of Th17 differentiation induced by IL-1b. Naïve CD4+ T cells were differentiated to Th17 in the presence or absence of IL-1b for 4 days. To test whether PPARg ligand inhibits IL-1b-mediated Th17 differentiation, 25 mM ciglitazone was added at the differentiation medium. On day 4, cells were harvested for CD4 and IL-17 staining (A), and cell supernatant was used for determination of IL-17 and IL-22 using ELISA (B). Statistically significant differences are indicated by asterisks (**, p<0.01; ***, p<0.001).
 표
Total ion chromatogram (TIC) generated using gas chromatography with single quadrupole mass system (A) authentic policosanols-TMS derivatives, Peaks: 1, C20; 2, C21; 3, C22; 4, C23; 5, C24; 6, C26; 7, C27; 8, C28; and 9, C30. (B–F) TMS derivatized extracts of barley sprouts (B, extract of 5 days; C, extract of 8 days; D, extract of 10 days; E, extract of 13 days; F, extract of 20 days, respectively).
표
Total ion chromatogram (TIC) generated using gas chromatography with single quadrupole mass system (A) authentic policosanols-TMS derivatives, Peaks: 1, C20; 2, C21; 3, C22; 4, C23; 5, C24; 6, C26; 7, C27; 8, C28; and 9, C30. (B–F) TMS derivatized extracts of barley sprouts (B, extract of 5 days; C, extract of 8 days; D, extract of 10 days; E, extract of 13 days; F, extract of 20 days, respectively).
 표
Lineweaver-Burk plots for the inhibition of the monophenolase and diphenolase activitiesof tyrosinase by compounds 1, 2, 3. In the presence of different concentrations of compounds for curves from bottom to top were (A) for monophenolase of 1;(B) for monophenolase of 2;(C) for monophenolase of 3;(D) for diphenolase of 1;(E) for diphenolase of 2;(F) for diphenolase of 3.
표
Lineweaver-Burk plots for the inhibition of the monophenolase and diphenolase activitiesof tyrosinase by compounds 1, 2, 3. In the presence of different concentrations of compounds for curves from bottom to top were (A) for monophenolase of 1;(B) for monophenolase of 2;(C) for monophenolase of 3;(D) for diphenolase of 1;(E) for diphenolase of 2;(F) for diphenolase of 3.
 표
PPARg ligands inhibts Th17 cells differentiation (A) Structure of Chem 1. Naïve CD4+ Tcells were purified anddifferentiated into Th17 cells with or without 25mM of ciglitazone, rosiglitazone, and troglitazone. After 4 days, IL-17 producing CD4+ were analyzed using FACS. (B) Data from IL-17-producing cells with various concentrations of PPARg ligands was shown. One-way ANOVA was used for statistical analysis (p<0.01).
표
PPARg ligands inhibts Th17 cells differentiation (A) Structure of Chem 1. Naïve CD4+ Tcells were purified anddifferentiated into Th17 cells with or without 25mM of ciglitazone, rosiglitazone, and troglitazone. After 4 days, IL-17 producing CD4+ were analyzed using FACS. (B) Data from IL-17-producing cells with various concentrations of PPARg ligands was shown. One-way ANOVA was used for statistical analysis (p<0.01).
 표
Ciglitazone inhibited the enhancement of Th17 differentiation induced by IL-1b. Naïve CD4+ T cells were differentiated to Th17 in the presence or absence of IL-1b for 4 days. To test whether PPARg ligand inhibits IL-1b-mediated Th17 differentiation, 25 mM ciglitazone was added at the differentiation medium. On day 4, cells were harvested for CD4 and IL-17 staining (A), and cell supernatant was used for determination of IL-17 and IL-22 using ELISA (B). Statistically significant differences are indicated by asterisks (**, p<0.01; ***, p<0.001).
표
Ciglitazone inhibited the enhancement of Th17 differentiation induced by IL-1b. Naïve CD4+ T cells were differentiated to Th17 in the presence or absence of IL-1b for 4 days. To test whether PPARg ligand inhibits IL-1b-mediated Th17 differentiation, 25 mM ciglitazone was added at the differentiation medium. On day 4, cells were harvested for CD4 and IL-17 staining (A), and cell supernatant was used for determination of IL-17 and IL-22 using ELISA (B). Statistically significant differences are indicated by asterisks (**, p<0.01; ***, p<0.001).
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.