최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 충북대학교 Chungbuk National University |
|---|---|
| 연구책임자 | 조용구 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2017-11 |
| 과제시작연도 | 2016 |
| 주관부처 | 미래창조과학부 Ministry of Science, ICT and Future Planning |
| 등록번호 | TRKO202000007428 |
| 과제고유번호 | 1711043231 |
| 사업명 | 개인연구지원 |
| DB 구축일자 | 2020-09-19 |
| 키워드 | 벼.흰잎마름병.PTI 엘리시터.시스테인 프로테아제.병저항성.병방어체계.Rice.Xanthomonas oryzae.PTI-eilicitor.Cysteine protease.Disease resistance.Defense system. |
□ 연구의 목적 및 내용
식물 병 저항성 기작에 관여하는 PTI-elicitor와 Cysteine protease의 역할을 밝히고, PTI-elicitor와 Cysteine protease에 의하여 유도되는 기주식물체의 defense system의 작용기작의 규명을 통하여 병에 대한 저항성 능력이 우수한 유전자를 발굴하고자 한다.
○ 식물 면역 신호전달에 의한 식물 병 저항성 유전자 발현네트워크 구명
1) 벼 흰잎마름병에 반응하는 유전자 선발 및 발굴
- 벼 품종에 흰잎마름병원균 접종후 총전사체 분석
□ 연구의 목적 및 내용
식물 병 저항성 기작에 관여하는 PTI-elicitor와 Cysteine protease의 역할을 밝히고, PTI-elicitor와 Cysteine protease에 의하여 유도되는 기주식물체의 defense system의 작용기작의 규명을 통하여 병에 대한 저항성 능력이 우수한 유전자를 발굴하고자 한다.
○ 식물 면역 신호전달에 의한 식물 병 저항성 유전자 발현네트워크 구명
1) 벼 흰잎마름병에 반응하는 유전자 선발 및 발굴
- 벼 품종에 흰잎마름병원균 접종후 총전사체 분석
- CP 유전자와 세균병원균 접종시 상호작용하는 유전자의 발현연구
- 벼 흰잎마름병에 의한 총전사체 분석결과 CP 유전자와 반응하는 R-gene의 발굴
- Pathogen effector 유전자 선발 및 클로닝
- Cysteine protease 유전자와 pathogen effector 유전자의 관련성 규명
2) Cysteine protease (CP) 과발현 형질전환체 저항성 검정
- 벼로부터 Cysteine protease 유전자 분리 및 형질전환체 생산
- CP 유전자 과발현 형질전환벼의 세균병원균 접종 및 저항성 검정
- 병원균 접종시 나타나는 생리적인 반응 분석
- CP 과발현 형질전환 벼의 biotic & abiotic stress 저항성 검정
3) CP 유전자와 신호전달에 상호작용하는 유전자의 발현 연구
- Yeast two hybrid system을 이용한 CP 단백질의 binding partner 탐색
- CP 단백질과 결합하는 단백질 분리 및 유전자분리
- Cysteine protease와 Pathogen effector 유전자와 상호작용 반응 분석
- 벼 흰잎마름병에 반응하는 신호전달 관련 유전자 작용기작 규명
- CP유전자 형질전환 계통을 이용하여 병원균 접종시 나타나는 ROS, R-gene, cell degradation 연구를 통해 저항성 기작 연구
- CP 유전자와 저항성 유전자간의 반응 분석을 통해 저항성 기작의 통합 분석
- 분리된 CP 결합 단백질의 pathogen-defense 시스템에서의 역할 구명
- R-gene과 CP 결합 단백질과의 상호작용 분석
□ 연구결과
식물체에서 Cysteine protease 및 PTI-elicitor에 관련된 면역체계 신호전달에 의한 병저항성 유전자의 실험적 네트워크의 확인
본 연구는 Xanthomonas oryzae pv. oryzae pathosystem과 관련하여 면역체계 네트워크를 총 병원균 인식, 분자적 신호, 저항성 도출 등으로 분류하여 벼에서의 기능 및 벼에서의 Brassica rapa cysteine protease를 조사하기 위하여 수행하였으며 그 성과는 다음과 같다.
1)Xoo의 K2 균계에 대한 감수성 및 저항성 품종의 상대적인 transcriptome 조사 - 저항성 품종에서 감수성 품종보다 3배 높은 1,259개의 DEGs을 발견하여 그 중 매우 높은 발현률을 나타낸 13개 DEGs들을 벼에서의 기능분석을 위하여 선발하여 유전자를 클로닝하였음.
2) 벼에서 K2-DEGs의 과발현 및 기능 분석 – 13 개 유전자의 cDNA를 pCAMBIA1300 binary vector에 삽입하였으며, Agrobacterium 형질전환법에 의하여 동진벼에 형질전환하여 흰잎마름병 K2균계에 대한 저항성 검정을 실시한 결과 13개 과발현체중 7개에서 저항성을 나타냄.
3)벼 및 Brassica rapa에서의 cysteine 및 serine proteases의 과발현과 기능 분석
-벼 proteases 4개와 Brassica rapa proteases 2개의 연관분석 결과, OsCP2와 BrCP1(67.6%) 사이에서 가장 높은 연관성을 보였고, OsCP4와 BrCP3(9.5%), OsCP4와 BrCP1(9.9%) 사이에 낮은 연관성 보임.
-벼 유래 4개 CP 유전자의 형질전환벼를 흰잎마름병 K3a 균계로 저항성 검정 결과 벼에서 OsCP2에서 2개, OsCP3에서 13개, OsCP4에서 26개, OsCP5에서 9개가 저항성이 확인됨.
-배추유래 2개 CP유전자의형질전환벼에서는 BrCP1에서47개, BrCP3에서 55개계통이저항성을 나타내었음.
4)Cysteine protease 유전자의 분자결합체 확인
-후보 CP 및 K2-DEGs의 분자결합체 확인을 위해 Yeast Two-Hybrid 분석을 진행중에 있으며 CP (OsCP2, 3, 4, 5)의 FL-cDNA을 포함하는 Y2H binding domain 및 선발된 K2-DEGs(E2, F2, G1, K2, L1, N1, O3)를 수행중.
-결합체 유전자에대한 up/downstream을 확인하기위해서,흰잎마름병에 감염된 어린잎으로부터 cDNA library를 합성하였고 activation domain에 결합 분석.
5)Cysteine protease (CP) 발현에 관련된 유전자 동정 및 기능 분석 검정
-Xoo effector oprO, hrpX, fruA, frlC, gumC KO 변이체의 실험에서 hrpX와 gumC effector가 흰잎마름병균의 발병에 밀접한 연관이 있음을 확인함.
6) 벼 흰잎마름병에 반응하는 신호전달 관련 유전자 작용기작 규명
-High DEG 유전자를 과발현시킨 형질전환 벼에서 wild type인 동진벼에 비하여 ROS 함량이 2배 이상 높아서 PCD 반응을 신속히 일으켜서 벼식물체가 저항성을 갖게 되는 것으로 판단됨.
-또한, ROS는 신호전달에도 작용할 것으로 생각됨.
7) 분리한 CP 단백질의 binding partner와 R-gene의 상호작용 검정
-벼 흰잎마름병균에 반응하는 유전자들을 과발현시킨 벼 식물체에 Xoo 병원균을 접종했더니 sPR1a, OsPR5, OPPR10등 PR gene들의 전사가 증가되었고, 그 중에서 LOC_Os01g45640.1 유전자가 과발현된 벼에서 지속적으로 발현이 높았다.
-LOC_Os08g26230.4와LOC_Os09g04310.1유전자는 최소한 2개의 PR gene에 높은 발현을 나타냈다. 이것은 Xoo 병원균이 침입할 때에 이들 DEG 유전자들이 신호를 PR gene이 있는 downstream으로 전달을 매개하여 일어나는 반응으로 생각된다.
□ 연구결과의 활용계획
식물과 병원균에서 유래된 PTI-elicitor와 cysteine protease를 이용한 면역 신호전달에 의한 벼 흰잎마름병균 저항성 유전자의 발현양상을 조사하고 병원균과 기주와의 분자상호반응 기구와 병저항성 유전자 발현 네트워크를 구명하여, 병 저항성 유전자를 감수성 품종의 벼에 형질전환하여 병 저항성 증진효과를 본다면 병 저항성 벼 창출에 따른 병 저항성 육종 소재로 활용 가능하며 체계적인 병 방제를 위한 유용한 자료로 활용이 가능하다. 특히 cysteine protease 형질전환체로부터 발현이 조절되는 병 저항성 유전자를 분리하여 분자 수준의 기능적 역할 분석을 통해 병 저항성 기작에 대한 포괄적 분석이 가능할 것이다. 또한, Cysteine protease를 포함한 병저항성 유용유전자들의 과발현 형질전환체를 이용해 세균병원균,진균병원균에 복합내병성 작물의 육성으로 내병성 고품질벼의 개발이 가능해질 것이다.
(출처 : 연구결과 요약문 4p)
□ Purpose& contents
The purposes of this research are to identify the active functions of PTI-elicitors and cysteine proteases and their relationships in the expression of disease resistance in rice against Xanthomonas oryzae and to isolate the useful resistance genes that lead to attain the dura
□ Purpose& contents
The purposes of this research are to identify the active functions of PTI-elicitors and cysteine proteases and their relationships in the expression of disease resistance in rice against Xanthomonas oryzae and to isolate the useful resistance genes that lead to attain the durable resistance to bacterial diseases through understanding of the defense mechanism in host plants induced by PTI-elicitors and cysteine proteases.
○ Identification of expression network of disease resistance genes by immune signaling in plants
1) Identification and selection of gene in response to Xanthomonas oryzae pv. oryzae
- Analysis of total transcriptome after pathogen infection in rice cultivars
- Study spatio-temporal expression of K2-DEGs in rice in response to Xoo infection
- Determination of R-gene reaction and function against infection of Xoo
- Isolation and cloning of pathogen effector gene
- Investigation of relationship between cysteine protease gene and pathogen effector gene
2) Examination of resistance in cysteine protease-RNAi and overexpression transgenic lines
- Isolation of cysteine protease genes in rice and production of transgenic line
- Resistance examination and pathogen innoculation in CP-RNAi and overexpression plants
- Analysis of physical interaction after pathogen infection
- Identification of biotic & abiotic stress resistance in CP overexpression transgenic lines
3) Functional and transcriptional analysis of CP-mediated resistance in rice against Xoo
- Identification of rice CP with high resistance to Xoo
- Transcriptomic analysis of resistance in CP overexpression plants
- Identification of enriched gene functions in CP-OX plants
- Analysis of resistance mechanisms through ROS, R gene, HR using CP transgenic lines in pathogen infection
- Integration analysis of resistance mechanism through CP gene and resistance gene
- Identification of defense-related and signal transduction signaling-related genes
- Analysis of interaction between R-gene and CP binding protein
□ Result
o Identification of expression network of disease resistance genes by immune signaling related to cysteine protease and PTI-elicitor in plants
This study is carried out to investigate the functions of rice and Brassica rapa cysteine proteases under rice – Xanthomonas oryzae pv. oryzae pathosystem, with a specific objective to implicate them in the three nodes of immunity network: pathogen perception, molecular signaling, and execution of resistance.
1)Comparative transcriptome analysis of susceptible and resistant rice cultivars in response to Xanthomonas oryzae pv. oryzae
- cDNA microarray revealed 1259 DEGs in resistant cultivar which is three-fold higher than the susceptible cultivar. Thirteen DEGs with the highest expression levels were identified and selected for functional analysis in rice.
2) Overexpression and functional analysis of K2-induced DEGs (K2-DEGs) in rice
– The full-length cDNA of selected putative genes were cloned into binary vector pCAMBIA1300. A total of 13 vector constructs were transformed into rice cultivar Dongjinbyeo by Agrobacterium transformation method. Promising lines showing resistance to the pathogen were identified in 7 out of 13 overexpression transgenes in rice.
- Levels of H2O2 were significantly higher in seven transgenic plants including; F2, O3, N1, K2, L2, I1, and E2.
- Transcripts level of marker genes such as pathogenesis-related and probenazole-inducible 1 were induiced by Xoo infection in O3, G1, E2, and N1 plants.
3)Overexpression and functional analysis of cysteine and serine proteases in rice and Brassica rapa
- Phylogenetic analysis of four rice proteases and two Brassica rapa proteases revealed distant relationship between each other. The closest similarity was found between OsCP2 and BrCP1 (67.6%) and lowest identity was noted between OsCP4 and BrCP3 (9.5%), and between OsCP4 and BrCP1 (9.9%).
-T0 plants were established in the field and screened for resistance against Xoo strain K3a. The number of resistant plants identified for each CP overexpression is: 2 in OsCP2, 13 in OsCP3, 26 in OsSP4, and 9 in OsCP5, 47 in BrCP1 and 55 in BrCP3.
-T0 RNAi plants were generated and established in the field. FIve plants were highly susceptible to K3a more than the wild type.
-T0 CP-OX plants were screened in the field. The number of plants with moderate to high resistance was 9 in BrCP1, 15 in BrCP3, 4 in OsCP2, 17 in OsSP4, 9 in OsCP5, and 8 in OsCP3.
4)Identification of molecular binding partner of cysteine protease genes
-To determine the possible molecular binding partner of any of the candidate CP and K2-DEGs, we are currently doing the Yeast Two-Hybrid system. A Y2H binding domain containing the FL-cDNA of CP (OsCP2, 3, 4, and 5) and selected K2-DEGs (E2, F2, G1, K2, L1, N1, and O3) are currently being constructed.
-To identify possible up/downstream binding partner genes, cDNA library from Xoo-infected fresh leaves of rice was synthesized and will be ligated into the activation domain.
5)Identification and functional analysis of cysteine protease (CP) expression
6)Identification of signal transduction-related gene action mechanisms in response to rice leaf blight
7)Expression of OsCP3 peaked at 30 minutes post-inoculation. Samples for RNA-seq were prepared using this time point.
- The numbers of differentially expressed genes (DEGs) were higher in the OsCP3-OX plants than in wild type Dongjin and the DEG frequency is higher at inoculated than in mock control.
- Comparison between the two genotypes revealed high number of overlapping genes (607) at 30 minutes post-inoculation.
- Most of the defense-related and signal transduction-related genes were expressed higher in CP3-OX than in wild type plants.
□ Expected Contribution
This project will give knowledge about the expression of bacterial blight resistance genes by immune signaling using PTI-elicitor and cysteine protease derived from plants and pathogens. The study of intermolecular reaction mechanism and disease resistant gene expression network between pathogen and host plants will generate data for systematic disease control system and produce disease-resistant breeding materials. Isolation of disease resistance genes regulated from cysteine protease overexpression lines will give a comprehensive analysis about the disease resistance mechanism at molecular level. Lastly, by breeding complex disease resistant varieties using cysteine protease overexpression transgenic lines will enable breeders to develop varieties with broad spectrum resistance.
(출처 : SUMMARY 5p)
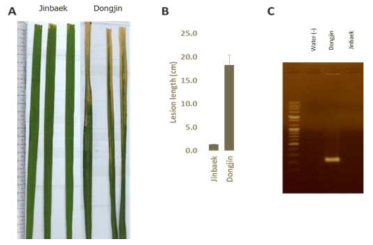 표
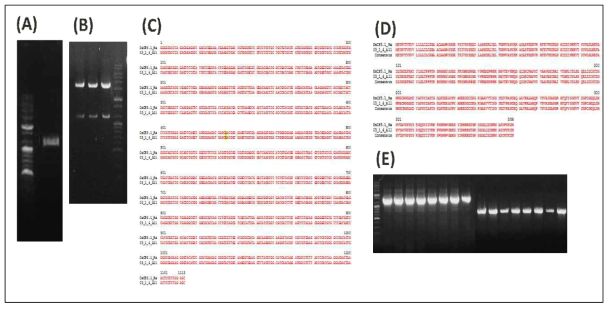
Resistance reaction of Jinbaek and Dongjin to Xoo isolate K2 infection. A) Brown lesions exhibited in the inoculated leaves of Jinbaek and Dongjin . B) Lesion length taken 14 days post-inoculation with 1x105cfu/mlofK2isolate.C) PCR detection of Xoo in the leaves of Jinbaek and Dongjin 5 days post-inoculation. Water, mock; Dongjin, susceptible; Jinbaek, resistant
표
Resistance reaction of Jinbaek and Dongjin to Xoo isolate K2 infection. A) Brown lesions exhibited in the inoculated leaves of Jinbaek and Dongjin . B) Lesion length taken 14 days post-inoculation with 1x105cfu/mlofK2isolate.C) PCR detection of Xoo in the leaves of Jinbaek and Dongjin 5 days post-inoculation. Water, mock; Dongjin, susceptible; Jinbaek, resistant
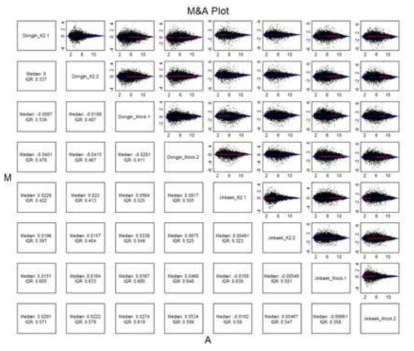 표
Basic statistics used in microarray analysis. All samples locate in diagonal of M&A plot and all pairs between each samples is represented in the upper and lower directions of the diagonal such as coordinate. The upper right of the diagonal is a plot, and the lower left of the diagonal is median and IQR value. Y axis: ‘M (log2 ratio)’ = log2(Sample-A/Sample-B), X Axis : ‘A (Log2 average)’ = (log2(sample-A/Sample-B))/2. Points of which log2 ratio (M=Y axis value) Is out of range (-1,1) indicates probes having more than 2-fold change between Sample A and Sample B
표
Basic statistics used in microarray analysis. All samples locate in diagonal of M&A plot and all pairs between each samples is represented in the upper and lower directions of the diagonal such as coordinate. The upper right of the diagonal is a plot, and the lower left of the diagonal is median and IQR value. Y axis: ‘M (log2 ratio)’ = log2(Sample-A/Sample-B), X Axis : ‘A (Log2 average)’ = (log2(sample-A/Sample-B))/2. Points of which log2 ratio (M=Y axis value) Is out of range (-1,1) indicates probes having more than 2-fold change between Sample A and Sample B
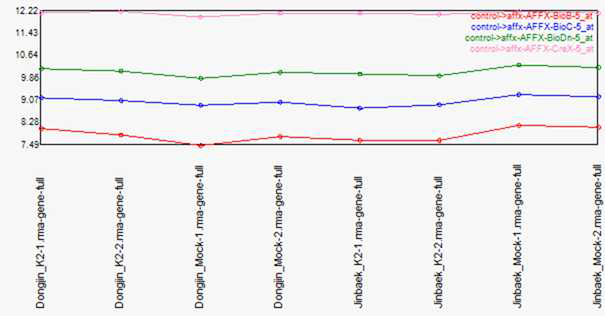 표
Hybridization control probe (bio B, C, Dn, Crex). Intensity order such as BioB , BioC , BioDn , Crex represents desirable Hybridization in this experiment. In general, Bio B, C, Dn, Crex probes are used to confirm that experiment was performed normally by mixing with samples for each concentration
표
Hybridization control probe (bio B, C, Dn, Crex). Intensity order such as BioB , BioC , BioDn , Crex represents desirable Hybridization in this experiment. In general, Bio B, C, Dn, Crex probes are used to confirm that experiment was performed normally by mixing with samples for each concentration
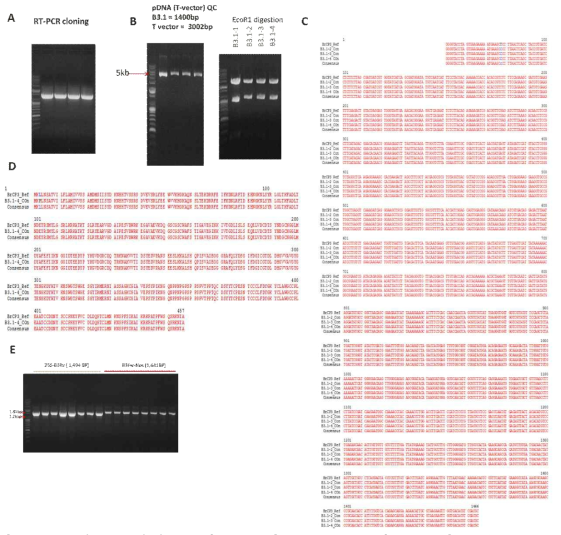
 표
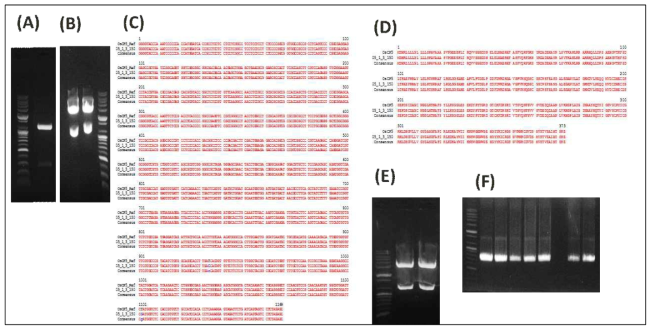
Isolation and cloning of BrCP1. A) RT-PCR assay of BrCP1. B) Restriction enzyme mapping to verify ligation of BrCP1 into T-vector. C) 100% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) Double enzyme digestion of pDNA containing BrCP1 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony assayed with HPT (internal) primer
표
Isolation and cloning of BrCP1. A) RT-PCR assay of BrCP1. B) Restriction enzyme mapping to verify ligation of BrCP1 into T-vector. C) 100% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) Double enzyme digestion of pDNA containing BrCP1 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony assayed with HPT (internal) primer
 표
Isolation and cloning of BrCP3. A) RT-PCR assay of BrCP3. B) Restriction enzyme mapping to verify ligation of BrCP3 into T-vector. C) 99.92% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) 99.78% amino acid sequence homology of BrCP3 with the reference gene seq. E) Transformed EHA105 colony PCR assayed with BrCP3 and HPT
표
Isolation and cloning of BrCP3. A) RT-PCR assay of BrCP3. B) Restriction enzyme mapping to verify ligation of BrCP3 into T-vector. C) 99.92% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) 99.78% amino acid sequence homology of BrCP3 with the reference gene seq. E) Transformed EHA105 colony PCR assayed with BrCP3 and HPT
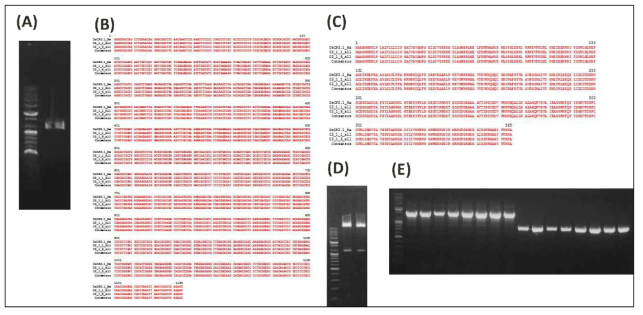 표
Isolation and cloning of OsCP2 gene. A) RT-PCR assay of OsCP2. B) Nucleotide sequence alignment of OsCP2 compared with the reference gene with 100% homology. C) 100% amino acid sequence homology of OsCP2 with the reference gene. D) Double enzyme digestion of pDNA containing OsCP2 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony PCR assayed with O2.1 and HPT
표
Isolation and cloning of OsCP2 gene. A) RT-PCR assay of OsCP2. B) Nucleotide sequence alignment of OsCP2 compared with the reference gene with 100% homology. C) 100% amino acid sequence homology of OsCP2 with the reference gene. D) Double enzyme digestion of pDNA containing OsCP2 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony PCR assayed with O2.1 and HPT
 표
Isolation and cloning of OsCP5 gene. A) RT-PCR assay of OsCP5. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of BrCP1 sample compared with the reference gene with 99.8289% hmology. D) 100% amino acid sequence homology of OsCP5 with the reference gene seq. E) Double enzyme digestion of pDNA containing OsCP5 as template for ligation to pHJ1 vector. F) Transformed EHA105 colony PCR assayed with HPT
표
Isolation and cloning of OsCP5 gene. A) RT-PCR assay of OsCP5. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of BrCP1 sample compared with the reference gene with 99.8289% hmology. D) 100% amino acid sequence homology of OsCP5 with the reference gene seq. E) Double enzyme digestion of pDNA containing OsCP5 as template for ligation to pHJ1 vector. F) Transformed EHA105 colony PCR assayed with HPT
 표
Isolation and cloning of OsCP3 gene. A) RT-PCR assay of OsCP3. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of OsCP3 compared with the reference gene with 99.9102% homology. D) 100% amino acid sequence homology of OsCP2 with the reference gene. E) Transformed EHA105 colony PCR assayed with O3.1 and HPT
표
Isolation and cloning of OsCP3 gene. A) RT-PCR assay of OsCP3. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of OsCP3 compared with the reference gene with 99.9102% homology. D) 100% amino acid sequence homology of OsCP2 with the reference gene. E) Transformed EHA105 colony PCR assayed with O3.1 and HPT
 표
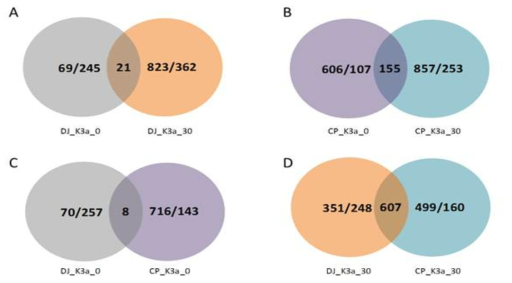
Venn diagram showing the number of up/down-regulated genes between Dongjin (WT) and OsCP3 at 0 and 30 minutes post-inoculation with Xanthomonas oryzae pv. oryzae race K3a. (A,B) Comparison of co-DEGs between 0 HPI and 30 min PI in Dongjin and OsCP3, respectively. (C,D) Comparison of CO-DEGs between two genotypes (Dongjin and OsCP3) at 0 HPI and 30 min PI, respectively. Overlapping portion indicates co-regulated genes
표
Venn diagram showing the number of up/down-regulated genes between Dongjin (WT) and OsCP3 at 0 and 30 minutes post-inoculation with Xanthomonas oryzae pv. oryzae race K3a. (A,B) Comparison of co-DEGs between 0 HPI and 30 min PI in Dongjin and OsCP3, respectively. (C,D) Comparison of CO-DEGs between two genotypes (Dongjin and OsCP3) at 0 HPI and 30 min PI, respectively. Overlapping portion indicates co-regulated genes
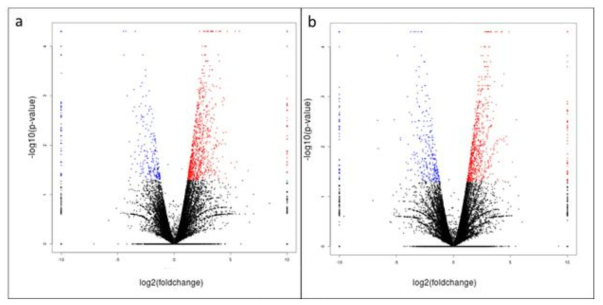 표
Transcriptome dynamics reveal large magnitude changes of gene regulation in resistant and susceptible genotypes – Xoo K3a interactions that are statistically significant. Volcano plots displaying meaningful fold change between two groups a. resistant genotype inoculated vs resistant genotype non-noculated (CP_K3a_30 vs CP_K3a_Mock) b. susceptible genotype inoculated vs susceptible genotype non-inoculated (DJ_K3a vs DJ_Mock). Y Axes indicate p<0.05 and x-axes indicate fold change (FC) following log2 scale. Differentially expressed genes (DEGs) are shown in blue, black, and red indicating meaningful down-regulated, no change, and up-regulated genes, respectively
표
Transcriptome dynamics reveal large magnitude changes of gene regulation in resistant and susceptible genotypes – Xoo K3a interactions that are statistically significant. Volcano plots displaying meaningful fold change between two groups a. resistant genotype inoculated vs resistant genotype non-noculated (CP_K3a_30 vs CP_K3a_Mock) b. susceptible genotype inoculated vs susceptible genotype non-inoculated (DJ_K3a vs DJ_Mock). Y Axes indicate p<0.05 and x-axes indicate fold change (FC) following log2 scale. Differentially expressed genes (DEGs) are shown in blue, black, and red indicating meaningful down-regulated, no change, and up-regulated genes, respectively
 표
Resistance reaction of Jinbaek and Dongjin to Xoo isolate K2 infection. A) Brown lesions exhibited in the inoculated leaves of Jinbaek and Dongjin . B) Lesion length taken 14 days post-inoculation with 1x105cfu/mlofK2isolate.C) PCR detection of Xoo in the leaves of Jinbaek and Dongjin 5 days post-inoculation. Water, mock; Dongjin, susceptible; Jinbaek, resistant
표
Resistance reaction of Jinbaek and Dongjin to Xoo isolate K2 infection. A) Brown lesions exhibited in the inoculated leaves of Jinbaek and Dongjin . B) Lesion length taken 14 days post-inoculation with 1x105cfu/mlofK2isolate.C) PCR detection of Xoo in the leaves of Jinbaek and Dongjin 5 days post-inoculation. Water, mock; Dongjin, susceptible; Jinbaek, resistant
 표
Basic statistics used in microarray analysis. All samples locate in diagonal of M&A plot and all pairs between each samples is represented in the upper and lower directions of the diagonal such as coordinate. The upper right of the diagonal is a plot, and the lower left of the diagonal is median and IQR value. Y axis: ‘M (log2 ratio)’ = log2(Sample-A/Sample-B), X Axis : ‘A (Log2 average)’ = (log2(sample-A/Sample-B))/2. Points of which log2 ratio (M=Y axis value) Is out of range (-1,1) indicates probes having more than 2-fold change between Sample A and Sample B
표
Basic statistics used in microarray analysis. All samples locate in diagonal of M&A plot and all pairs between each samples is represented in the upper and lower directions of the diagonal such as coordinate. The upper right of the diagonal is a plot, and the lower left of the diagonal is median and IQR value. Y axis: ‘M (log2 ratio)’ = log2(Sample-A/Sample-B), X Axis : ‘A (Log2 average)’ = (log2(sample-A/Sample-B))/2. Points of which log2 ratio (M=Y axis value) Is out of range (-1,1) indicates probes having more than 2-fold change between Sample A and Sample B
 표
Hybridization control probe (bio B, C, Dn, Crex). Intensity order such as BioB , BioC , BioDn , Crex represents desirable Hybridization in this experiment. In general, Bio B, C, Dn, Crex probes are used to confirm that experiment was performed normally by mixing with samples for each concentration
표
Hybridization control probe (bio B, C, Dn, Crex). Intensity order such as BioB , BioC , BioDn , Crex represents desirable Hybridization in this experiment. In general, Bio B, C, Dn, Crex probes are used to confirm that experiment was performed normally by mixing with samples for each concentration
 표
Isolation and cloning of BrCP1. A) RT-PCR assay of BrCP1. B) Restriction enzyme mapping to verify ligation of BrCP1 into T-vector. C) 100% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) Double enzyme digestion of pDNA containing BrCP1 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony assayed with HPT (internal) primer
표
Isolation and cloning of BrCP1. A) RT-PCR assay of BrCP1. B) Restriction enzyme mapping to verify ligation of BrCP1 into T-vector. C) 100% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) Double enzyme digestion of pDNA containing BrCP1 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony assayed with HPT (internal) primer
 표
Isolation and cloning of BrCP3. A) RT-PCR assay of BrCP3. B) Restriction enzyme mapping to verify ligation of BrCP3 into T-vector. C) 99.92% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) 99.78% amino acid sequence homology of BrCP3 with the reference gene seq. E) Transformed EHA105 colony PCR assayed with BrCP3 and HPT
표
Isolation and cloning of BrCP3. A) RT-PCR assay of BrCP3. B) Restriction enzyme mapping to verify ligation of BrCP3 into T-vector. C) 99.92% nucleotide sequence alignment of BrCP1 sample compared with the reference gene. D) 99.78% amino acid sequence homology of BrCP3 with the reference gene seq. E) Transformed EHA105 colony PCR assayed with BrCP3 and HPT
 표
Isolation and cloning of OsCP2 gene. A) RT-PCR assay of OsCP2. B) Nucleotide sequence alignment of OsCP2 compared with the reference gene with 100% homology. C) 100% amino acid sequence homology of OsCP2 with the reference gene. D) Double enzyme digestion of pDNA containing OsCP2 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony PCR assayed with O2.1 and HPT
표
Isolation and cloning of OsCP2 gene. A) RT-PCR assay of OsCP2. B) Nucleotide sequence alignment of OsCP2 compared with the reference gene with 100% homology. C) 100% amino acid sequence homology of OsCP2 with the reference gene. D) Double enzyme digestion of pDNA containing OsCP2 as template for ligation to pCAMBIA1300 (pHJ1) vector. E) Transformed EHA105 colony PCR assayed with O2.1 and HPT
 표
Isolation and cloning of OsCP5 gene. A) RT-PCR assay of OsCP5. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of BrCP1 sample compared with the reference gene with 99.8289% hmology. D) 100% amino acid sequence homology of OsCP5 with the reference gene seq. E) Double enzyme digestion of pDNA containing OsCP5 as template for ligation to pHJ1 vector. F) Transformed EHA105 colony PCR assayed with HPT
표
Isolation and cloning of OsCP5 gene. A) RT-PCR assay of OsCP5. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of BrCP1 sample compared with the reference gene with 99.8289% hmology. D) 100% amino acid sequence homology of OsCP5 with the reference gene seq. E) Double enzyme digestion of pDNA containing OsCP5 as template for ligation to pHJ1 vector. F) Transformed EHA105 colony PCR assayed with HPT
 표
Isolation and cloning of OsCP3 gene. A) RT-PCR assay of OsCP3. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of OsCP3 compared with the reference gene with 99.9102% homology. D) 100% amino acid sequence homology of OsCP2 with the reference gene. E) Transformed EHA105 colony PCR assayed with O3.1 and HPT
표
Isolation and cloning of OsCP3 gene. A) RT-PCR assay of OsCP3. B) Restriction enzyme mapping to verify ligation of OsCP5 into T-vector. C) Nucleotide sequence alignment of OsCP3 compared with the reference gene with 99.9102% homology. D) 100% amino acid sequence homology of OsCP2 with the reference gene. E) Transformed EHA105 colony PCR assayed with O3.1 and HPT
 표
Venn diagram showing the number of up/down-regulated genes between Dongjin (WT) and OsCP3 at 0 and 30 minutes post-inoculation with Xanthomonas oryzae pv. oryzae race K3a. (A,B) Comparison of co-DEGs between 0 HPI and 30 min PI in Dongjin and OsCP3, respectively. (C,D) Comparison of CO-DEGs between two genotypes (Dongjin and OsCP3) at 0 HPI and 30 min PI, respectively. Overlapping portion indicates co-regulated genes
표
Venn diagram showing the number of up/down-regulated genes between Dongjin (WT) and OsCP3 at 0 and 30 minutes post-inoculation with Xanthomonas oryzae pv. oryzae race K3a. (A,B) Comparison of co-DEGs between 0 HPI and 30 min PI in Dongjin and OsCP3, respectively. (C,D) Comparison of CO-DEGs between two genotypes (Dongjin and OsCP3) at 0 HPI and 30 min PI, respectively. Overlapping portion indicates co-regulated genes
 표
Transcriptome dynamics reveal large magnitude changes of gene regulation in resistant and susceptible genotypes – Xoo K3a interactions that are statistically significant. Volcano plots displaying meaningful fold change between two groups a. resistant genotype inoculated vs resistant genotype non-noculated (CP_K3a_30 vs CP_K3a_Mock) b. susceptible genotype inoculated vs susceptible genotype non-inoculated (DJ_K3a vs DJ_Mock). Y Axes indicate p<0.05 and x-axes indicate fold change (FC) following log2 scale. Differentially expressed genes (DEGs) are shown in blue, black, and red indicating meaningful down-regulated, no change, and up-regulated genes, respectively
표
Transcriptome dynamics reveal large magnitude changes of gene regulation in resistant and susceptible genotypes – Xoo K3a interactions that are statistically significant. Volcano plots displaying meaningful fold change between two groups a. resistant genotype inoculated vs resistant genotype non-noculated (CP_K3a_30 vs CP_K3a_Mock) b. susceptible genotype inoculated vs susceptible genotype non-inoculated (DJ_K3a vs DJ_Mock). Y Axes indicate p<0.05 and x-axes indicate fold change (FC) following log2 scale. Differentially expressed genes (DEGs) are shown in blue, black, and red indicating meaningful down-regulated, no change, and up-regulated genes, respectively
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.