최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 국립원예특작과학원 National Institute of Horticultural and Herbal Science |
|---|---|
| 연구책임자 | 허윤영 |
| 참여연구자 | 김수진 , 박서준 , 이동훈 , 임동준 , 최경옥 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2021-02 |
| 과제시작연도 | 2020 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO202100009593 |
| 과제고유번호 | 1395062845 |
| 사업명 | FTA대응경쟁력향상기술개발(R&D) |
| DB 구축일자 | 2021-09-18 |
| 키워드 | 위단위결과.종자발달.과립비대.발달유전체.유전자 네트워크.stenospermo-carpy.seed development.berry enlargement.developmental genomics.gene networks. |
- 위단위결과성 무핵 자방친을 이용한 배배양 기술을 확립하여 배배양 효율을 2.2%(’16)에서 10%(’20)까지 향상하고, 배배양 실생 2,918주 획득
- 유핵과 무핵 포도의 종자 및 종피 발달의 해부학적, 생화학적 특성 비교 완료하고 유핵과 무핵 포도의 종자발달 동안 종자 전사체의 차등발현 유전자의 분석 및 후보 유전자 선발을 통해 유핵과 무핵 포도를 구분할 수 있는 발현 마커 세트 개발과 선발지표의 기능을 검정함
- 위단위결과성 포도의 과립비대 유전자네트워크 분석 및 후보 유전자 선발
- 배발생캘러스를 이용
- 위단위결과성 무핵 자방친을 이용한 배배양 기술을 확립하여 배배양 효율을 2.2%(’16)에서 10%(’20)까지 향상하고, 배배양 실생 2,918주 획득
- 유핵과 무핵 포도의 종자 및 종피 발달의 해부학적, 생화학적 특성 비교 완료하고 유핵과 무핵 포도의 종자발달 동안 종자 전사체의 차등발현 유전자의 분석 및 후보 유전자 선발을 통해 유핵과 무핵 포도를 구분할 수 있는 발현 마커 세트 개발과 선발지표의 기능을 검정함
- 위단위결과성 포도의 과립비대 유전자네트워크 분석 및 후보 유전자 선발
- 배발생캘러스를 이용한 포도 식물체 형질전환 체계를 수립하고 포도 U6 프로모터를 이용한 고효율 유전자편집 체계 개발 및 실증
- 유핵, 무핵, 및 야생 근연종 포도 유전체를>37x mean depth까지 재분석한 high-depth resequencing data에서 고밀도 변이 데이터를 획득하고 열성 무핵 조절 유전자좌와 연관된 Vitvi01g00455, Vitvi08g01528, 및 Vitvi18g01237을 포함하는 신규 후보 원인 유전자를 예측하였으며 무핵 포도 육종 프로그램에서 사용이 가능한 allele-specific PCR marker를 이를 3점의 유전자에서 개발
(출처 : 요약서 3p)
Purpose&Contents
○ Development of breeding material with stenospermocarpic seedless and more than 8g of berry weight
○ Investigation of the mechanism of seed development and berry enlargement in stenospermocarpic grape
○ Analysis of genomic characteristics of stenospermocarpic seedless grap
Purpose&Contents
○ Development of breeding material with stenospermocarpic seedless and more than 8g of berry weight
○ Investigation of the mechanism of seed development and berry enlargement in stenospermocarpic grape
○ Analysis of genomic characteristics of stenospermocarpic seedless grape
Results
[1세부]
○ Establishment of embryo rescue method on grapevine to improve cultivation efficiency from 2.2% to 10% and acquire 2,918 grapes seedlings
○ Breeding elite lines TE-16-32-04 and TE-17-21-08 with seedless and more than 8g of berry weight
[1협동]
○ Completed anatomical and histochemical analysis of seeds and seed coats in seeded grapes and seedless grapes during development
○ Developed a set of qRT-PCR markers for selection of seedless grape and selection of differentially expressed genes via transcriptome analysis between seeds of seeded grape and those of stenospermocarpic grape during its developmental stages.
○ Produced transformants and cassettes to make specific genes of over
-expression, restoration, knock-out, and expression within cells to further study functions of genes related with seed development in grapes
[2협동]
○ mRNA-seq and network analysis identified group of genes related to berry development, and candidate genes for functional study were selected according to their expression characteristics and putative function
○ An efficient Agrobacterium tumefaciens-mediated transformation and plant regeneration system was developed using embryogenic callus lines of grapevines
○ The CRISPR/Cas9-mediated genome editing system was applied to grapevines where the promoters of the Vitis vinifera U6 small nuclear RNA genes were used for efficient transcription of guide RNAs in the transformed cells of grapevines
[3협동]
○ We collected dense variation data from high-depth resequencing data of seeded, seedless, and wild relative grape genomes sequenced to > 37x mean depth.
○ Variation data enabled us to confirm a dominant gene and identify recessive loci for seedlessness.
○ Incidentally, we found that grape cultivar Rizamat contains an ancestral chromosomal region of the dominant gene in Sultanina, a predominant seedlessness donor cultivar.
○ We predicted new candidate causal genes including Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the recessive seedless-regulating loci
○ We developed a allele-specific PCR marker from each of the three predicted genes for application in grape breeding for seedlessness.
Expected Contribution
○ Gene network and the list of candidate genes provide new insights into molecular mechanisms regulating seed and berry development of stenospermocarpic grape
○ With significant efficiency, the plant transformation/regeneration and CRISPR/Cas9-mediated genome editing systems for grapevine developed in this study will contribute to biology as well as the breeding of stenospermocarpic grape
○ This study provides fundamental insights relevant to variant calling from genome resequencing data of diverse interspecific hybrid germplasms such as grape.
○ Thus, The results of this study will be of great value both to grape breeders who are striving to more effectively harness haplotype variation at seedless-regulating loci to develop superior seedless grape cultivars and to genome researchers in general.
(출처 : Summary 5p)
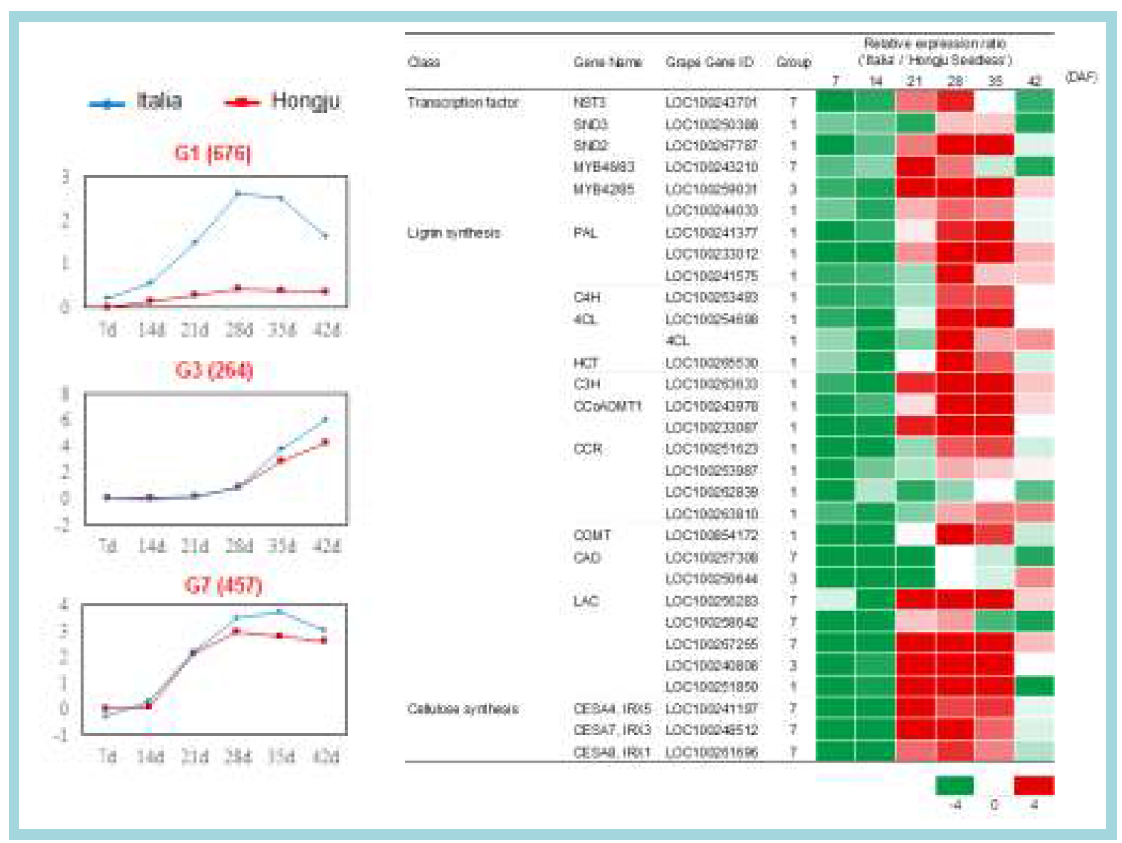 표
군집분석 결과, ‘Hongju Seedless’에서 보다 ‘Italia’ 에서 더 많이 발현되는 전사체 그룹(좌)과 리그닌 생합성관련 유전자의 발현양(우). 그룹1, 그룹3, 그룹7 (괄호 속 숫자는 그룹에 속하는 유전자 수)와 이들 중 리그닌 생합성 및 조절 유전자들의 만개 후 일자에 따른 종자들의 발현양. RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, 상대 발현값 -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 차등발현을 보이는 리그닌 관련 전사인자들은 TMM 최소값이 최소 60 이상을 만족하는 것으로, 리그닌 생합성 효소는 TMM 이 최소 100이상인 것을 제시함
표
군집분석 결과, ‘Hongju Seedless’에서 보다 ‘Italia’ 에서 더 많이 발현되는 전사체 그룹(좌)과 리그닌 생합성관련 유전자의 발현양(우). 그룹1, 그룹3, 그룹7 (괄호 속 숫자는 그룹에 속하는 유전자 수)와 이들 중 리그닌 생합성 및 조절 유전자들의 만개 후 일자에 따른 종자들의 발현양. RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, 상대 발현값 -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 차등발현을 보이는 리그닌 관련 전사인자들은 TMM 최소값이 최소 60 이상을 만족하는 것으로, 리그닌 생합성 효소는 TMM 이 최소 100이상인 것을 제시함
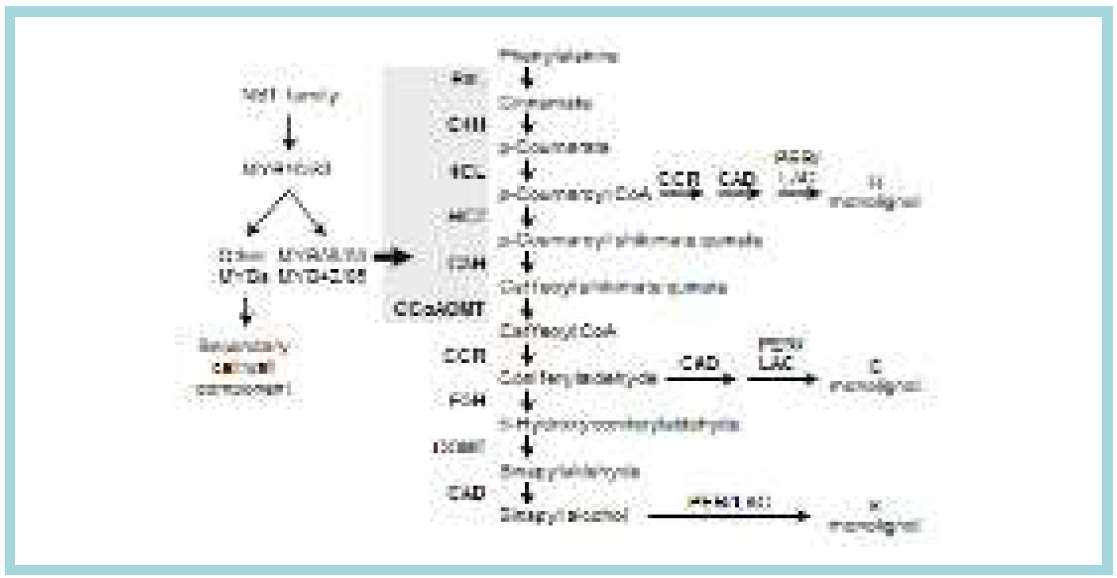 표
리그닌 생합성 관련 효소와 이들의 발현을 조절하는 조절인자. H-, G-, S- 의 3 가지 모노리그놀 유형이 만들어 질 때 중간 산물을 표시함. 화살표 옆의 약자는 리그닌 생합성 관련 효소이고 맨 왼편에는 이들의 전사인자. 회색박스는 전사인자가 작용할 것으로 예상되는 목표 유전자를 표시함. PAL, Phenylalanine ammonia-lyase; C4H, Cinnamate 4-hydroxylase; 4CL, 4-coumarate-CoA ligase; HCT, hydroxycinnamoyltransferase; C3H, p-Coumarate 3- hydroxylase; CCoAOMT, Caffeoyl-CoA O-mathytrasferase; CCR, Cinnamyl-CoA reductase; F5H, Ferulate 5-hydroxylase; COMT, Caffeic O-methyltransferase; CAD, Cinnamyl alcohol dehydrogenase
표
리그닌 생합성 관련 효소와 이들의 발현을 조절하는 조절인자. H-, G-, S- 의 3 가지 모노리그놀 유형이 만들어 질 때 중간 산물을 표시함. 화살표 옆의 약자는 리그닌 생합성 관련 효소이고 맨 왼편에는 이들의 전사인자. 회색박스는 전사인자가 작용할 것으로 예상되는 목표 유전자를 표시함. PAL, Phenylalanine ammonia-lyase; C4H, Cinnamate 4-hydroxylase; 4CL, 4-coumarate-CoA ligase; HCT, hydroxycinnamoyltransferase; C3H, p-Coumarate 3- hydroxylase; CCoAOMT, Caffeoyl-CoA O-mathytrasferase; CCR, Cinnamyl-CoA reductase; F5H, Ferulate 5-hydroxylase; COMT, Caffeic O-methyltransferase; CAD, Cinnamyl alcohol dehydrogenase
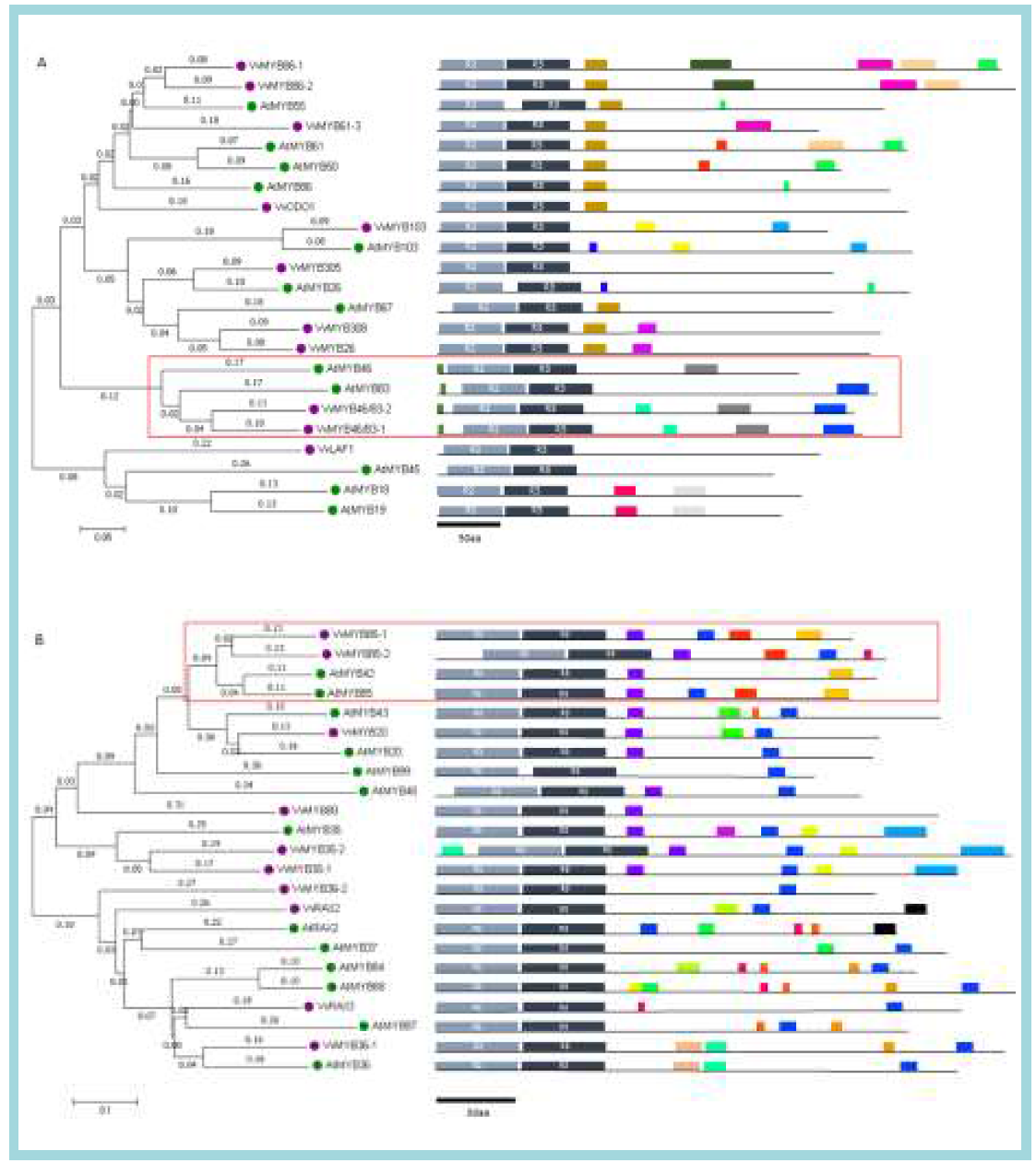 표
포도와 애기장대의 MYB family의 phylogenetic tree 중 VvMYB46/83과 VvMYB42/85를 포함하는 일부. 계통수는 133개 애기장대 R2R3-MYB 유전자와 145개 포도 R2R3-MYB 유전자를 MEGA7 프로그램의 neigbor joining method를 사용하여 분석함. 두 개의 부분적 계통수는 VvMYB46/83(A)와 VvMYB42/85(B)의 진화적 유연관계를 보여줌. 오른쪽 그림은 R2R3 myb-binding domain과 각 유전자의 모티프를 나타냄. 도메인은 PFAM에서, 모티프는 MEME 로 확인함
표
포도와 애기장대의 MYB family의 phylogenetic tree 중 VvMYB46/83과 VvMYB42/85를 포함하는 일부. 계통수는 133개 애기장대 R2R3-MYB 유전자와 145개 포도 R2R3-MYB 유전자를 MEGA7 프로그램의 neigbor joining method를 사용하여 분석함. 두 개의 부분적 계통수는 VvMYB46/83(A)와 VvMYB42/85(B)의 진화적 유연관계를 보여줌. 오른쪽 그림은 R2R3 myb-binding domain과 각 유전자의 모티프를 나타냄. 도메인은 PFAM에서, 모티프는 MEME 로 확인함
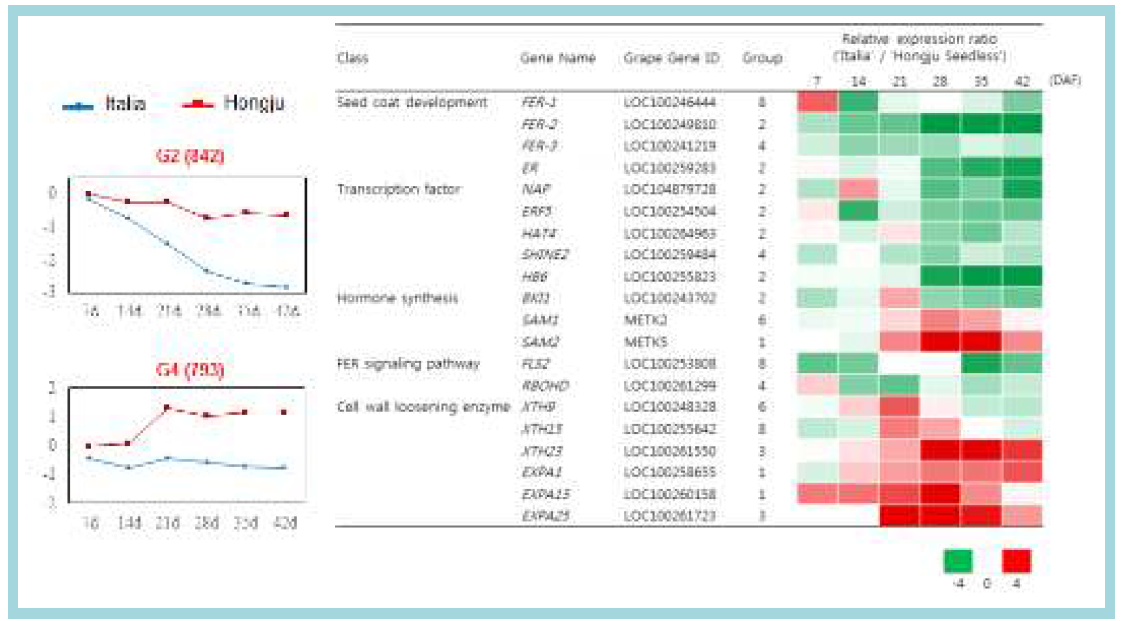 표
군집분석 결과, ‘Italia’ 보다 ‘Hongju Seedless’에서 더 많이 발현되는 차등발현 유전자(DEG) 중 군집 그룹(좌)과 종자 크기 조절 유전자들의 발현 양상(우). 그룹2, 그룹4 (괄호 안 숫자는 각 그룹에 속하는 유전자 수) RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 종자 크기를 조절하는 차등발현 유전자 선발 조건은 발현량 최대 값이 50 이상이며 상대적인 발현 비율이 3 이상 되는 유전자를 선발함
표
군집분석 결과, ‘Italia’ 보다 ‘Hongju Seedless’에서 더 많이 발현되는 차등발현 유전자(DEG) 중 군집 그룹(좌)과 종자 크기 조절 유전자들의 발현 양상(우). 그룹2, 그룹4 (괄호 안 숫자는 각 그룹에 속하는 유전자 수) RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 종자 크기를 조절하는 차등발현 유전자 선발 조건은 발현량 최대 값이 50 이상이며 상대적인 발현 비율이 3 이상 되는 유전자를 선발함
 표
‘Hongju Seedless’와 ‘Italia’의 종자에서 차등 발현하는 유전자 중 딱딱한 세포벽형성 관련 유전자의 발현. A, 리그닌 생합성 경로와 식물체 내에서 리그닌 생합성유전자 발현을 조절하는 전사인자. VND/NST/SND, NAC domain transcription factors; MYB, myeloblastosis family transcription factors; PAL, phenylalanine ammonia-lyase; C4H, cinnamate 4-hydroxylase; 4CL, 4-coumarate:CoA ligase; HCT, hydroxycinnamoyl-CoA shikimate/quinate hydroxycinnamoyl transferase; C3H, p-coumaroyl shikimate 3-hydroxylase; CCoAOMT, caffeoyl-CoA 3‑o‑methyltransferase; CCR, cinnamoyl-CoA reductase; F5H, ferulate 5-hydroxylase; COMT, caffeic acid 3-o-methyltransferase; CAD, cinnamyl alcohol dehydrogenase; PER/LAC; peroxidase/laccase. B, 선발된 리그닌 생합성 유전자의 Trimmed mean of M-values (TMM) count을 기반으로 ‘Hongju Seedless’와 ‘Italia’의 7-42DAF 단계에서 유전자의 발현 차이를 나타낸 heat map. 붉은 박스는 선발된 리그닌 생합성 유전자 표시(qRT-PCR primer 제작)
표
‘Hongju Seedless’와 ‘Italia’의 종자에서 차등 발현하는 유전자 중 딱딱한 세포벽형성 관련 유전자의 발현. A, 리그닌 생합성 경로와 식물체 내에서 리그닌 생합성유전자 발현을 조절하는 전사인자. VND/NST/SND, NAC domain transcription factors; MYB, myeloblastosis family transcription factors; PAL, phenylalanine ammonia-lyase; C4H, cinnamate 4-hydroxylase; 4CL, 4-coumarate:CoA ligase; HCT, hydroxycinnamoyl-CoA shikimate/quinate hydroxycinnamoyl transferase; C3H, p-coumaroyl shikimate 3-hydroxylase; CCoAOMT, caffeoyl-CoA 3‑o‑methyltransferase; CCR, cinnamoyl-CoA reductase; F5H, ferulate 5-hydroxylase; COMT, caffeic acid 3-o-methyltransferase; CAD, cinnamyl alcohol dehydrogenase; PER/LAC; peroxidase/laccase. B, 선발된 리그닌 생합성 유전자의 Trimmed mean of M-values (TMM) count을 기반으로 ‘Hongju Seedless’와 ‘Italia’의 7-42DAF 단계에서 유전자의 발현 차이를 나타낸 heat map. 붉은 박스는 선발된 리그닌 생합성 유전자 표시(qRT-PCR primer 제작)
 표
포도 종피 발달 관련 후보 유전자에 대한 애기장대 KO mutant에 대한 유전자형 분석. Single mutant인 agl15 (A), myb42 (B), myb46 (C), myb83 (D), myb85 (E)와 Double mutant인 myb85/myb42 (F)에 대한 유전자형 분석 결과. 1; 각각의 유전자에 대한 right primer (RP)와 left primer (LP)을 사용해 PCR 결과, 2; T-DNA에 존재하는 primer (LBa1)과 각각의 유전자에 대한 right primer (RP)를 사용해 PCR한 결과; 붉은색은 homozygous KO mutant 번호를 나타냄
표
포도 종피 발달 관련 후보 유전자에 대한 애기장대 KO mutant에 대한 유전자형 분석. Single mutant인 agl15 (A), myb42 (B), myb46 (C), myb83 (D), myb85 (E)와 Double mutant인 myb85/myb42 (F)에 대한 유전자형 분석 결과. 1; 각각의 유전자에 대한 right primer (RP)와 left primer (LP)을 사용해 PCR 결과, 2; T-DNA에 존재하는 primer (LBa1)과 각각의 유전자에 대한 right primer (RP)를 사용해 PCR한 결과; 붉은색은 homozygous KO mutant 번호를 나타냄
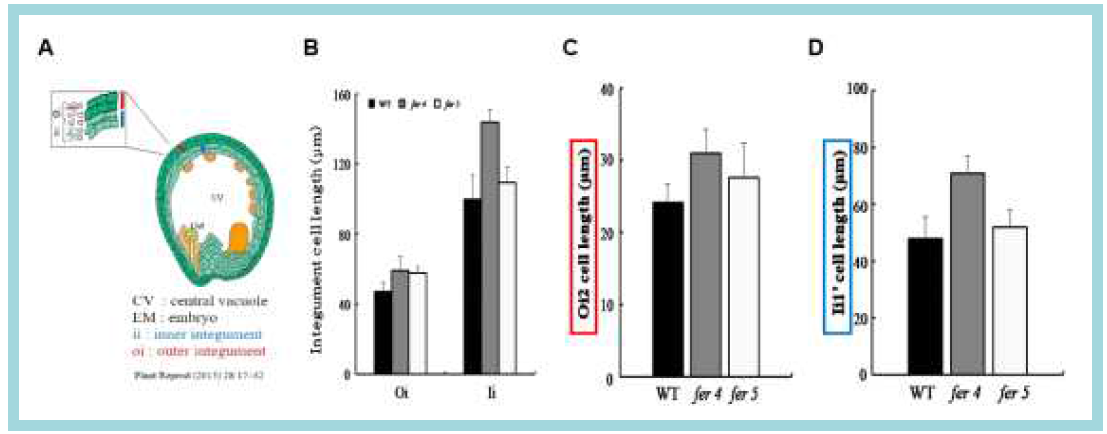 표
포도 종피 발달 관련 후보 유전자 FER에 대한 애기장대 KO mutant의 주피 세포의 길이 비교. A, 애기장대 종자 발달 단계 중 globular embryo stage의 종자 모식도; B, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 전체 외주피와 내주피 세포 길이; C, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 외주피(Oi2) 세포 길이; D, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 내주피(Ii1’) 세포 길이
표
포도 종피 발달 관련 후보 유전자 FER에 대한 애기장대 KO mutant의 주피 세포의 길이 비교. A, 애기장대 종자 발달 단계 중 globular embryo stage의 종자 모식도; B, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 전체 외주피와 내주피 세포 길이; C, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 외주피(Oi2) 세포 길이; D, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 내주피(Ii1’) 세포 길이
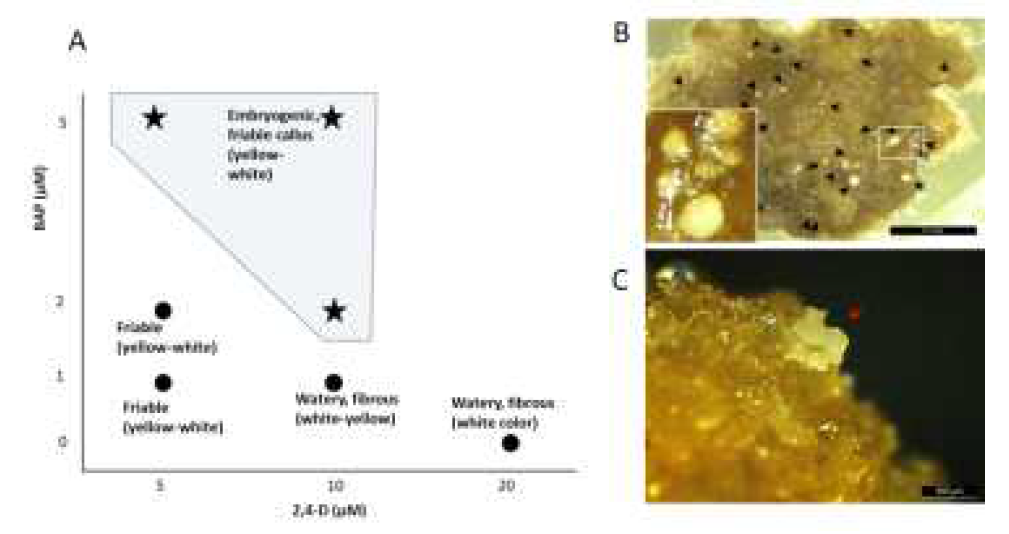 표
Italia 품종의 미분화 캘러스로부터 체세포배 발생 및 발달 조건 A. Italia 품종의 덩굴손 유래 미분화 캘러스에서 배발생 캘러스 형성을 위한 배양배지의 호르몬 조건과 캘러스 형성 반응. 별표가 있는 5각 음영은 배발생 캘러스가 형성된 호르몬 조성 영역을 표시하였다. B. 10 μM 2,4-D, 2 μM BAP 호르몬을 처리한 SH 배지(Callus induction 2)에서 2개월간 생장한 미분화 캘러스에서 형성된 pro-embryogenic mass (PEM)을 검은색 화살표로 표시하였다. 작은 상자의 안은 확대한 PEM 모습. C. PEM이 형성된 캘러스를 5 μM 2,4-D, 5 μM BAP 호르몬을 처리한 배발생 배지(Embryo development)로 옮겨, 3개월간 배양했을 때 형성된 heart stage의 체세포배
표
Italia 품종의 미분화 캘러스로부터 체세포배 발생 및 발달 조건 A. Italia 품종의 덩굴손 유래 미분화 캘러스에서 배발생 캘러스 형성을 위한 배양배지의 호르몬 조건과 캘러스 형성 반응. 별표가 있는 5각 음영은 배발생 캘러스가 형성된 호르몬 조성 영역을 표시하였다. B. 10 μM 2,4-D, 2 μM BAP 호르몬을 처리한 SH 배지(Callus induction 2)에서 2개월간 생장한 미분화 캘러스에서 형성된 pro-embryogenic mass (PEM)을 검은색 화살표로 표시하였다. 작은 상자의 안은 확대한 PEM 모습. C. PEM이 형성된 캘러스를 5 μM 2,4-D, 5 μM BAP 호르몬을 처리한 배발생 배지(Embryo development)로 옮겨, 3개월간 배양했을 때 형성된 heart stage의 체세포배
 표
HM 및 AH 교배 조합의 미성숙 접합배로부터 발생한 배발생 캘러스의 증식, 체세포배 발달 및 식물체 재분화 캘러스 발생 배지(SH, sucrose 30 g, casein hydrolysates 1 g, 10 uM 2,4-D, 0.2 uM TDZ, 2 uM AVG)에서 1개월마다 배지를 교체하여 배양한지 2-3 개월 후 형성된 배발생 캘러스의 증식과 여러 단계의 체세포배의 발생 모습. 7개의 선발된 배발생 캘러스 세포주. HM (Hongju Seedless×Muscat of Alexandria) 교배조합의 HM031, HM032, HM033, HM034, HM036, HM037과 AH (안예 × Hongju Seedless) 교배조합의 AH003을 나타내었음
표
HM 및 AH 교배 조합의 미성숙 접합배로부터 발생한 배발생 캘러스의 증식, 체세포배 발달 및 식물체 재분화 캘러스 발생 배지(SH, sucrose 30 g, casein hydrolysates 1 g, 10 uM 2,4-D, 0.2 uM TDZ, 2 uM AVG)에서 1개월마다 배지를 교체하여 배양한지 2-3 개월 후 형성된 배발생 캘러스의 증식과 여러 단계의 체세포배의 발생 모습. 7개의 선발된 배발생 캘러스 세포주. HM (Hongju Seedless×Muscat of Alexandria) 교배조합의 HM031, HM032, HM033, HM034, HM036, HM037과 AH (안예 × Hongju Seedless) 교배조합의 AH003을 나타내었음
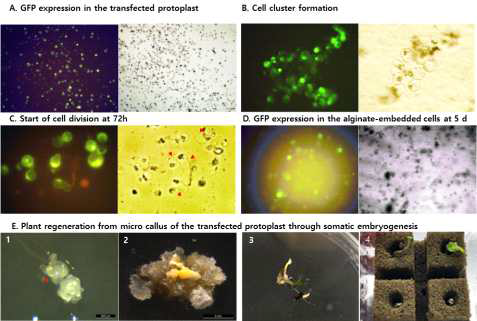 표
배발생캘러스 세포주 HM032의 원형질체로부터 식물체 재분화 A. CRISPR/Cas9 벡터 pGK1064를 transfection 시킨 원형질체의 형광현미경 사진. 대부분의 원형질체 세포에서 GFP 녹색형광이 발현됨. B. WI 버퍼에서 24시간 배양 후, 0.5 M mannitol을 넣은 원형질체배양 배지로 옮겨 48시간 추가 배양 중 형성된 세포 클러스터. C. 72시간 후 세포분열이 관찰됨. D. Alginate embedding된 상태에서 원형질체의 구형 형상이 유지되고, 녹색 형광이 발현되는 모습. E. 고체배지에서 8개월 동안 진행된 Microcalli 형성과 체세포배 발달, 재분화 식물체의 발달 과정
표
배발생캘러스 세포주 HM032의 원형질체로부터 식물체 재분화 A. CRISPR/Cas9 벡터 pGK1064를 transfection 시킨 원형질체의 형광현미경 사진. 대부분의 원형질체 세포에서 GFP 녹색형광이 발현됨. B. WI 버퍼에서 24시간 배양 후, 0.5 M mannitol을 넣은 원형질체배양 배지로 옮겨 48시간 추가 배양 중 형성된 세포 클러스터. C. 72시간 후 세포분열이 관찰됨. D. Alginate embedding된 상태에서 원형질체의 구형 형상이 유지되고, 녹색 형광이 발현되는 모습. E. 고체배지에서 8개월 동안 진행된 Microcalli 형성과 체세포배 발달, 재분화 식물체의 발달 과정
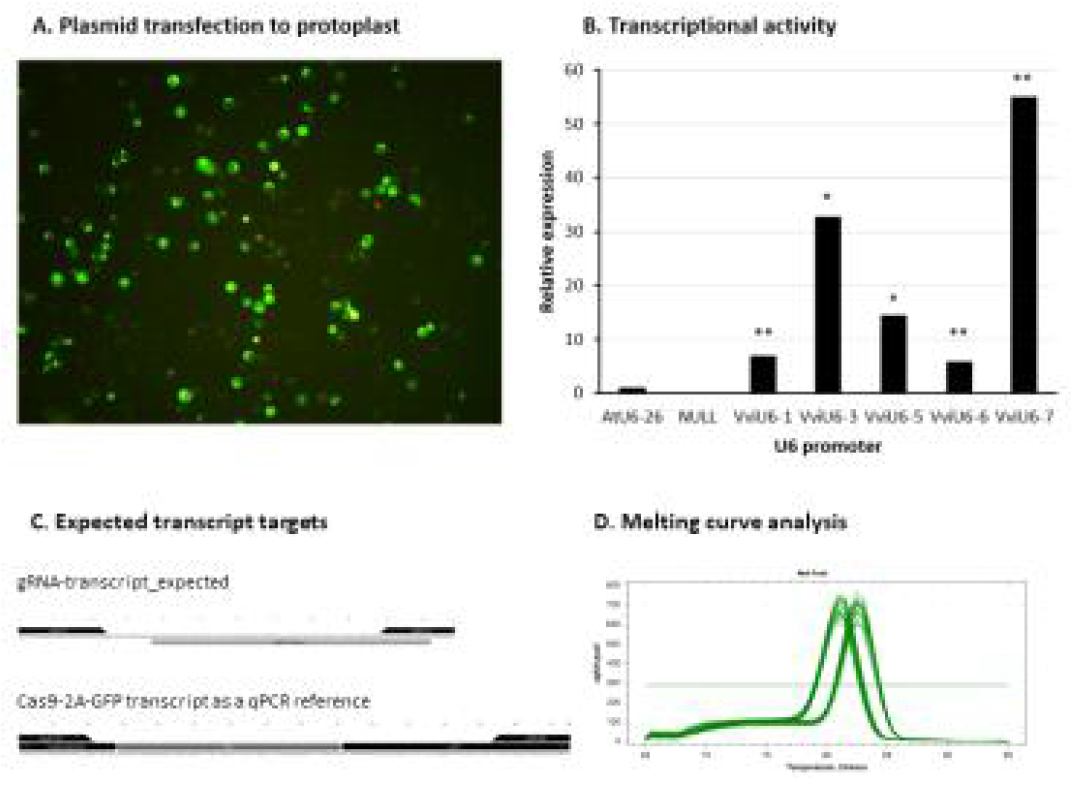 표
Guide RNA 발현을 위한 포도 U6 프로모터의 전사활성 비교 A. Italia 품종의 포도 원형질체에 플라스미드를 형질주입하여 24시간 배양한 후 total RNA를 추출하였다. B. Realtime PCR을 이용하여 U6 프로모터 하위에 클로닝한 170 bp 길이의 gRNA fragment의 전사량을 측정하였다. 총 4개의 생물학적 반복, 2개의 기술적 반복으로 측정하였으며 애기장대 AtU6-26 프로모터 실험군에 대한 상대값으로 나타내었음. 별표는 t-검정에 의한 유의확률(p-value)에 따라 표현한 것으로 *는 5%, **는 1%의 유의확률을 나타냄. C. Realtime PCR에서 증폭할 RNA transcript의 서열 구조와 프라이머 위치. D. Realtime PCR 종료 후, Melting curve analysis를 수행한 결과. gRNA-transcript와 reference transcript가 각각 단일 피크로 증폭되었음을 확인하였다
표
Guide RNA 발현을 위한 포도 U6 프로모터의 전사활성 비교 A. Italia 품종의 포도 원형질체에 플라스미드를 형질주입하여 24시간 배양한 후 total RNA를 추출하였다. B. Realtime PCR을 이용하여 U6 프로모터 하위에 클로닝한 170 bp 길이의 gRNA fragment의 전사량을 측정하였다. 총 4개의 생물학적 반복, 2개의 기술적 반복으로 측정하였으며 애기장대 AtU6-26 프로모터 실험군에 대한 상대값으로 나타내었음. 별표는 t-검정에 의한 유의확률(p-value)에 따라 표현한 것으로 *는 5%, **는 1%의 유의확률을 나타냄. C. Realtime PCR에서 증폭할 RNA transcript의 서열 구조와 프라이머 위치. D. Realtime PCR 종료 후, Melting curve analysis를 수행한 결과. gRNA-transcript와 reference transcript가 각각 단일 피크로 증폭되었음을 확인하였다
 표
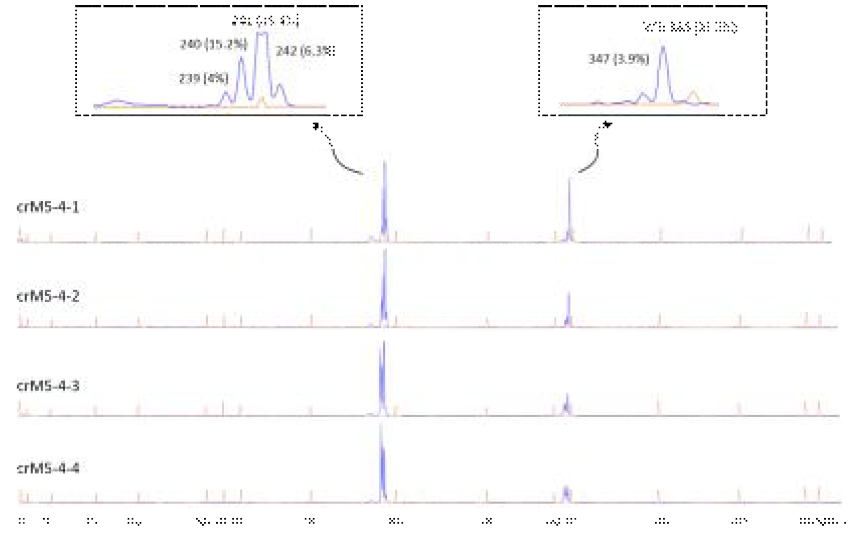
IDAA 분석: 아그로박테리움으로 형질전환된 crMADS5-1493.1599D의 4개의 캘러스 군집 (crM5-4-1부터 4)의 InDel 유전형 야생형 증폭 DNA 크기는 348 bp이다. 파란색 크로마토그램이 6FAM으로 표지된 PCR 증폭 DNA이고, 주황색 크로마토그램은 GeneScan™ 500 LIZ™ dye Size Standard (ThermoFisher Scientific) 마커이다. 윗쪽의 상자는 crM5-4-1 시료에서 빈도가 높은 크기 영역의 피크를 확대하여 제시하였다. 가장 아래 쪽에 마커 피크의 크기를 표시하였다
표
IDAA 분석: 아그로박테리움으로 형질전환된 crMADS5-1493.1599D의 4개의 캘러스 군집 (crM5-4-1부터 4)의 InDel 유전형 야생형 증폭 DNA 크기는 348 bp이다. 파란색 크로마토그램이 6FAM으로 표지된 PCR 증폭 DNA이고, 주황색 크로마토그램은 GeneScan™ 500 LIZ™ dye Size Standard (ThermoFisher Scientific) 마커이다. 윗쪽의 상자는 crM5-4-1 시료에서 빈도가 높은 크기 영역의 피크를 확대하여 제시하였다. 가장 아래 쪽에 마커 피크의 크기를 표시하였다
 표
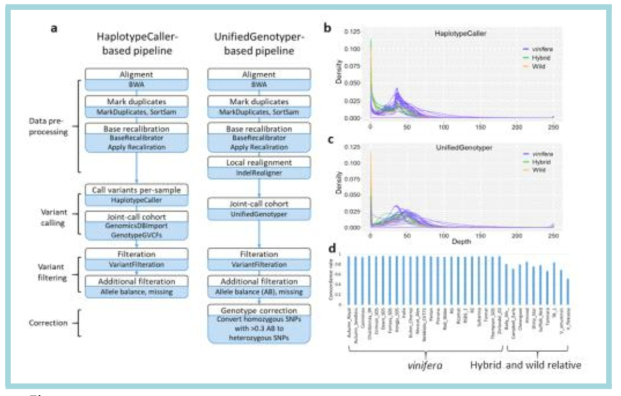
Comparison of workflows for variant discovery from grape genome sequencing data. a Workflows of HaplotypeCaller-based variant calling pipeline similar to the GATK Best Practices and UnifiedGenotyper-based variant calling pipeline. b Distribution of the depth of coverage (DP) per site from each of our grape accessions in raw SNP calling data obtained through Genotype GVCFs using the Haplotype Caller-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. c Distribution of the DP per site from each of our grape accessions in raw SNP calling data obtained through Unified Genotyper using the Unified Genotyper-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. Accessions with relatively higher DP per site are Cannonau (V. vinifera) and Suffolk Red (hybrid). d Genotype concordance rate of SNPs called by the GenotypeGVCFs with SNPs called by the UnifiedGenotyper in each of grape accessions. Only the SNPs that shared the grape reference genome coordinates were compared. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Comparison of workflows for variant discovery from grape genome sequencing data. a Workflows of HaplotypeCaller-based variant calling pipeline similar to the GATK Best Practices and UnifiedGenotyper-based variant calling pipeline. b Distribution of the depth of coverage (DP) per site from each of our grape accessions in raw SNP calling data obtained through Genotype GVCFs using the Haplotype Caller-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. c Distribution of the DP per site from each of our grape accessions in raw SNP calling data obtained through Unified Genotyper using the Unified Genotyper-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. Accessions with relatively higher DP per site are Cannonau (V. vinifera) and Suffolk Red (hybrid). d Genotype concordance rate of SNPs called by the GenotypeGVCFs with SNPs called by the UnifiedGenotyper in each of grape accessions. Only the SNPs that shared the grape reference genome coordinates were compared. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
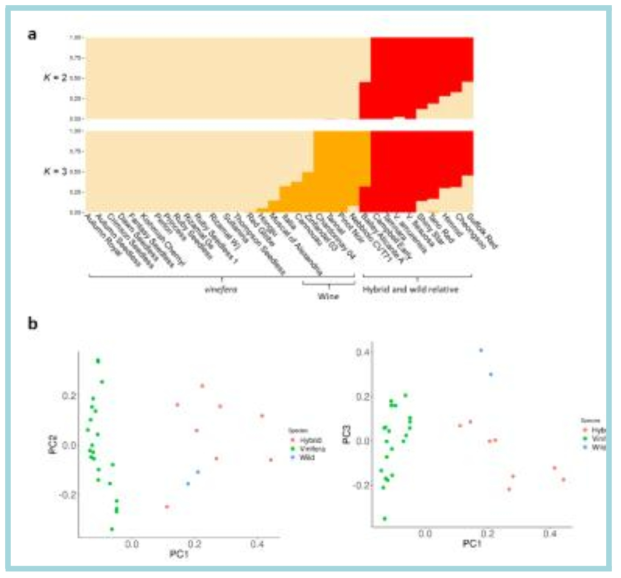
Grape population structure. a Population structure of 34 grape accessions estimated by fastSTRUCTURE. Each color represents one ancestral population. Each accession is represented by a vertical bar, and the length of colored segment in each vertical bar represents the proportion contributed by ancestral populations. b Principal components of SNP variation in grape accessions using whole-genome SNP data. The plots show the first three principal components. Vitis vinifera, interspecific hybrids, and wild relatives are shown by green, red, and blue dots, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Grape population structure. a Population structure of 34 grape accessions estimated by fastSTRUCTURE. Each color represents one ancestral population. Each accession is represented by a vertical bar, and the length of colored segment in each vertical bar represents the proportion contributed by ancestral populations. b Principal components of SNP variation in grape accessions using whole-genome SNP data. The plots show the first three principal components. Vitis vinifera, interspecific hybrids, and wild relatives are shown by green, red, and blue dots, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
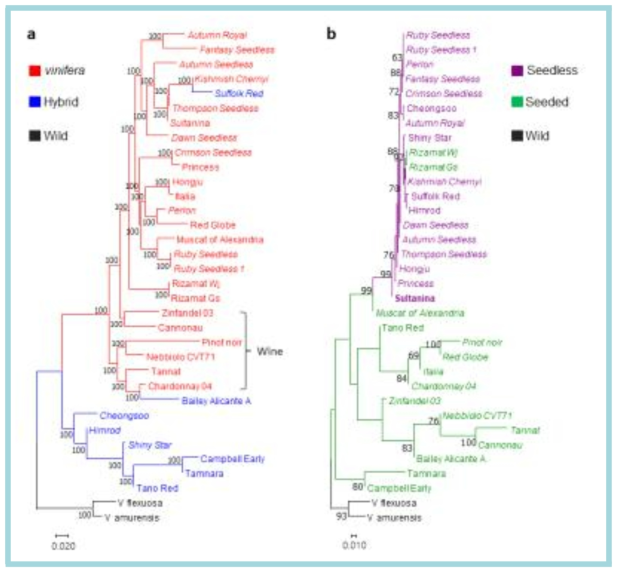
Phylogeny of grape. a Neighbor-joining phylogenetic tree of 34 grape nuclear genomes constructed using the 5,373,452 high-quality SNPs called from whole genome resequencing data. Accessions in the Neighbor-joining tree are represented by different colors: Vitis vinifera (red), interspecific hybrids (blue), and wild relatives (black). Group of wine grape accessions is indicated to emphasize their unique pedigree in this tree. Seedless accessions are in italic. b The tree constructed using 1,744 SNPs from 100-kb chromosomal region that contains the SDI locus in the central position. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are represented by black letters and seedless accessions represented by red letters. V. vinifera accessions are in italic. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Phylogeny of grape. a Neighbor-joining phylogenetic tree of 34 grape nuclear genomes constructed using the 5,373,452 high-quality SNPs called from whole genome resequencing data. Accessions in the Neighbor-joining tree are represented by different colors: Vitis vinifera (red), interspecific hybrids (blue), and wild relatives (black). Group of wine grape accessions is indicated to emphasize their unique pedigree in this tree. Seedless accessions are in italic. b The tree constructed using 1,744 SNPs from 100-kb chromosomal region that contains the SDI locus in the central position. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are represented by black letters and seedless accessions represented by red letters. V. vinifera accessions are in italic. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
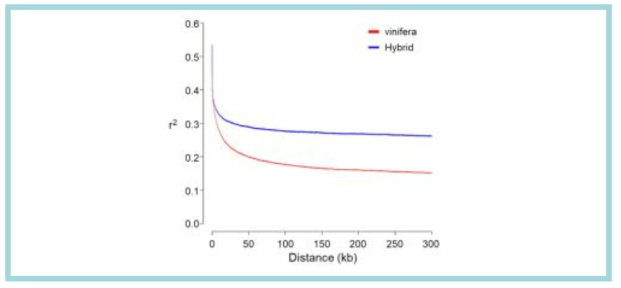 표
Curves of linkage disequilibrium decay patterns determined by squared correlations of allele frequencies (r2) against distance between polymorphic sites in 20 Vitis vinefera (red) and eight interspecific hybrid (blue) grape accessions. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Curves of linkage disequilibrium decay patterns determined by squared correlations of allele frequencies (r2) against distance between polymorphic sites in 20 Vitis vinefera (red) and eight interspecific hybrid (blue) grape accessions. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
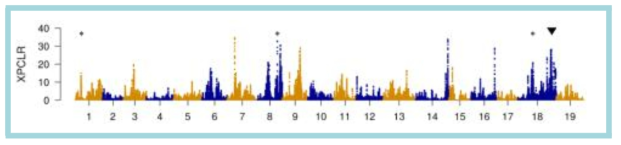 표
Genome-wide likelihood (XP-CLR) values for selection of seedlessness for seedless grape relatives to seeded grape accessions in 5-kb windows across the genome. The chromosome number is indicated along the x-axis. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the minor seedless-regulating QTL and AGL11 associated with a major dominant QTL, which were predicted based on this XP-CLR analysis as well as logistic association and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Genome-wide likelihood (XP-CLR) values for selection of seedlessness for seedless grape relatives to seeded grape accessions in 5-kb windows across the genome. The chromosome number is indicated along the x-axis. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the minor seedless-regulating QTL and AGL11 associated with a major dominant QTL, which were predicted based on this XP-CLR analysis as well as logistic association and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
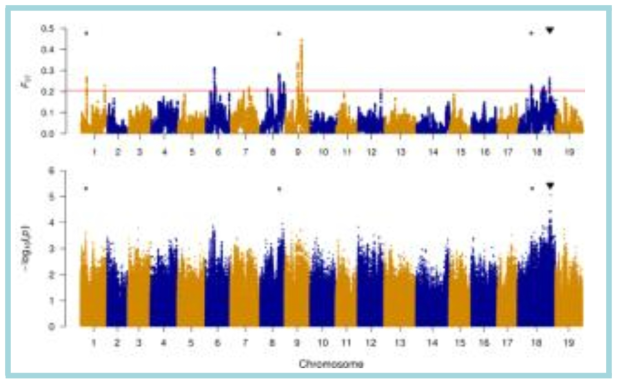 표
Manhattan plots of selective sweep regions for selection of seedlessness inferred from FST (upper panel) and of seedlessness genome-wide logistic association scans using GENESIS (lower panel). The red line marks the regions at the top 0.5% of FST values. The -log10 P values from a genome-wide scan are plotted against the position on each of the 19 grape chromosomes. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the recessive seedless-regulating genes and VviAGL11 associated with a dominant gene, which were predicted based on FST and GENESIS analyses as well as XP-CLR and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Manhattan plots of selective sweep regions for selection of seedlessness inferred from FST (upper panel) and of seedlessness genome-wide logistic association scans using GENESIS (lower panel). The red line marks the regions at the top 0.5% of FST values. The -log10 P values from a genome-wide scan are plotted against the position on each of the 19 grape chromosomes. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the recessive seedless-regulating genes and VviAGL11 associated with a dominant gene, which were predicted based on FST and GENESIS analyses as well as XP-CLR and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
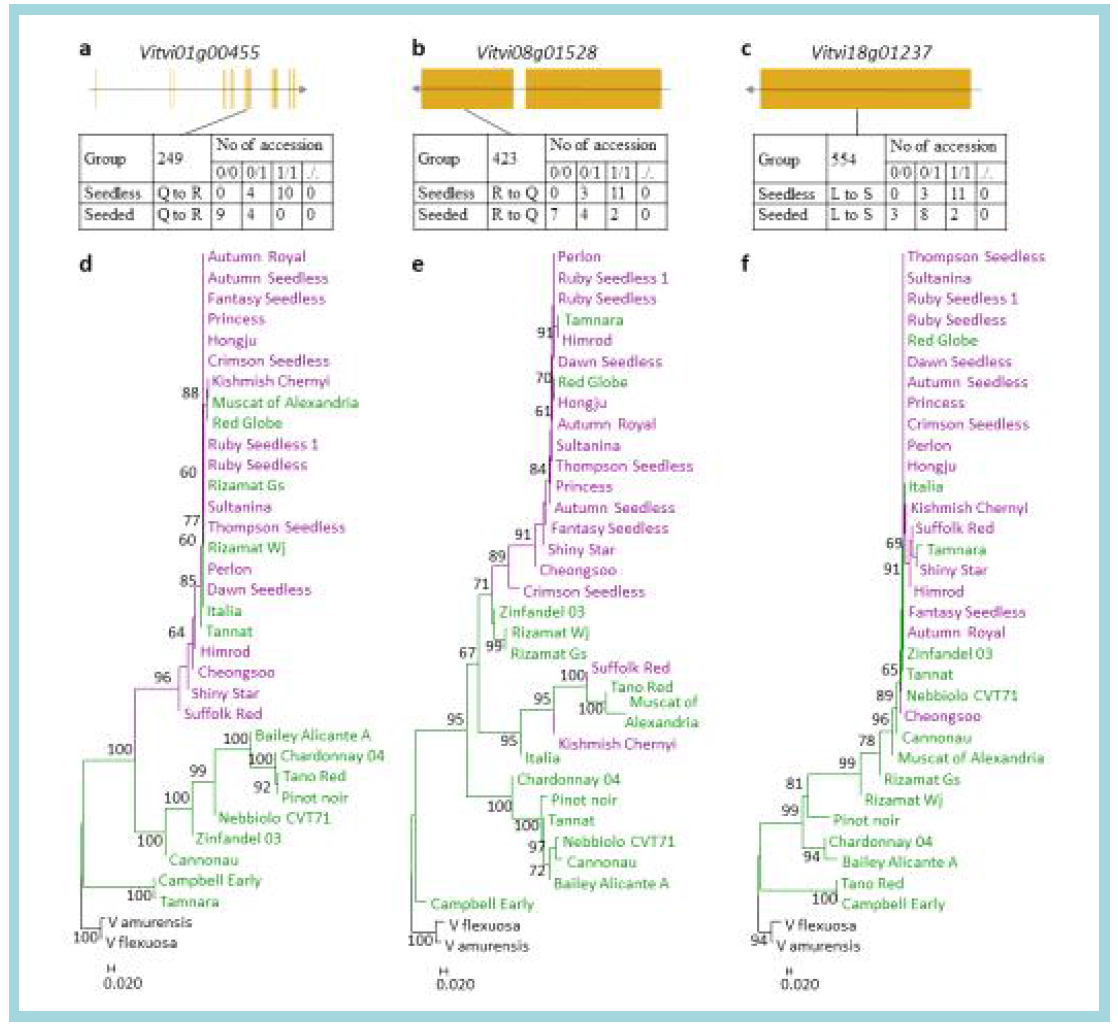 표
Genetic features for the candidate causal genes for minor recessive seedless-regulating candidate selective sweeps. Coding sequence structures of Vitvi01g00455 (a), Vitvi08g01528 (b), and Vitvi18g01237 (c) and genotype distributions of candidate causal SNPs in these genes for 15 seedless and 13 seeded grape accessions tested. Reference homozygous genotype is indicated by 0/0, heterozygous 0/1, non-reference homozygous 1/1, and missing ./.. Amino acid positions are indicated by numbers. Neighbor-joining phylogenetic trees of 17 seedless and 14 seeded accessions constructed using 1,744 SNPs, 939 SNPs, and 871 SNPs from 100-kb chromosomal regions that contains the Vitvi01g00455 (d), Vitvi08g01528 (e), and Vitvi18g01237 (f) genes in their central position, respectively. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are in green, seedless accessions in purple, and two wild relatives in black. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Genetic features for the candidate causal genes for minor recessive seedless-regulating candidate selective sweeps. Coding sequence structures of Vitvi01g00455 (a), Vitvi08g01528 (b), and Vitvi18g01237 (c) and genotype distributions of candidate causal SNPs in these genes for 15 seedless and 13 seeded grape accessions tested. Reference homozygous genotype is indicated by 0/0, heterozygous 0/1, non-reference homozygous 1/1, and missing ./.. Amino acid positions are indicated by numbers. Neighbor-joining phylogenetic trees of 17 seedless and 14 seeded accessions constructed using 1,744 SNPs, 939 SNPs, and 871 SNPs from 100-kb chromosomal regions that contains the Vitvi01g00455 (d), Vitvi08g01528 (e), and Vitvi18g01237 (f) genes in their central position, respectively. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are in green, seedless accessions in purple, and two wild relatives in black. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
군집분석 결과, ‘Hongju Seedless’에서 보다 ‘Italia’ 에서 더 많이 발현되는 전사체 그룹(좌)과 리그닌 생합성관련 유전자의 발현양(우). 그룹1, 그룹3, 그룹7 (괄호 속 숫자는 그룹에 속하는 유전자 수)와 이들 중 리그닌 생합성 및 조절 유전자들의 만개 후 일자에 따른 종자들의 발현양. RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, 상대 발현값 -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 차등발현을 보이는 리그닌 관련 전사인자들은 TMM 최소값이 최소 60 이상을 만족하는 것으로, 리그닌 생합성 효소는 TMM 이 최소 100이상인 것을 제시함
표
군집분석 결과, ‘Hongju Seedless’에서 보다 ‘Italia’ 에서 더 많이 발현되는 전사체 그룹(좌)과 리그닌 생합성관련 유전자의 발현양(우). 그룹1, 그룹3, 그룹7 (괄호 속 숫자는 그룹에 속하는 유전자 수)와 이들 중 리그닌 생합성 및 조절 유전자들의 만개 후 일자에 따른 종자들의 발현양. RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, 상대 발현값 -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 차등발현을 보이는 리그닌 관련 전사인자들은 TMM 최소값이 최소 60 이상을 만족하는 것으로, 리그닌 생합성 효소는 TMM 이 최소 100이상인 것을 제시함
 표
리그닌 생합성 관련 효소와 이들의 발현을 조절하는 조절인자. H-, G-, S- 의 3 가지 모노리그놀 유형이 만들어 질 때 중간 산물을 표시함. 화살표 옆의 약자는 리그닌 생합성 관련 효소이고 맨 왼편에는 이들의 전사인자. 회색박스는 전사인자가 작용할 것으로 예상되는 목표 유전자를 표시함. PAL, Phenylalanine ammonia-lyase; C4H, Cinnamate 4-hydroxylase; 4CL, 4-coumarate-CoA ligase; HCT, hydroxycinnamoyltransferase; C3H, p-Coumarate 3- hydroxylase; CCoAOMT, Caffeoyl-CoA O-mathytrasferase; CCR, Cinnamyl-CoA reductase; F5H, Ferulate 5-hydroxylase; COMT, Caffeic O-methyltransferase; CAD, Cinnamyl alcohol dehydrogenase
표
리그닌 생합성 관련 효소와 이들의 발현을 조절하는 조절인자. H-, G-, S- 의 3 가지 모노리그놀 유형이 만들어 질 때 중간 산물을 표시함. 화살표 옆의 약자는 리그닌 생합성 관련 효소이고 맨 왼편에는 이들의 전사인자. 회색박스는 전사인자가 작용할 것으로 예상되는 목표 유전자를 표시함. PAL, Phenylalanine ammonia-lyase; C4H, Cinnamate 4-hydroxylase; 4CL, 4-coumarate-CoA ligase; HCT, hydroxycinnamoyltransferase; C3H, p-Coumarate 3- hydroxylase; CCoAOMT, Caffeoyl-CoA O-mathytrasferase; CCR, Cinnamyl-CoA reductase; F5H, Ferulate 5-hydroxylase; COMT, Caffeic O-methyltransferase; CAD, Cinnamyl alcohol dehydrogenase
 표
포도와 애기장대의 MYB family의 phylogenetic tree 중 VvMYB46/83과 VvMYB42/85를 포함하는 일부. 계통수는 133개 애기장대 R2R3-MYB 유전자와 145개 포도 R2R3-MYB 유전자를 MEGA7 프로그램의 neigbor joining method를 사용하여 분석함. 두 개의 부분적 계통수는 VvMYB46/83(A)와 VvMYB42/85(B)의 진화적 유연관계를 보여줌. 오른쪽 그림은 R2R3 myb-binding domain과 각 유전자의 모티프를 나타냄. 도메인은 PFAM에서, 모티프는 MEME 로 확인함
표
포도와 애기장대의 MYB family의 phylogenetic tree 중 VvMYB46/83과 VvMYB42/85를 포함하는 일부. 계통수는 133개 애기장대 R2R3-MYB 유전자와 145개 포도 R2R3-MYB 유전자를 MEGA7 프로그램의 neigbor joining method를 사용하여 분석함. 두 개의 부분적 계통수는 VvMYB46/83(A)와 VvMYB42/85(B)의 진화적 유연관계를 보여줌. 오른쪽 그림은 R2R3 myb-binding domain과 각 유전자의 모티프를 나타냄. 도메인은 PFAM에서, 모티프는 MEME 로 확인함
 표
군집분석 결과, ‘Italia’ 보다 ‘Hongju Seedless’에서 더 많이 발현되는 차등발현 유전자(DEG) 중 군집 그룹(좌)과 종자 크기 조절 유전자들의 발현 양상(우). 그룹2, 그룹4 (괄호 안 숫자는 각 그룹에 속하는 유전자 수) RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 종자 크기를 조절하는 차등발현 유전자 선발 조건은 발현량 최대 값이 50 이상이며 상대적인 발현 비율이 3 이상 되는 유전자를 선발함
표
군집분석 결과, ‘Italia’ 보다 ‘Hongju Seedless’에서 더 많이 발현되는 차등발현 유전자(DEG) 중 군집 그룹(좌)과 종자 크기 조절 유전자들의 발현 양상(우). 그룹2, 그룹4 (괄호 안 숫자는 각 그룹에 속하는 유전자 수) RNA sequencing 값은 TMM으로 보정됨. DEG의 상대 발현비율은 log2 fold change로 홍주를 분모로 하였을 때, -4 이하를 초록색으로, 4 이상을 빨간색으로 표시함. 종자 크기를 조절하는 차등발현 유전자 선발 조건은 발현량 최대 값이 50 이상이며 상대적인 발현 비율이 3 이상 되는 유전자를 선발함
 표
‘Hongju Seedless’와 ‘Italia’의 종자에서 차등 발현하는 유전자 중 딱딱한 세포벽형성 관련 유전자의 발현. A, 리그닌 생합성 경로와 식물체 내에서 리그닌 생합성유전자 발현을 조절하는 전사인자. VND/NST/SND, NAC domain transcription factors; MYB, myeloblastosis family transcription factors; PAL, phenylalanine ammonia-lyase; C4H, cinnamate 4-hydroxylase; 4CL, 4-coumarate:CoA ligase; HCT, hydroxycinnamoyl-CoA shikimate/quinate hydroxycinnamoyl transferase; C3H, p-coumaroyl shikimate 3-hydroxylase; CCoAOMT, caffeoyl-CoA 3‑o‑methyltransferase; CCR, cinnamoyl-CoA reductase; F5H, ferulate 5-hydroxylase; COMT, caffeic acid 3-o-methyltransferase; CAD, cinnamyl alcohol dehydrogenase; PER/LAC; peroxidase/laccase. B, 선발된 리그닌 생합성 유전자의 Trimmed mean of M-values (TMM) count을 기반으로 ‘Hongju Seedless’와 ‘Italia’의 7-42DAF 단계에서 유전자의 발현 차이를 나타낸 heat map. 붉은 박스는 선발된 리그닌 생합성 유전자 표시(qRT-PCR primer 제작)
표
‘Hongju Seedless’와 ‘Italia’의 종자에서 차등 발현하는 유전자 중 딱딱한 세포벽형성 관련 유전자의 발현. A, 리그닌 생합성 경로와 식물체 내에서 리그닌 생합성유전자 발현을 조절하는 전사인자. VND/NST/SND, NAC domain transcription factors; MYB, myeloblastosis family transcription factors; PAL, phenylalanine ammonia-lyase; C4H, cinnamate 4-hydroxylase; 4CL, 4-coumarate:CoA ligase; HCT, hydroxycinnamoyl-CoA shikimate/quinate hydroxycinnamoyl transferase; C3H, p-coumaroyl shikimate 3-hydroxylase; CCoAOMT, caffeoyl-CoA 3‑o‑methyltransferase; CCR, cinnamoyl-CoA reductase; F5H, ferulate 5-hydroxylase; COMT, caffeic acid 3-o-methyltransferase; CAD, cinnamyl alcohol dehydrogenase; PER/LAC; peroxidase/laccase. B, 선발된 리그닌 생합성 유전자의 Trimmed mean of M-values (TMM) count을 기반으로 ‘Hongju Seedless’와 ‘Italia’의 7-42DAF 단계에서 유전자의 발현 차이를 나타낸 heat map. 붉은 박스는 선발된 리그닌 생합성 유전자 표시(qRT-PCR primer 제작)
 표
포도 종피 발달 관련 후보 유전자에 대한 애기장대 KO mutant에 대한 유전자형 분석. Single mutant인 agl15 (A), myb42 (B), myb46 (C), myb83 (D), myb85 (E)와 Double mutant인 myb85/myb42 (F)에 대한 유전자형 분석 결과. 1; 각각의 유전자에 대한 right primer (RP)와 left primer (LP)을 사용해 PCR 결과, 2; T-DNA에 존재하는 primer (LBa1)과 각각의 유전자에 대한 right primer (RP)를 사용해 PCR한 결과; 붉은색은 homozygous KO mutant 번호를 나타냄
표
포도 종피 발달 관련 후보 유전자에 대한 애기장대 KO mutant에 대한 유전자형 분석. Single mutant인 agl15 (A), myb42 (B), myb46 (C), myb83 (D), myb85 (E)와 Double mutant인 myb85/myb42 (F)에 대한 유전자형 분석 결과. 1; 각각의 유전자에 대한 right primer (RP)와 left primer (LP)을 사용해 PCR 결과, 2; T-DNA에 존재하는 primer (LBa1)과 각각의 유전자에 대한 right primer (RP)를 사용해 PCR한 결과; 붉은색은 homozygous KO mutant 번호를 나타냄
 표
포도 종피 발달 관련 후보 유전자 FER에 대한 애기장대 KO mutant의 주피 세포의 길이 비교. A, 애기장대 종자 발달 단계 중 globular embryo stage의 종자 모식도; B, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 전체 외주피와 내주피 세포 길이; C, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 외주피(Oi2) 세포 길이; D, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 내주피(Ii1’) 세포 길이
표
포도 종피 발달 관련 후보 유전자 FER에 대한 애기장대 KO mutant의 주피 세포의 길이 비교. A, 애기장대 종자 발달 단계 중 globular embryo stage의 종자 모식도; B, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 전체 외주피와 내주피 세포 길이; C, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 외주피(Oi2) 세포 길이; D, FER에 대한 애기장대 homozygous KO mutant (fer4, fer5)와 야생형(Col-0) globular embryo stage의 내주피(Ii1’) 세포 길이
 표
Italia 품종의 미분화 캘러스로부터 체세포배 발생 및 발달 조건 A. Italia 품종의 덩굴손 유래 미분화 캘러스에서 배발생 캘러스 형성을 위한 배양배지의 호르몬 조건과 캘러스 형성 반응. 별표가 있는 5각 음영은 배발생 캘러스가 형성된 호르몬 조성 영역을 표시하였다. B. 10 μM 2,4-D, 2 μM BAP 호르몬을 처리한 SH 배지(Callus induction 2)에서 2개월간 생장한 미분화 캘러스에서 형성된 pro-embryogenic mass (PEM)을 검은색 화살표로 표시하였다. 작은 상자의 안은 확대한 PEM 모습. C. PEM이 형성된 캘러스를 5 μM 2,4-D, 5 μM BAP 호르몬을 처리한 배발생 배지(Embryo development)로 옮겨, 3개월간 배양했을 때 형성된 heart stage의 체세포배
표
Italia 품종의 미분화 캘러스로부터 체세포배 발생 및 발달 조건 A. Italia 품종의 덩굴손 유래 미분화 캘러스에서 배발생 캘러스 형성을 위한 배양배지의 호르몬 조건과 캘러스 형성 반응. 별표가 있는 5각 음영은 배발생 캘러스가 형성된 호르몬 조성 영역을 표시하였다. B. 10 μM 2,4-D, 2 μM BAP 호르몬을 처리한 SH 배지(Callus induction 2)에서 2개월간 생장한 미분화 캘러스에서 형성된 pro-embryogenic mass (PEM)을 검은색 화살표로 표시하였다. 작은 상자의 안은 확대한 PEM 모습. C. PEM이 형성된 캘러스를 5 μM 2,4-D, 5 μM BAP 호르몬을 처리한 배발생 배지(Embryo development)로 옮겨, 3개월간 배양했을 때 형성된 heart stage의 체세포배
 표
HM 및 AH 교배 조합의 미성숙 접합배로부터 발생한 배발생 캘러스의 증식, 체세포배 발달 및 식물체 재분화 캘러스 발생 배지(SH, sucrose 30 g, casein hydrolysates 1 g, 10 uM 2,4-D, 0.2 uM TDZ, 2 uM AVG)에서 1개월마다 배지를 교체하여 배양한지 2-3 개월 후 형성된 배발생 캘러스의 증식과 여러 단계의 체세포배의 발생 모습. 7개의 선발된 배발생 캘러스 세포주. HM (Hongju Seedless×Muscat of Alexandria) 교배조합의 HM031, HM032, HM033, HM034, HM036, HM037과 AH (안예 × Hongju Seedless) 교배조합의 AH003을 나타내었음
표
HM 및 AH 교배 조합의 미성숙 접합배로부터 발생한 배발생 캘러스의 증식, 체세포배 발달 및 식물체 재분화 캘러스 발생 배지(SH, sucrose 30 g, casein hydrolysates 1 g, 10 uM 2,4-D, 0.2 uM TDZ, 2 uM AVG)에서 1개월마다 배지를 교체하여 배양한지 2-3 개월 후 형성된 배발생 캘러스의 증식과 여러 단계의 체세포배의 발생 모습. 7개의 선발된 배발생 캘러스 세포주. HM (Hongju Seedless×Muscat of Alexandria) 교배조합의 HM031, HM032, HM033, HM034, HM036, HM037과 AH (안예 × Hongju Seedless) 교배조합의 AH003을 나타내었음
 표
배발생캘러스 세포주 HM032의 원형질체로부터 식물체 재분화 A. CRISPR/Cas9 벡터 pGK1064를 transfection 시킨 원형질체의 형광현미경 사진. 대부분의 원형질체 세포에서 GFP 녹색형광이 발현됨. B. WI 버퍼에서 24시간 배양 후, 0.5 M mannitol을 넣은 원형질체배양 배지로 옮겨 48시간 추가 배양 중 형성된 세포 클러스터. C. 72시간 후 세포분열이 관찰됨. D. Alginate embedding된 상태에서 원형질체의 구형 형상이 유지되고, 녹색 형광이 발현되는 모습. E. 고체배지에서 8개월 동안 진행된 Microcalli 형성과 체세포배 발달, 재분화 식물체의 발달 과정
표
배발생캘러스 세포주 HM032의 원형질체로부터 식물체 재분화 A. CRISPR/Cas9 벡터 pGK1064를 transfection 시킨 원형질체의 형광현미경 사진. 대부분의 원형질체 세포에서 GFP 녹색형광이 발현됨. B. WI 버퍼에서 24시간 배양 후, 0.5 M mannitol을 넣은 원형질체배양 배지로 옮겨 48시간 추가 배양 중 형성된 세포 클러스터. C. 72시간 후 세포분열이 관찰됨. D. Alginate embedding된 상태에서 원형질체의 구형 형상이 유지되고, 녹색 형광이 발현되는 모습. E. 고체배지에서 8개월 동안 진행된 Microcalli 형성과 체세포배 발달, 재분화 식물체의 발달 과정
 표
Guide RNA 발현을 위한 포도 U6 프로모터의 전사활성 비교 A. Italia 품종의 포도 원형질체에 플라스미드를 형질주입하여 24시간 배양한 후 total RNA를 추출하였다. B. Realtime PCR을 이용하여 U6 프로모터 하위에 클로닝한 170 bp 길이의 gRNA fragment의 전사량을 측정하였다. 총 4개의 생물학적 반복, 2개의 기술적 반복으로 측정하였으며 애기장대 AtU6-26 프로모터 실험군에 대한 상대값으로 나타내었음. 별표는 t-검정에 의한 유의확률(p-value)에 따라 표현한 것으로 *는 5%, **는 1%의 유의확률을 나타냄. C. Realtime PCR에서 증폭할 RNA transcript의 서열 구조와 프라이머 위치. D. Realtime PCR 종료 후, Melting curve analysis를 수행한 결과. gRNA-transcript와 reference transcript가 각각 단일 피크로 증폭되었음을 확인하였다
표
Guide RNA 발현을 위한 포도 U6 프로모터의 전사활성 비교 A. Italia 품종의 포도 원형질체에 플라스미드를 형질주입하여 24시간 배양한 후 total RNA를 추출하였다. B. Realtime PCR을 이용하여 U6 프로모터 하위에 클로닝한 170 bp 길이의 gRNA fragment의 전사량을 측정하였다. 총 4개의 생물학적 반복, 2개의 기술적 반복으로 측정하였으며 애기장대 AtU6-26 프로모터 실험군에 대한 상대값으로 나타내었음. 별표는 t-검정에 의한 유의확률(p-value)에 따라 표현한 것으로 *는 5%, **는 1%의 유의확률을 나타냄. C. Realtime PCR에서 증폭할 RNA transcript의 서열 구조와 프라이머 위치. D. Realtime PCR 종료 후, Melting curve analysis를 수행한 결과. gRNA-transcript와 reference transcript가 각각 단일 피크로 증폭되었음을 확인하였다
 표
IDAA 분석: 아그로박테리움으로 형질전환된 crMADS5-1493.1599D의 4개의 캘러스 군집 (crM5-4-1부터 4)의 InDel 유전형 야생형 증폭 DNA 크기는 348 bp이다. 파란색 크로마토그램이 6FAM으로 표지된 PCR 증폭 DNA이고, 주황색 크로마토그램은 GeneScan™ 500 LIZ™ dye Size Standard (ThermoFisher Scientific) 마커이다. 윗쪽의 상자는 crM5-4-1 시료에서 빈도가 높은 크기 영역의 피크를 확대하여 제시하였다. 가장 아래 쪽에 마커 피크의 크기를 표시하였다
표
IDAA 분석: 아그로박테리움으로 형질전환된 crMADS5-1493.1599D의 4개의 캘러스 군집 (crM5-4-1부터 4)의 InDel 유전형 야생형 증폭 DNA 크기는 348 bp이다. 파란색 크로마토그램이 6FAM으로 표지된 PCR 증폭 DNA이고, 주황색 크로마토그램은 GeneScan™ 500 LIZ™ dye Size Standard (ThermoFisher Scientific) 마커이다. 윗쪽의 상자는 crM5-4-1 시료에서 빈도가 높은 크기 영역의 피크를 확대하여 제시하였다. 가장 아래 쪽에 마커 피크의 크기를 표시하였다
 표
Comparison of workflows for variant discovery from grape genome sequencing data. a Workflows of HaplotypeCaller-based variant calling pipeline similar to the GATK Best Practices and UnifiedGenotyper-based variant calling pipeline. b Distribution of the depth of coverage (DP) per site from each of our grape accessions in raw SNP calling data obtained through Genotype GVCFs using the Haplotype Caller-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. c Distribution of the DP per site from each of our grape accessions in raw SNP calling data obtained through Unified Genotyper using the Unified Genotyper-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. Accessions with relatively higher DP per site are Cannonau (V. vinifera) and Suffolk Red (hybrid). d Genotype concordance rate of SNPs called by the GenotypeGVCFs with SNPs called by the UnifiedGenotyper in each of grape accessions. Only the SNPs that shared the grape reference genome coordinates were compared. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Comparison of workflows for variant discovery from grape genome sequencing data. a Workflows of HaplotypeCaller-based variant calling pipeline similar to the GATK Best Practices and UnifiedGenotyper-based variant calling pipeline. b Distribution of the depth of coverage (DP) per site from each of our grape accessions in raw SNP calling data obtained through Genotype GVCFs using the Haplotype Caller-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. c Distribution of the DP per site from each of our grape accessions in raw SNP calling data obtained through Unified Genotyper using the Unified Genotyper-based pipeline. Vitis vinifera, interspecific grape hybrids, and wild relative species are shown by green, blue, and orange lines. Accessions with relatively higher DP per site are Cannonau (V. vinifera) and Suffolk Red (hybrid). d Genotype concordance rate of SNPs called by the GenotypeGVCFs with SNPs called by the UnifiedGenotyper in each of grape accessions. Only the SNPs that shared the grape reference genome coordinates were compared. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Grape population structure. a Population structure of 34 grape accessions estimated by fastSTRUCTURE. Each color represents one ancestral population. Each accession is represented by a vertical bar, and the length of colored segment in each vertical bar represents the proportion contributed by ancestral populations. b Principal components of SNP variation in grape accessions using whole-genome SNP data. The plots show the first three principal components. Vitis vinifera, interspecific hybrids, and wild relatives are shown by green, red, and blue dots, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Grape population structure. a Population structure of 34 grape accessions estimated by fastSTRUCTURE. Each color represents one ancestral population. Each accession is represented by a vertical bar, and the length of colored segment in each vertical bar represents the proportion contributed by ancestral populations. b Principal components of SNP variation in grape accessions using whole-genome SNP data. The plots show the first three principal components. Vitis vinifera, interspecific hybrids, and wild relatives are shown by green, red, and blue dots, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Phylogeny of grape. a Neighbor-joining phylogenetic tree of 34 grape nuclear genomes constructed using the 5,373,452 high-quality SNPs called from whole genome resequencing data. Accessions in the Neighbor-joining tree are represented by different colors: Vitis vinifera (red), interspecific hybrids (blue), and wild relatives (black). Group of wine grape accessions is indicated to emphasize their unique pedigree in this tree. Seedless accessions are in italic. b The tree constructed using 1,744 SNPs from 100-kb chromosomal region that contains the SDI locus in the central position. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are represented by black letters and seedless accessions represented by red letters. V. vinifera accessions are in italic. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Phylogeny of grape. a Neighbor-joining phylogenetic tree of 34 grape nuclear genomes constructed using the 5,373,452 high-quality SNPs called from whole genome resequencing data. Accessions in the Neighbor-joining tree are represented by different colors: Vitis vinifera (red), interspecific hybrids (blue), and wild relatives (black). Group of wine grape accessions is indicated to emphasize their unique pedigree in this tree. Seedless accessions are in italic. b The tree constructed using 1,744 SNPs from 100-kb chromosomal region that contains the SDI locus in the central position. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are represented by black letters and seedless accessions represented by red letters. V. vinifera accessions are in italic. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Curves of linkage disequilibrium decay patterns determined by squared correlations of allele frequencies (r2) against distance between polymorphic sites in 20 Vitis vinefera (red) and eight interspecific hybrid (blue) grape accessions. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Curves of linkage disequilibrium decay patterns determined by squared correlations of allele frequencies (r2) against distance between polymorphic sites in 20 Vitis vinefera (red) and eight interspecific hybrid (blue) grape accessions. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Genome-wide likelihood (XP-CLR) values for selection of seedlessness for seedless grape relatives to seeded grape accessions in 5-kb windows across the genome. The chromosome number is indicated along the x-axis. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the minor seedless-regulating QTL and AGL11 associated with a major dominant QTL, which were predicted based on this XP-CLR analysis as well as logistic association and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Genome-wide likelihood (XP-CLR) values for selection of seedlessness for seedless grape relatives to seeded grape accessions in 5-kb windows across the genome. The chromosome number is indicated along the x-axis. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the minor seedless-regulating QTL and AGL11 associated with a major dominant QTL, which were predicted based on this XP-CLR analysis as well as logistic association and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Manhattan plots of selective sweep regions for selection of seedlessness inferred from FST (upper panel) and of seedlessness genome-wide logistic association scans using GENESIS (lower panel). The red line marks the regions at the top 0.5% of FST values. The -log10 P values from a genome-wide scan are plotted against the position on each of the 19 grape chromosomes. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the recessive seedless-regulating genes and VviAGL11 associated with a dominant gene, which were predicted based on FST and GENESIS analyses as well as XP-CLR and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Manhattan plots of selective sweep regions for selection of seedlessness inferred from FST (upper panel) and of seedlessness genome-wide logistic association scans using GENESIS (lower panel). The red line marks the regions at the top 0.5% of FST values. The -log10 P values from a genome-wide scan are plotted against the position on each of the 19 grape chromosomes. Chromosomal locations of Vitvi01g00455, Vitvi08g01528, and Vitvi18g01237 associated with the recessive seedless-regulating genes and VviAGL11 associated with a dominant gene, which were predicted based on FST and GENESIS analyses as well as XP-CLR and SIFT (Sorting Intolerant From Tolerant) analyses, are indicated by * and ▼, respectively. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
 표
Genetic features for the candidate causal genes for minor recessive seedless-regulating candidate selective sweeps. Coding sequence structures of Vitvi01g00455 (a), Vitvi08g01528 (b), and Vitvi18g01237 (c) and genotype distributions of candidate causal SNPs in these genes for 15 seedless and 13 seeded grape accessions tested. Reference homozygous genotype is indicated by 0/0, heterozygous 0/1, non-reference homozygous 1/1, and missing ./.. Amino acid positions are indicated by numbers. Neighbor-joining phylogenetic trees of 17 seedless and 14 seeded accessions constructed using 1,744 SNPs, 939 SNPs, and 871 SNPs from 100-kb chromosomal regions that contains the Vitvi01g00455 (d), Vitvi08g01528 (e), and Vitvi18g01237 (f) genes in their central position, respectively. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are in green, seedless accessions in purple, and two wild relatives in black. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
표
Genetic features for the candidate causal genes for minor recessive seedless-regulating candidate selective sweeps. Coding sequence structures of Vitvi01g00455 (a), Vitvi08g01528 (b), and Vitvi18g01237 (c) and genotype distributions of candidate causal SNPs in these genes for 15 seedless and 13 seeded grape accessions tested. Reference homozygous genotype is indicated by 0/0, heterozygous 0/1, non-reference homozygous 1/1, and missing ./.. Amino acid positions are indicated by numbers. Neighbor-joining phylogenetic trees of 17 seedless and 14 seeded accessions constructed using 1,744 SNPs, 939 SNPs, and 871 SNPs from 100-kb chromosomal regions that contains the Vitvi01g00455 (d), Vitvi08g01528 (e), and Vitvi18g01237 (f) genes in their central position, respectively. Percentages higher than 60 based on 1000 bootstrap replicates are shown above branches. Seeded grape accessions are in green, seedless accessions in purple, and two wild relatives in black. From Kim et al. (2020) G3: Genes, Genome, Genetics 10: 3365-3377
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.