최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 한국생명공학연구원 Korea Research Institute of Bioscience and Biotechnology |
|---|---|
| 연구책임자 | 송재준 |
| 참여연구자 | 최종현 , 고경철 , 한윤전 , 김진선 , 정대은 , 이빛나 , 전호근 |
| 보고서유형 | 2단계보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2013-07 |
| 과제시작연도 | 2012 |
| 주관부처 | 미래창조과학부 KA |
| 사업 관리 기관 | 한국연구재단 |
| 등록번호 | TRKO201300035539 |
| 과제고유번호 | 1345174605 |
| DB 구축일자 | 2013-12-21 |
| 키워드 | 초고속 탐색 시스템,메타게놈,신규효소,생물학적 통합분석 시스템,라이브러리,유세포 분석기HTS,Metagenome,Novel Enzyme,Bio-TAS,Library,FACS |
본 연구는 HTS기반 초고속 효소탐색 다중기술 개발 및 시스템 통합을 위한 기반 구축과 이를 통한 활용 기술확대를 목적으로 하고 있음.
● 본 연구를 통하여 다양한 환경에서 존재하는 신규 미생물/메타게놈 자원 확보 및 난배양성 회소 미생물에 대한 단일 세포 유래 미생물 유전체 확보 기술을 개발하였음.
● 최초로 FACS와 FISH 기술을 융합하여 희소미생물 분리 방법을 개발하였으며, 이렇게 분리된 회소미생물을 단일 세포 기반 유전체증폭기술(MDA)을 이용한 신규 효소 탐색을 위한 유전체 라이브러리 제조하였음.
● 2
본 연구는 HTS기반 초고속 효소탐색 다중기술 개발 및 시스템 통합을 위한 기반 구축과 이를 통한 활용 기술확대를 목적으로 하고 있음.
● 본 연구를 통하여 다양한 환경에서 존재하는 신규 미생물/메타게놈 자원 확보 및 난배양성 회소 미생물에 대한 단일 세포 유래 미생물 유전체 확보 기술을 개발하였음.
● 최초로 FACS와 FISH 기술을 융합하여 희소미생물 분리 방법을 개발하였으며, 이렇게 분리된 회소미생물을 단일 세포 기반 유전체증폭기술(MDA)을 이용한 신규 효소 탐색을 위한 유전체 라이브러리 제조하였음.
● 2종 이상의 효소를 다중 동시 활성 측정하는 새로운 기술을 개발하였음.
● ORFome 라이브러리로부터 형광단백질을 활성 리포터로 채용한 HTS 기반 coupling assay를 통한 다양한 신규 dehydrogenase/oxidoreductase 발굴하였음.
● 다양한 기질 디자인을 통하여 흡광/형광 방법을 이용하여 빠르고 쉽고 정확하게 다양한 효소의 활성 측정 및 탐색기술을 개발함.
● 단일세포수준의 미생물 균체 캡슐화 기술과 Bio-TAS 기술의 통합하였음
● 위의 개발 기술과 HTS를 연동하여 glucansucrase, cellulase, protease, xylanase, lipase, exocellulase, esterase 등 다양한 10종류 이상의 효소를 분석할 수 있는 기술과 각 효소를 확보하여 특성을 파악하였으며, 특성 분석을 통한 HTS 이용 개량 기술을 확보하였음.
It is well known that increasing number of drug intermediates and industrial chemicals are manufactured by biocatalytic processes. A key factor for those processes is the availability of useful enzymes with the necessary activity, specificity and stability under operational conditions. Over the past
It is well known that increasing number of drug intermediates and industrial chemicals are manufactured by biocatalytic processes. A key factor for those processes is the availability of useful enzymes with the necessary activity, specificity and stability under operational conditions. Over the past few decades, many enzymes were screened from the pure cultured microorganisms using activity based screening method. However, it is very difficult to screen a novel enzyme from environment due to the limitation of resources and screening methods. More than 99% of microbes in the environment cannot be easily cultivated. "Metagenomics", which is the genomic analysis of the microbial community attempts to overcome un-culturability. In general, the diversity of metagenomic libraries was affected by abundance of bacteria in environmental sample. Therefore the research of minor microbial texa in environmental samples remains the biggest challenge.
A new strategy for enrichment of rare bacteria from environmental samples was developed. Fosmid library could be efficiently generated from rare single cell, which is screened by combining Fluorescence in situ hybridization (FISH), Fluorescence associated cell sorter (FACS) and Multiple displacement amplification (MDA) technique from minor bacterial pools. We could optimize condition for whole genome amplification based on MDA from rare single microorganism, and construct fosmid libraries from MDA products derived from two different rare single cells. As a result, we could generate 130,000 of fosmid clones having an average insert size of 32 kb, ranging from 27 to 40 kb. We also could screen 26 and 15 clones showing protease and cellulase activity, respectively. This is considerably valuable to generate metagenomic libraries from unculturable rare single microorganisms in various environmental conditions, and moreover helps to screen novel enzymes for white biotechnological applications.
 표
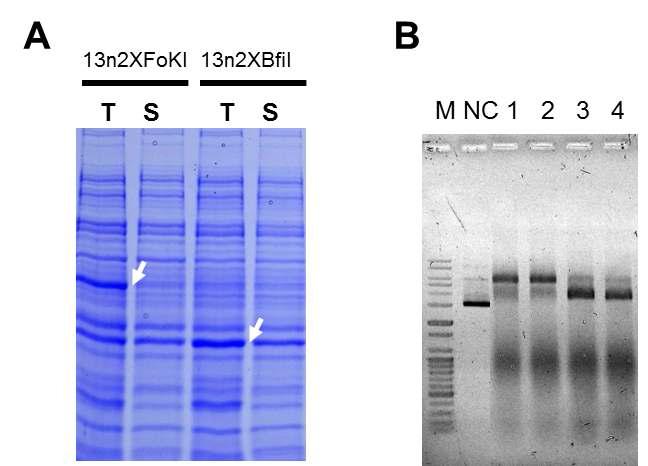
단량체로 융합된 활성영역의 발현 및 활성. (A) (GGGGS)×13 linker를 이용하여 2량체의 FokI(2(13n)×FokI) 와 BfiI(2(13n)×BfiII)를 단량체로 융합한 활성영역의 전체 단백질(T)과 가용성 단백질량(S)을 나타낸다. (B)는 단량체로 융합한 두 인공 제한효소의 활성을 확인한 것이다. 활성 완충용액 (33 mM Tris-acetate, 66 mM Potassium acetate, 10 mM Magnessium acetate, pH 7.9, 37℃)에 (A)의 가용성 단백질과 pGFPuv를 혼합하여 37℃에서 30분간 반응시켜 agarose gel에서 전기 영동한 것이다. NC는 활성 완충용액만, 1과 2는 13n2×FokI를 포함한 재조합 균주의 파쇄액, 3 과 4는 13n2×BfiI를 포함한 재조합 균주의 파쇄액을 첨가한 것이다.
표
단량체로 융합된 활성영역의 발현 및 활성. (A) (GGGGS)×13 linker를 이용하여 2량체의 FokI(2(13n)×FokI) 와 BfiI(2(13n)×BfiII)를 단량체로 융합한 활성영역의 전체 단백질(T)과 가용성 단백질량(S)을 나타낸다. (B)는 단량체로 융합한 두 인공 제한효소의 활성을 확인한 것이다. 활성 완충용액 (33 mM Tris-acetate, 66 mM Potassium acetate, 10 mM Magnessium acetate, pH 7.9, 37℃)에 (A)의 가용성 단백질과 pGFPuv를 혼합하여 37℃에서 30분간 반응시켜 agarose gel에서 전기 영동한 것이다. NC는 활성 완충용액만, 1과 2는 13n2×FokI를 포함한 재조합 균주의 파쇄액, 3 과 4는 13n2×BfiI를 포함한 재조합 균주의 파쇄액을 첨가한 것이다.
 표
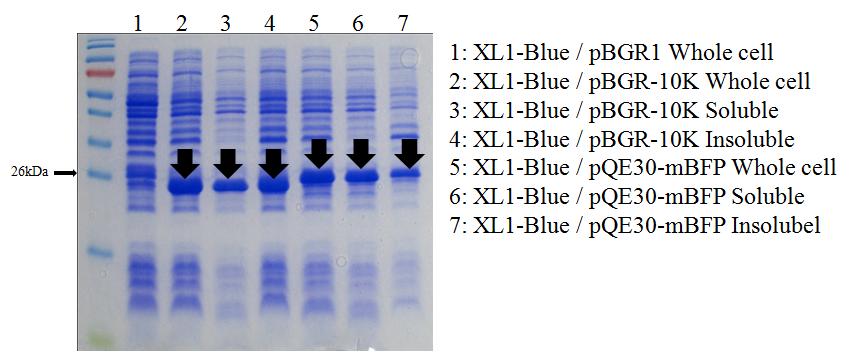
SDS-PAGE를 통한 mBFP 발현량 분석. LB배지에서 별도의 유도제 첨가 없이 발현시킨 mBFP를 SDS-PAGE로 분석하였다. 1은 대조군으로서 pBGRI을 갖는 대장균 전체 단백질이며, 2는 메타게놈에서 발굴한 mBFP가 포함된 pBGRI을 지닌 대장균 전체 단백질이고, 3은 초음파 분쇄 후 원심 분리하여 얻은 가용성 단백질을 나타내며, 4는 원심 분리로 회수된 불용성 단백질이다. 5는 아미노 말단에 6X histidine이 융합된 mBFP를 지닌 대장균전체 단백질이며, 6은 초음파 분쇄와 원심 분리 후 얻은 가용성 단백질이고, 7은 원심 분리로 회수한 불용성 단백질을 전기 영동한 것이다.
표
SDS-PAGE를 통한 mBFP 발현량 분석. LB배지에서 별도의 유도제 첨가 없이 발현시킨 mBFP를 SDS-PAGE로 분석하였다. 1은 대조군으로서 pBGRI을 갖는 대장균 전체 단백질이며, 2는 메타게놈에서 발굴한 mBFP가 포함된 pBGRI을 지닌 대장균 전체 단백질이고, 3은 초음파 분쇄 후 원심 분리하여 얻은 가용성 단백질을 나타내며, 4는 원심 분리로 회수된 불용성 단백질이다. 5는 아미노 말단에 6X histidine이 융합된 mBFP를 지닌 대장균전체 단백질이며, 6은 초음파 분쇄와 원심 분리 후 얻은 가용성 단백질이고, 7은 원심 분리로 회수한 불용성 단백질을 전기 영동한 것이다.
 표
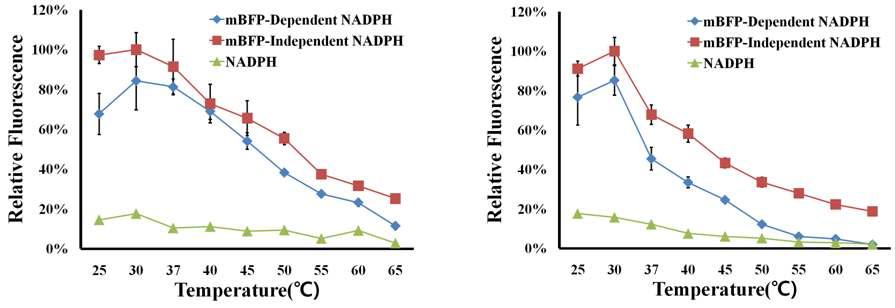
mBFP의 최적 온도 분석과 열안정성 분석. (좌)는 다양한 온도에서 형광 단백질을 10분간 정치 후 형광 세기를 측정한 것이다. (우)는 각 온도에서 1시간 동안 처리하고 4℃에서 10분간 정치 후에 다시 형광을 측정하였다. mBFP-dependent NADPH는 mBFP에 해당 온도를 적용 후, 형광 세기의 측정 직전에 첨가한 것이며, mBFP-independent NADPH는 mBFP과 함께 각각의 온도에서 10분간 처리 후에 측정한 것을 나타낸 것이다. NADPH는 해당 온도에서 처리된 NADPH의 형광 세기를 나타낸다.
표
mBFP의 최적 온도 분석과 열안정성 분석. (좌)는 다양한 온도에서 형광 단백질을 10분간 정치 후 형광 세기를 측정한 것이다. (우)는 각 온도에서 1시간 동안 처리하고 4℃에서 10분간 정치 후에 다시 형광을 측정하였다. mBFP-dependent NADPH는 mBFP에 해당 온도를 적용 후, 형광 세기의 측정 직전에 첨가한 것이며, mBFP-independent NADPH는 mBFP과 함께 각각의 온도에서 10분간 처리 후에 측정한 것을 나타낸 것이다. NADPH는 해당 온도에서 처리된 NADPH의 형광 세기를 나타낸다.
 표
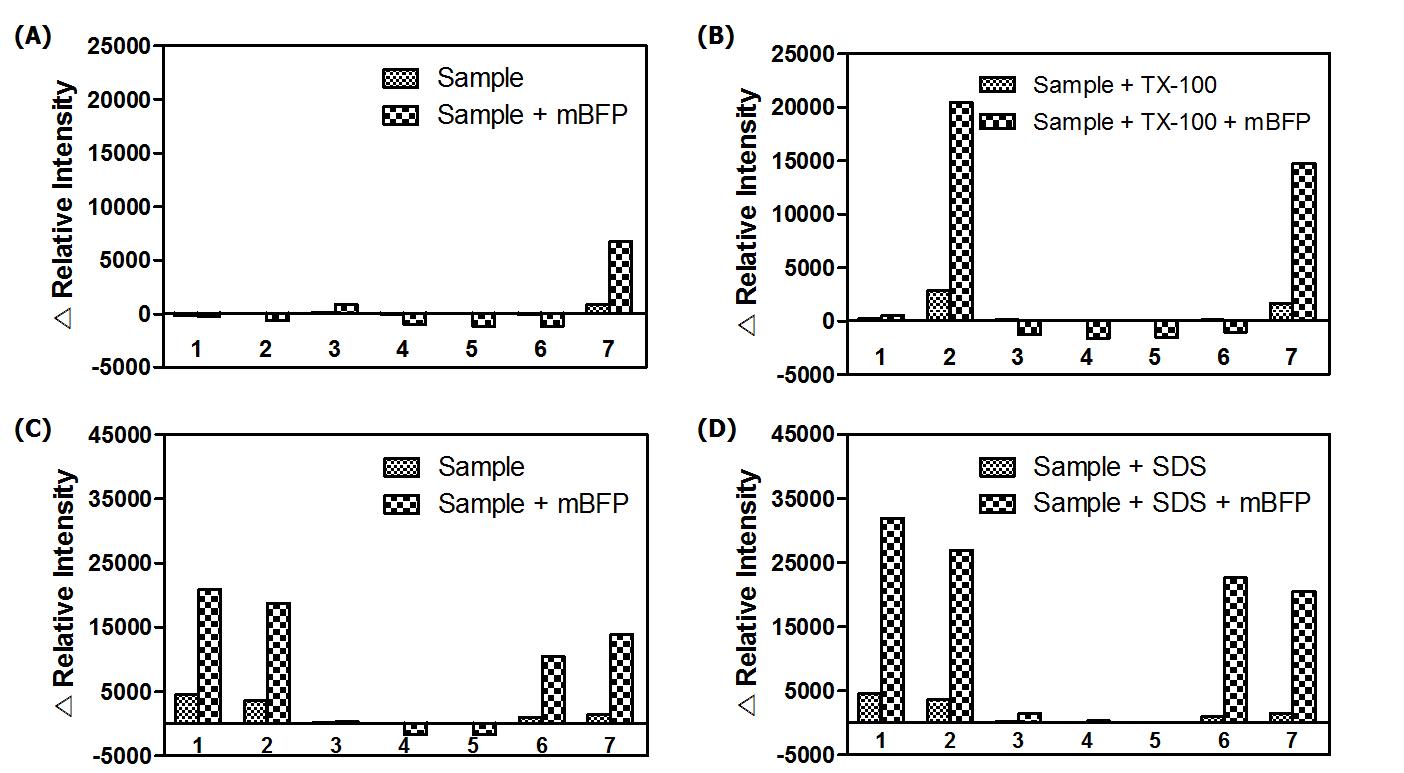
세포의 NADPH 의존 효소 활성 검출을 위한 계면활성제 채용. 포도당 6-인산(glucose 6-phosphate)을 첨가하여 균주 내 관련 효소 활성을 계면 활성제 없이 측정한 형광 변화 값 (A)과 0.01%(w/v) Triton X-100을 첨가한 측정값(B). 대조군으로 초음파분쇄기를 이용하여 세포를 파쇄 한 후, 측정(C)한 것과 파쇄액에 이온 계면 활성제 SDS를 첨가하여 측정(D)한 밧을 같이 도시하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
표
세포의 NADPH 의존 효소 활성 검출을 위한 계면활성제 채용. 포도당 6-인산(glucose 6-phosphate)을 첨가하여 균주 내 관련 효소 활성을 계면 활성제 없이 측정한 형광 변화 값 (A)과 0.01%(w/v) Triton X-100을 첨가한 측정값(B). 대조군으로 초음파분쇄기를 이용하여 세포를 파쇄 한 후, 측정(C)한 것과 파쇄액에 이온 계면 활성제 SDS를 첨가하여 측정(D)한 밧을 같이 도시하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
 표
HTS format 으로 세포 효소활성 측정을 위한 기질 농도 분석. 균주 내 포도당-6 인산 탈수소효소 활성을 측정하기 위해 포도당 6-인산(glucose 6-phosphate)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
표
HTS format 으로 세포 효소활성 측정을 위한 기질 농도 분석. 균주 내 포도당-6 인산 탈수소효소 활성을 측정하기 위해 포도당 6-인산(glucose 6-phosphate)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
 표
전세포를 이용한 만니톨과 L-글루탐산에 대한 효소 활성 측정. 각각 1 mM 만니톨(좌), L-글루탐산(우)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100를 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
표
전세포를 이용한 만니톨과 L-글루탐산에 대한 효소 활성 측정. 각각 1 mM 만니톨(좌), L-글루탐산(우)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100를 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
 표
균주 내 글루타치온에 의한 효소 활성 형광 측정. 글루타치온 환원효소 활성을 측정하기 위해 2 mM 글루타치온과 0.02(좌), 2(우) mM NADPH, 0.2%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)을 37℃에서 10분간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
표
균주 내 글루타치온에 의한 효소 활성 형광 측정. 글루타치온 환원효소 활성을 측정하기 위해 2 mM 글루타치온과 0.02(좌), 2(우) mM NADPH, 0.2%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)을 37℃에서 10분간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
 표
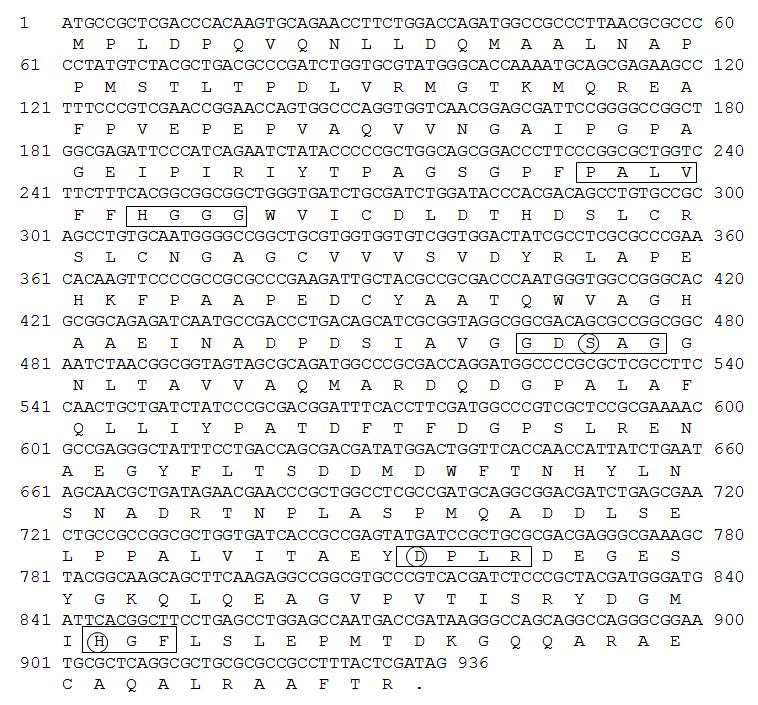
The nucleotide sequence of the EST1 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of EST1 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser166, Asp252, and His302 of lipases/esterases are indicated in bold with a circle.
표
The nucleotide sequence of the EST1 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of EST1 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser166, Asp252, and His302 of lipases/esterases are indicated in bold with a circle.
 표
The nucleotide sequence of the Fos6 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of Fos6 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser177, Asp274, and His304 of lipases/esterases are indicated in bold with a circle.
표
The nucleotide sequence of the Fos6 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of Fos6 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser177, Asp274, and His304 of lipases/esterases are indicated in bold with a circle.
 표
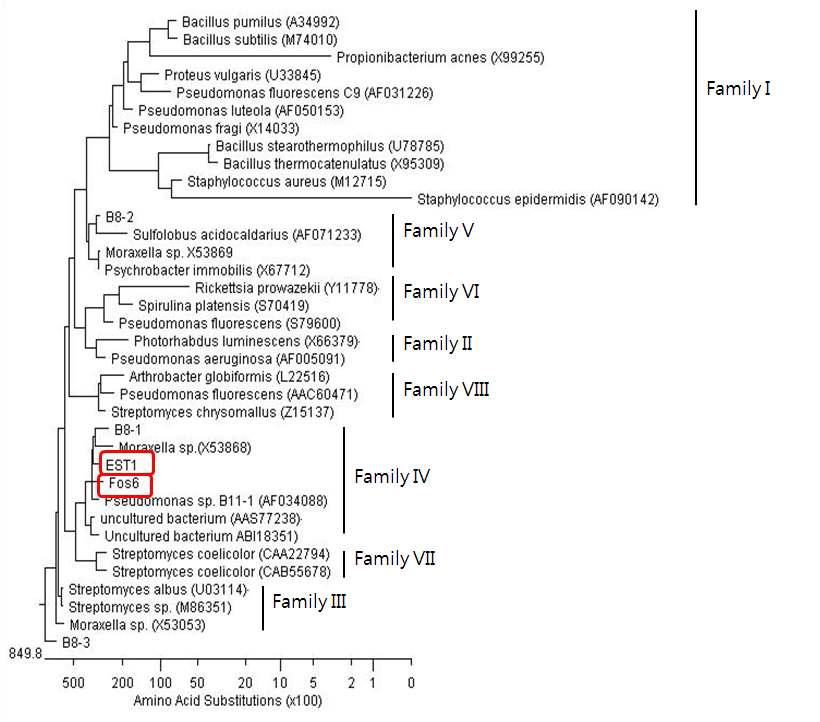
Phylogenetic tree of isolated gene. Phylogenetic analysis was performed using the program MEGALIGN (DNASTAR). Except for EST1, the protein sequences for previously identified families of bacterial lipolytic enzymes were retrieved from GenBank (http://www.ncbi.nlm.nih.gov). The units at the bottom of the tree indicate the number of substitution events.
표
Phylogenetic tree of isolated gene. Phylogenetic analysis was performed using the program MEGALIGN (DNASTAR). Except for EST1, the protein sequences for previously identified families of bacterial lipolytic enzymes were retrieved from GenBank (http://www.ncbi.nlm.nih.gov). The units at the bottom of the tree indicate the number of substitution events.
 표
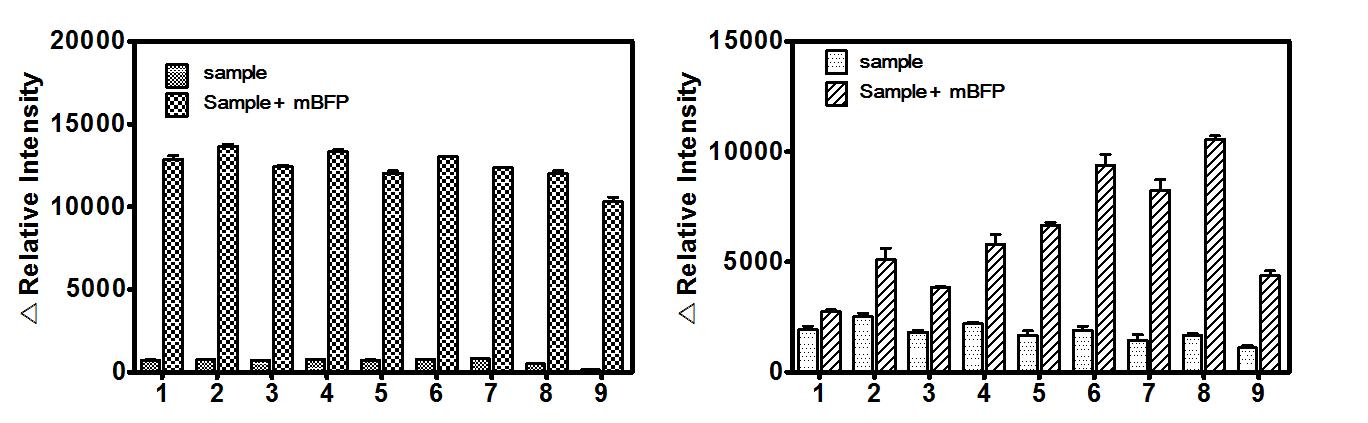
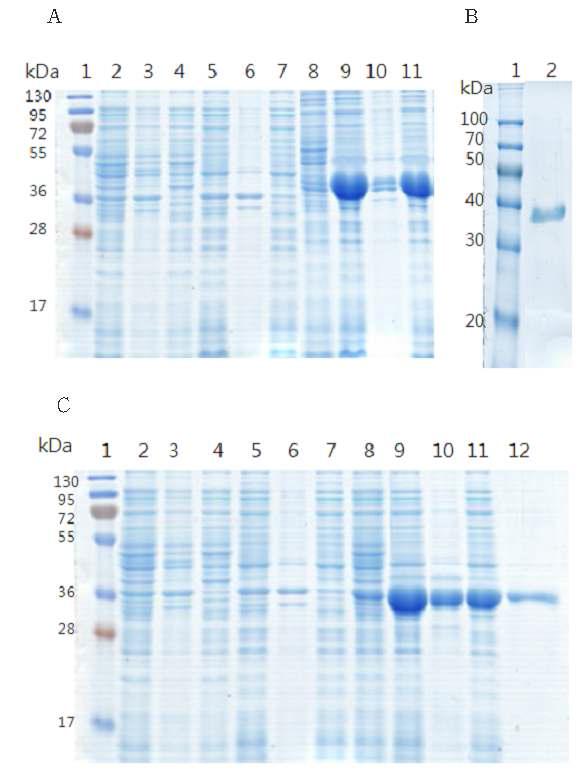
SDS– PAGE analysis of the purified EST1 (A, B) and Fos6 (C). (A) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector, 7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate. (B) 1. molecular mass marker, 2. purified EST1 protein. (C) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector,7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate 12 purified protein.
표
SDS– PAGE analysis of the purified EST1 (A, B) and Fos6 (C). (A) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector, 7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate. (B) 1. molecular mass marker, 2. purified EST1 protein. (C) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector,7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate 12 purified protein.
 표
단량체로 융합된 활성영역의 발현 및 활성. (A) (GGGGS)×13 linker를 이용하여 2량체의 FokI(2(13n)×FokI) 와 BfiI(2(13n)×BfiII)를 단량체로 융합한 활성영역의 전체 단백질(T)과 가용성 단백질량(S)을 나타낸다. (B)는 단량체로 융합한 두 인공 제한효소의 활성을 확인한 것이다. 활성 완충용액 (33 mM Tris-acetate, 66 mM Potassium acetate, 10 mM Magnessium acetate, pH 7.9, 37℃)에 (A)의 가용성 단백질과 pGFPuv를 혼합하여 37℃에서 30분간 반응시켜 agarose gel에서 전기 영동한 것이다. NC는 활성 완충용액만, 1과 2는 13n2×FokI를 포함한 재조합 균주의 파쇄액, 3 과 4는 13n2×BfiI를 포함한 재조합 균주의 파쇄액을 첨가한 것이다.
표
단량체로 융합된 활성영역의 발현 및 활성. (A) (GGGGS)×13 linker를 이용하여 2량체의 FokI(2(13n)×FokI) 와 BfiI(2(13n)×BfiII)를 단량체로 융합한 활성영역의 전체 단백질(T)과 가용성 단백질량(S)을 나타낸다. (B)는 단량체로 융합한 두 인공 제한효소의 활성을 확인한 것이다. 활성 완충용액 (33 mM Tris-acetate, 66 mM Potassium acetate, 10 mM Magnessium acetate, pH 7.9, 37℃)에 (A)의 가용성 단백질과 pGFPuv를 혼합하여 37℃에서 30분간 반응시켜 agarose gel에서 전기 영동한 것이다. NC는 활성 완충용액만, 1과 2는 13n2×FokI를 포함한 재조합 균주의 파쇄액, 3 과 4는 13n2×BfiI를 포함한 재조합 균주의 파쇄액을 첨가한 것이다.
 표
SDS-PAGE를 통한 mBFP 발현량 분석. LB배지에서 별도의 유도제 첨가 없이 발현시킨 mBFP를 SDS-PAGE로 분석하였다. 1은 대조군으로서 pBGRI을 갖는 대장균 전체 단백질이며, 2는 메타게놈에서 발굴한 mBFP가 포함된 pBGRI을 지닌 대장균 전체 단백질이고, 3은 초음파 분쇄 후 원심 분리하여 얻은 가용성 단백질을 나타내며, 4는 원심 분리로 회수된 불용성 단백질이다. 5는 아미노 말단에 6X histidine이 융합된 mBFP를 지닌 대장균전체 단백질이며, 6은 초음파 분쇄와 원심 분리 후 얻은 가용성 단백질이고, 7은 원심 분리로 회수한 불용성 단백질을 전기 영동한 것이다.
표
SDS-PAGE를 통한 mBFP 발현량 분석. LB배지에서 별도의 유도제 첨가 없이 발현시킨 mBFP를 SDS-PAGE로 분석하였다. 1은 대조군으로서 pBGRI을 갖는 대장균 전체 단백질이며, 2는 메타게놈에서 발굴한 mBFP가 포함된 pBGRI을 지닌 대장균 전체 단백질이고, 3은 초음파 분쇄 후 원심 분리하여 얻은 가용성 단백질을 나타내며, 4는 원심 분리로 회수된 불용성 단백질이다. 5는 아미노 말단에 6X histidine이 융합된 mBFP를 지닌 대장균전체 단백질이며, 6은 초음파 분쇄와 원심 분리 후 얻은 가용성 단백질이고, 7은 원심 분리로 회수한 불용성 단백질을 전기 영동한 것이다.
 표
mBFP의 최적 온도 분석과 열안정성 분석. (좌)는 다양한 온도에서 형광 단백질을 10분간 정치 후 형광 세기를 측정한 것이다. (우)는 각 온도에서 1시간 동안 처리하고 4℃에서 10분간 정치 후에 다시 형광을 측정하였다. mBFP-dependent NADPH는 mBFP에 해당 온도를 적용 후, 형광 세기의 측정 직전에 첨가한 것이며, mBFP-independent NADPH는 mBFP과 함께 각각의 온도에서 10분간 처리 후에 측정한 것을 나타낸 것이다. NADPH는 해당 온도에서 처리된 NADPH의 형광 세기를 나타낸다.
표
mBFP의 최적 온도 분석과 열안정성 분석. (좌)는 다양한 온도에서 형광 단백질을 10분간 정치 후 형광 세기를 측정한 것이다. (우)는 각 온도에서 1시간 동안 처리하고 4℃에서 10분간 정치 후에 다시 형광을 측정하였다. mBFP-dependent NADPH는 mBFP에 해당 온도를 적용 후, 형광 세기의 측정 직전에 첨가한 것이며, mBFP-independent NADPH는 mBFP과 함께 각각의 온도에서 10분간 처리 후에 측정한 것을 나타낸 것이다. NADPH는 해당 온도에서 처리된 NADPH의 형광 세기를 나타낸다.
 표
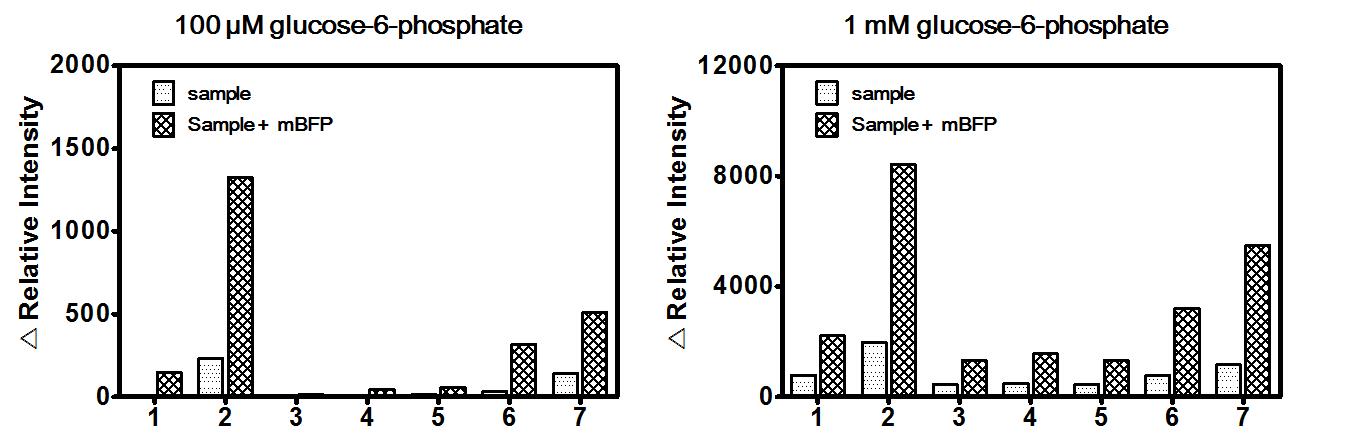
세포의 NADPH 의존 효소 활성 검출을 위한 계면활성제 채용. 포도당 6-인산(glucose 6-phosphate)을 첨가하여 균주 내 관련 효소 활성을 계면 활성제 없이 측정한 형광 변화 값 (A)과 0.01%(w/v) Triton X-100을 첨가한 측정값(B). 대조군으로 초음파분쇄기를 이용하여 세포를 파쇄 한 후, 측정(C)한 것과 파쇄액에 이온 계면 활성제 SDS를 첨가하여 측정(D)한 밧을 같이 도시하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
표
세포의 NADPH 의존 효소 활성 검출을 위한 계면활성제 채용. 포도당 6-인산(glucose 6-phosphate)을 첨가하여 균주 내 관련 효소 활성을 계면 활성제 없이 측정한 형광 변화 값 (A)과 0.01%(w/v) Triton X-100을 첨가한 측정값(B). 대조군으로 초음파분쇄기를 이용하여 세포를 파쇄 한 후, 측정(C)한 것과 파쇄액에 이온 계면 활성제 SDS를 첨가하여 측정(D)한 밧을 같이 도시하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
 표
HTS format 으로 세포 효소활성 측정을 위한 기질 농도 분석. 균주 내 포도당-6 인산 탈수소효소 활성을 측정하기 위해 포도당 6-인산(glucose 6-phosphate)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
표
HTS format 으로 세포 효소활성 측정을 위한 기질 농도 분석. 균주 내 포도당-6 인산 탈수소효소 활성을 측정하기 위해 포도당 6-인산(glucose 6-phosphate)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, Candida albicaus 2, Bacillus subtillis 3, Staphylococcus aureus 4, Corynebacterium ammoniagenes 5, Corynebacterium glutamicum 6, Salmonella typhimurium 7, Escherichia coli 이다.
 표
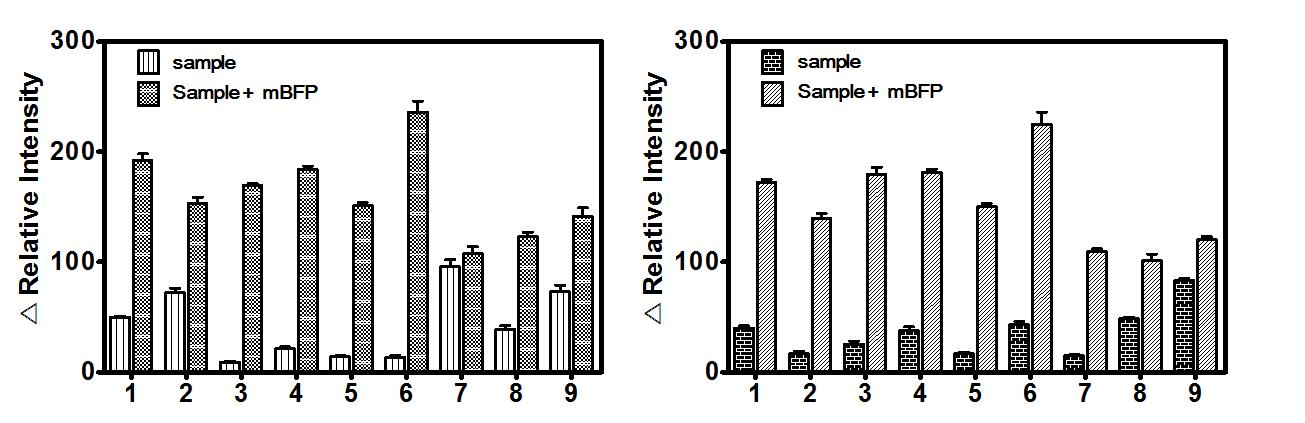
전세포를 이용한 만니톨과 L-글루탐산에 대한 효소 활성 측정. 각각 1 mM 만니톨(좌), L-글루탐산(우)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100를 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
표
전세포를 이용한 만니톨과 L-글루탐산에 대한 효소 활성 측정. 각각 1 mM 만니톨(좌), L-글루탐산(우)과 0.2 mM NADP+, 0.01%(w/v) Triton X-100를 포함하는 50mM Tris-HCl 완충용액(pH 7.5)에 배양된 균주를 첨가하여 37℃에서 한시간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
 표
균주 내 글루타치온에 의한 효소 활성 형광 측정. 글루타치온 환원효소 활성을 측정하기 위해 2 mM 글루타치온과 0.02(좌), 2(우) mM NADPH, 0.2%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)을 37℃에서 10분간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
표
균주 내 글루타치온에 의한 효소 활성 형광 측정. 글루타치온 환원효소 활성을 측정하기 위해 2 mM 글루타치온과 0.02(좌), 2(우) mM NADPH, 0.2%(w/v) Triton X-100을 포함하는 50mM Tris-HCl 완충용액(pH 7.5)을 37℃에서 10분간 반응시켜 형광 변화 값을 측정하였다. 사용된 균주는 1, E.coli 2, Staphylococcus aureus 3, Salmonella typhimurium 4, Corynebacterium glutamicum 5, Bacillus subtillis 6, Sinorhizobium meliloti 7, Corynebacterium ammoniagenes 8, Candida albicaus 9, Propionibacterium acnes 이다.
 표
The nucleotide sequence of the EST1 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of EST1 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser166, Asp252, and His302 of lipases/esterases are indicated in bold with a circle.
표
The nucleotide sequence of the EST1 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of EST1 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser166, Asp252, and His302 of lipases/esterases are indicated in bold with a circle.
 표
The nucleotide sequence of the Fos6 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of Fos6 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser177, Asp274, and His304 of lipases/esterases are indicated in bold with a circle.
표
The nucleotide sequence of the Fos6 esterase gene from the metagenome indicated in boldface with a box. library. The predicted amino acid sequence of Fos6 is given below the nucleotide sequence in the standard one-letter code. An asterisk denotes the stop codon. The conserved motifs of HGGG, GxSxG, and the putative catalytic triad residues composed of Ser177, Asp274, and His304 of lipases/esterases are indicated in bold with a circle.
 표
Phylogenetic tree of isolated gene. Phylogenetic analysis was performed using the program MEGALIGN (DNASTAR). Except for EST1, the protein sequences for previously identified families of bacterial lipolytic enzymes were retrieved from GenBank (http://www.ncbi.nlm.nih.gov). The units at the bottom of the tree indicate the number of substitution events.
표
Phylogenetic tree of isolated gene. Phylogenetic analysis was performed using the program MEGALIGN (DNASTAR). Except for EST1, the protein sequences for previously identified families of bacterial lipolytic enzymes were retrieved from GenBank (http://www.ncbi.nlm.nih.gov). The units at the bottom of the tree indicate the number of substitution events.
 표
SDS– PAGE analysis of the purified EST1 (A, B) and Fos6 (C). (A) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector, 7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate. (B) 1. molecular mass marker, 2. purified EST1 protein. (C) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector,7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate 12 purified protein.
표
SDS– PAGE analysis of the purified EST1 (A, B) and Fos6 (C). (A) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector, 7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate. (B) 1. molecular mass marker, 2. purified EST1 protein. (C) 1: molecular mass marker, 2. uninduced total lysate of E. coli BL21 (DE3) containing vector, 3. uninduced insouble lysate of E. coli BL21 (DE3) containing vector, 4. uninduced soluble lysate of E. coli BL21 (DE3) containing vector, 5. induced total lysate of E. coli BL21 (DE3) containing vector, 6. induced insouble lysate of E. coli BL21 (DE3) containing vector,7. induced soluble lysate of E. coli BL21 (DE3) containing vector, 8. uninduced total cell lysate, 9. induced total cell lysate, 10. induced insoluble cell lysate, 11. induced soluble cell lysate 12 purified protein.
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.