최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 국립농업과학원 National Institute of Agricultural Sciences |
|---|---|
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2014-02 |
| 과제시작연도 | 2011 |
| 주관부처 | 농촌진흥청 Rural Development Administration(RDA) |
| 등록번호 | TRKO201400010991 |
| 과제고유번호 | 1395022241 |
| 사업명 | 차세대바이오그린21 |
| DB 구축일자 | 2014-07-05 |
| DOI | https://doi.org/10.23000/TRKO201400010991 |
Ⅳ. 연구개발결과
□ 제1세부과제 : 벼흰잎마름병원균 돌연변이체를 이용한 병원성관련 유전자 발굴
○ 벼흰잎마름병원균 돌연변이체를 이용한 병원성 관련 유전자 발굴
- 벼흰잎마름병원균의 mutant pool 20,000 점 중 10,000 점을 감수성 벼 품종 IR24에 3차까지 병원성 검정을 수행하여 병원성이 현저히 감소 된 돌연변이체 280종을 선발하였다.
○ 벼흰잎마름병원균의 병원성 관련 유전자 분리 및 특성 분석
- Tail-PCR, sequencing, 그리고 southern hybridization
Ⅳ. 연구개발결과
□ 제1세부과제 : 벼흰잎마름병원균 돌연변이체를 이용한 병원성관련 유전자 발굴
○ 벼흰잎마름병원균 돌연변이체를 이용한 병원성 관련 유전자 발굴
- 벼흰잎마름병원균의 mutant pool 20,000 점 중 10,000 점을 감수성 벼 품종 IR24에 3차까지 병원성 검정을 수행하여 병원성이 현저히 감소 된 돌연변이체 280종을 선발하였다.
○ 벼흰잎마름병원균의 병원성 관련 유전자 분리 및 특성 분석
- Tail-PCR, sequencing, 그리고 southern hybridization 등을 수행하여 transposon이 transposase에 삽입된 24종과 transposon이 2개 이상 삽입된 9종을 제외하고 최종 125종이 선별되었다.
○ 병원성 소실 돌연변이체 유전정보 D/B 구축 및 등록
- 최종 선별된 125종 중 1차로 93종에 대하여 데이터베이스를 구축 및 등록하였다.
- 93종 중 42종(19 genes, 42 mutants)은 이전에 보고된 병원성 관련 유전자들에 transposon이 삽입되었으며, 17종(16 genes, 17 mutants)은 hypothetical protein, 2종(2 genes, 2 mutants)은 유전자와 유전자 사이, 그리고 32종(32 genes, 32 mutants)은 병원성 관련 유전자와 metabolism 및 cellular processes에 관련된 유전자들에 transposon이 삽입되었다.
○ 병원성 소실 관련 유전자의 기능분석 및 병 발생 기작 구명
- 병원성 소실 돌연변이체(aroK 유전자)의 식물(벼)과의 병원성 상관관계, 색소 생합성 분석, DNA-Chip 분석, Reverse Transcription (RT)-PCR 분석 등을 수행하여 동 유전자의 기능을 구명하였다.
- 병원성 소실 돌연변이체(aroC 유전자)의 식물(벼)과의 병원성 상관관계, 색소 생합성 분석, 기주내 생장률 분석, Reverse Transcription (RT)-PCR 분석 그리고 영양요구성 분석을 통해 동 유전자의 대사관련 기작을 구명하였다.
□ 제2세부과제 : 벼흰잎마름병원균 avr 유전자 기능분석 및 레이스판별 기술 활용 연구
○ 벼흰잎마름병원균 유전체내의 avr 유전자 탐색 및 분석
- Xoo KACC10331의 유전체 해독정보로부터 벼의 저항성 유전자와 상호작용 할 것으로 예상되는 avr 유전자들을 탐색하였고 총 16종의 유전자가 존재하는 것을 확인하였다.
확인된 총 16종의 avr 유전자에 대한 각각의 염기서열을 분석한 결과 이중 5종의 유전자들은 유전자 내부에 termination codon 존재하는 것을 확인하였다. 이를 바탕으로 총 16종의 유전자 중 11종의 유전자만이 실제적으로 발현될 것으로 예측하였다.
○ 벼흰잎마름병원균의 avr 유전자 삽입 및 결손 돌연변이체 제작
- avr 유전자의 기능 구명을 위해 Xoo KACC10331의 유전체로부터 avr 유전자를 분리 및 transposon을 사용하여 돌연변이체를 유발하여 marker-exchagne를 통해 삽입돌 연변이체를 제작하였다. 또한 유전자 결손 변이 균주를 제조하기 위하여 avr 유전자가 내부적으로 결손된 DNA 단편을 지니는 pK18mobsacB 벡터를 이용하여 deletion 돌연변이체를 제작하였다.
○ 식물(벼)과의 병원성 상관관계 분석
- 제작된 삽입돌연변이체 및 결손 돌연변이체들을 단인자 저항성 벼 품종 (IRBB1, 2, 3, 4, 5, 7, 8, 10, 11, 13, 14, 그리고 21)에 병원성 검정을 수행하였다. 그 결과 단인자 저항성 벼 품종들에 병원성이 보이지 않았다. 이결과 제작된 돌연변이체들 중 단인자 저항성 벼 품종들과 특이적으로 상호작용하는 mutant는 없는 것으로 나타났다.
○ 벼흰잎마름병원균 특이적 검출 및 레이스 판별을 위한 triplex-PCR kit 개발
- Xoo의 특이적 검출 및 레이스판별을 위해 총 5종의 유전자 마커를 개발하여 실제적용 가능한 3종의 유전자 마커를 선발하였다. 선발된 3종의 마커에 대한 특이 프라이머를 제작하고 검출 및 판별이 가능한 triplex-PCR premix kit을 개발하였다. 개발한 kit을 이용하여 광범위하게 수집된 Xoo 균주를 대상으로 PCR을 수행하였다. PCR 분석 결과 광범위하게 수집된 96개의 균주들이 3그룹으로 분류되어지는 것을 확인할 수 있었다.
- 개발된 kit의 현장적용 및 실용화를 위해 다양한 시료를 사용하여 PCR 증폭반응을 수행하였다. 감염된 벼 잎을 증류수에 10분정도 침지시킨 침지액을 직접 PCR을 수행한 결과 벼흰잎마름병원균이 검출되는 것을 확인하였다. 이 결과 실제 현장적용 시균 분리 혹은 DNA 추출 없이 신속하고 정확하게 검출 및 판별이 가능함을 확인하였다.
○ 벼흰잎마름병원균의 병원성 양상에 따른 레이스 판별체계정립
- 국내에서 수집한 벼 흰잎마름병원균 134개 균주를 8계통(IRBB1, IRBB3, IRBB4, IRBB5, IRBB7, IRBB8, IRBB10 & IRBB21)에 병원성 검정을 수행한 결과 9 그룹으로 분류되는 것으로 나타났다. 분류 되어진 9 그룹에서 2개 혹은 3개의 균을 선별(20균주)하여 단인자 저항성 벼 품종(IRBB1, IRBB3, IRBB4, IRBB5, IRBB7, IRBB8, IRBB10 & IRBB21)에 병원성 검정 수행하였다. 병원성 분석 결과 10 그룹으로 분류되는 것으로 나타났다. 이 결과 국내에 분포하는 벼흰잎마름병원균들의 개체가 다양하게 분화 및 진화되었음을 확인하였다.
□ 제3세부과제 : 벼의 병 발현기작과 관련된 벼흰잎마름병원균 HRP 단백질 기능 구명
○ Xoo KACC10331 hrpB 돌연변이균주의 병원성과 과민반응 검정
- Xoo hrpB1::Tn5을 비롯한 8종의 Tn삽입돌연변이균주의 병원성과 과민반응이 소실되었고, 이것으로 이 유전자들이 코딩하는 단백질이 식물병원세균의 병 발현 기작에 필수인자임을 확인하였다.
○ HRP 단백질간의 상호작용 분석
- 8종의 HRP단백질 간의 상호결합을 yeast two-hybrid 결과와 in vitro pulldown assay를 수행한 결과 64조합의 상호결합 중 31조합의 결합을 확인하였다.
○ 벼흰잎마름병균 HRP 단백질 분비 및 기주 식물로의 이동 검정
- HRP 단백질 발현을 유도한 배양여액에서 HrcJ 단백질이 분비되는 것을 Western blot으로 확인하였다. 배양여액으로 분비되는 HrcJ 단백질에 대해 cya 리포터 실험을 수행한 결과 기주식물인 벼의 세포안으로 분비되는 것을 확인하였다.
○ 벼흰잎마름병균의 HRP 단백질과 결합하는 벼 표적단백질 탐색
- 벼흰잎마름병균의 HrcJ 단백질이 기주인 벼에서 어떠한 역할을 할 것인지를 예측하기 위하여 yeast two-hybrid library screening을 이용하여 HrcJ 단백질과 결합하는 벼표적단백질을 탐색하였고, 그 표적단백질을 코딩하는 벼 유전자의 유전정보를 분석한 결과 TBAP (thylakoid-bound ascorbate peroxidase)라는 유전자였다.
○ 벼 표적 단백질 knockout 돌연변이체 도입 및 병원성 검정
- 벼의 TBAP 유전자가 벼흰잎마름병균의 병 발현에 관련이 있는지를 확인하기 위하여, 이 유전자가 파괴된 T-DNA/Ds 삽입변이체를 분양받았다. Genotyping 및 reverse transcription-PCR로 T-DNA/Ds 삽입돌연변이체의 TBAP 유전자 소실을 확인한 후 병원성 검정을 수행한 결과 병징이 감소하는 것을 확인하였다.
□ 제1협동과제 : 벼흰잎마름병원균 잔탄검의 분자생물학분석 및 생화학적인 기능연구
○ Xanthan gum 생합성 대사과정의 작용제한점 규명
- Xoo 세포의 중심 탄소 대사과정의 활성 조절을 통한 glucose 6-phosphate의 세포내 농도 조절이 X oo 세포의 xanthan gum 생합성 증대에 중요한 영향을 미친다는 것을 발견하면서 X oo 세포내 glucose 6-phosphate의 축적량이 xanthan gum 생합성 대사과정의 작용제한점을 구성하는 것으로 규명하였다.
○ Xanthan gum 생합성 대사과정의 조절작용 기작 (mechanism) 규명
- Xoo 세포의 xanthan gum 생합성 대사과정의 작용제한점을 구성하는 세포내 glucose 6-phosphate의 축적량을 증대시키기 위한 중심 탄소 대사과정의 활성조절이 6-phosphogluconate dehydratase (edd) 유전자의 결손으로 인한 Entner-Doudoroff pathway의 불활성화 또는 glucose 6-phosphate dehydrogenase(zwf) 유전자의 결손으로 인한 oxidative pentose phosphate pathway의 불활성화를 통하여 이루어 질 수 있으며 동시에 xanthan gum 생합성 증대를 유도할 수 있음을 증명하였다.
○ Xanthan gum 생합성을 증대시키기 위한 대사과정의 재설계 및 최적화
- Xoo 세포로부터 xanthan gum 생산성을 증대시키기 위한 세포기능의 재설계 및 최적화가 (1) 중심 탄소 대사과정의 활성 조절을 통한 glucose 6-phosphate의 축적량을 증대 뿐 만 아니라, (2) 세포의 성장속도 증대를 위한 glycolysis 활성 증대 [phosphofructokinase (PFK) 유전자의 과발현]을 통하여 이루어 질 수 있음을 증명하였다.
□ 제2협동과제 : 벼흰잎마름병균의 세포외 분비효소의 기능분석 및 산업화 이용 연구
○ Xoo 유전체로부터 cellulase 유전자 cloning 및 병원성과의 관련성 구명
- 유전체에 존재하는 cellulase 유전자 12종을 transposon 변이체를 제작하여 식물(벼)과의 병원성 검정 결과 병원성에 관련된 유전자 3종[Xoo0281 (eglX oA), Xoo0282(eglX oB ), 그리고 Xoo4036 (celX oB )]을 확인하였다.
○ 병원성관련 Xoo cellulase의 효소학적 특성 및 세포외 분비기구 구명
- eglxoA::Tn5, 야생주 KACC10859와 hrpX 돌연변이체(hrpX::Tn5), 단백질 분비관련 유전자인 xpsF의 돌연변이체(xpsF::Tn5)를 XOM2 배지에 배양하여 세포외 분비단백질(extracellular protein)을 분리하고 SDS-PAGE에 전기영동 한 후에 silver staining하여 각각의 단백질 양상을 비교 분석 하였다. xpsF::Tn5 돌연변이체에서는 extracellular protein이 KACC10859와 비교 할 때 많은 분비단백질이 나타나지 않았으나 eglxoA::Tn5의 extracellular protein에서는 야생주와 비교할 때 약한 밴드의 차이가 있었다
○ Xoo cellulase 유전자의 발현제어
- celX oB 유전자가 HrpX에 의하여 제어 되는지 여부를 조사하기 위해 RT-PCR을 수행한 결과 celX oB 유전자 전사발현은 hrpX ::Tn5에서 RT-PCR 밴드가 검출되지 않아 hrpX 가 celX oB 전사발현을 제어 하는 것으로 나타났다.
Bacterial blight, caused by X anthomonas oryzae pv. oryzae, is the major disease in most rice-growing areas. A random insertional mutant library of X . oryzae pv. oryzae KACC10331 was previously constructed. By screening mutants against susceptible rice cultivar IR24, 280 mutants that had reduced vi
Bacterial blight, caused by X anthomonas oryzae pv. oryzae, is the major disease in most rice-growing areas. A random insertional mutant library of X . oryzae pv. oryzae KACC10331 was previously constructed. By screening mutants against susceptible rice cultivar IR24, 280 mutants that had reduced virulence on rice plants were isolated.
Southern hybridization confirmed that all mutant strains had single-copy insertions and the insertion site of the transposon was defined by thermal asymmetric interlaced (TAIL)-PCR and sequence analysis. The single-transposon-tagged sequence of 42 mutant strains belonged to pathogenicity-related genes previously reported in various bacterial pathogens, while the other 51 single-transposon-tagged sequences included diverse functional genes encoding, regulatory proteins, metabolic regulators, transposase and hypothetical proteins, which were identified as novel pathogenicity-related genes of X . oryzae pv. oryzae.
We identified a mutant strain (KXOM9) that is deficient for pigment production and virulence. Furthermore, the KXOM9 mutant was unable to grow in minimal medium lacking aromatic amino acids. Thermal asymmetric interlaced-PCR and sequence analysis of KXOM9 revealed that the transposon was inserted into the aroC gene, which encodes a chorismate synthase in various bacterial pathogens. In planta growth assays revealed that bacterial growth of the KXOM9 mutant in rice leaves was severely reduced. Genetic complementation of this mutant with a 7.9-kb fragment containing aroC restored virulence, pigmentation, and prototrophy. These results suggest that the aroC gene plays a crucial role in the growth, virulence, and pigment production of X . oryzae pv. oryzae.
Avirulence (avr) genes of several phytopathogens including Xoo were identified on the basis of their ability to direct specific recognition leading to disease resistance in plant-microbe interactions. Structural features of these genes important for avirulence and/or virulence functions include a central region of multiple direct repeats and three nuclear localization signals (NLSs) and an acidic activation domain (AD) at the C-terminal.
Recently, we determined the complete genome sequence and isolated the avrBs3-like genes of Korean Xoo KACC10331. Total 11 avrBs3-like genes were found and identified. In order to elucidate their role and function, we constructed the avr-deficient mutant via marker-exchange and the deletion mutant via electroporation with pK18mobSacB vectors harboring the internally deleted avr gene. After clip inoculation with all the bacterial strains, the symptoms on the near isogenic lines (IRBB1, 2, 3, 4, 5, 7, 8, 10, 11, 13, 14, 21 and IR24) were recorded. The results indicated that all the mutants were not able to cause disease on the near isogenic lines.
A triplex PCR method has been developed for the race-specific detection of Xanthomonas oryzae pv. oryzae (Xoo), the bacterial blight (BB) pathogen of rice. For this, three primer sets were designed: for specific internal regions of two genes (hpaA and XorII veryshort-patch-repair endonuclease) and for a genomic locus derived from an amplified fragment length polymorphism (AFLP) fragment specific for the K3 and K5 races. The sizes of the PCR products when using XOOF/XOOR, XRMF/XRMR, and XAF3F/XAF3R primer pairs were 327, 427 bp and 1 kb, respectively, when the assay was applied to detect the pathogen in solution and lesion exudates, and as a template. Amplicons were obtained without the need for any prior processing (e.g. DNA preparation from infected leaf or bacterial cell isolation from the lesion). Furthermore, the pathogen could be quickly detected in the asymptomatic rice leaf 3 days after inoculation and at a distance of 6 cm from the lesion site. This PCR based simple and rapid assay will be a useful method for the detection and identification of Xoo as well as for disease forecasting in paddy fields.
X anthomonas oryzae pathovar oryzae (Xoo) causes a bacterial blight, which is one of the most destructive diseases in the rice-growing regions. This plant pathogenic bacteria invades the rice plant through the wounds or water pores of leaves and causes a vascular disease in the rice plant.
For successive infection, X . oryzae pv oryzae uses type III secretion (T3S) system to secret bacterial virulence factors into the extracellular milieu or to transport effector proteins into target cells. The T3S systems are essential for many Gram-negative bacterial pathogens to cause disease in susceptible hosts by the secretion and translocation of effector proteins. In resistant and non-host plants, the T3S systems are involved in defense response of host by induction of the hypersensitive response (HR) manifested as rapid cell death at the infection site and restrict to bacterial multiplication In this study, we aimed at the functional analysis of HrpB proteins (encoded from the hrpB operon) in rice infection. For this, we first analyzed the interaction among HrpB proteins. HrpB proteins are localized in various region of bacterial cells - cytosol, inner membrane, periplasmic space, outer membrane and extracellular milieu. With localization, the interactions are important to understand functions on plant infection. Second, we identified the secretion and translocation of HrpB proteins. And with these proteins, we screened the rice target proteins using yeast two-hybrid library system. To identify the effect of rice target genes on X oo infection, we obtained the T-DNA/Ds insertional mutants of disrupted rice target gene and carried out the pathogenicity assay of X . oryzae pv oryzae. As the results, HrcJ protein are secreted and translocated into rice cell cytosol and interact with rice proteins involving ROS (Reactive Oxygen Species) systems.
Genome sequence analysis of X anthomonas oryzae pv. oryzae has revealed a cluster of 12 ORFs that are closely related to the gum gene cluster of X anthomonas campestris pv. campestris. The gum gene cluster of X . oryzae encodes proteins involved in xanthan production; however, there is little experimental evidence supporting this. In previous study, biochemical analyses of xanthan produced by a defined set of X . oryzae gum mutant strains allowed us to preliminarily assign functions to most of the gum gene products: biosynthesis of the pentasaccharide repeating unit for GumD, GumM, GumH, GumK, and GumI, xanthan polymerization and transport for GumB, GumC, GumE, and GumJ, and modification of the pentasaccharide repeating unit for GumF, GumG, and GumL. Two genes involved in central carbon metabolism were inactivated to modulate intracellular glucose 6-phosphate and to evaluate its effects on xanthan production in wild-type X . oryzae.
Upon the inactivation of the phosphogluconate dehydratase gene (edd), intracellular glucose 6-phosphate increased from 0.05 to 1.17 mmol/g (dry cell wt). This was accompanied by increased xanthan production of up to 2.55 g/l (culture medium). In contrast, inactivation of 6-phosphogluconate dehydrogenase gene (gndA) did not influence intracellular glucose 6-phosphate nor xanthan production. The intracellular availability of glucose 6-phosphate is proposed as a rate-limiting factor in xanthan production, and it may be possible to increases production of xanthan by modulating the activities of enzymes in central carbon metabolism. In this study, the glucose 6-phosphate dehydrogenase gene (XOO2314) was inactivated in order to modulate the intracellular glucose 6-phosphate, and its effects on xanthan production in a wild-type strain of X . oryzae were evaluated. The intracellular glucose 6-phosphate was increased from 17.6 to 99.4 mol μmol/g (dry cell weight) in the gene-disrupted mutant strain. The concomitant increase in the glucose 6-phosphate was accompanied by an increase in xanthan production of up to 2.23 g/1 (culture medium).
However, in defined medium supplemented with 0.4% glucose, the growth rate of the mutant strain was reduced to 52.9% of the wild-type level. Subsequently, when a family BATP-dependent phosphofructokinase from Escherichia coli was overexpressed in the mutant strain, the growth rate was increased to 142.9%, whereas the yields of xanthan per mole of glucose remained approximately the same.
Extracellular enzymes have recently been considered to play an important role in the virulence of X.oryzae pv.oryzae (Hu et al., 2007; Jha et al., 2007; Rajeshwari et al., 2005). It has confirmed that the purified cellulase and lipase proteins induced defense responses in rice that were suppressible by Xoo in a T3S- dependent manner [Jha et al., 2007].
In this study, Twelve cellulase genes were PCR amplified from X. oryzae. pv. oryzae KACC10859 genome and cloned into TA-cloning vector. Transposon inserted cellulase genes were maker exchanged with target genes of wild type strain and their pathogenicity was assayed. Pathogenecity of the mutant strains was assayed on susceptible rice variety, Milyang 23. Of six mutants, eglXoA::Tn5, eglXoB::Tn5, celXoB::Tn5 showed virulence-deficient phenotype, while pathogenecity of celbXoA::Tn5, bglXoC::Tn5, and bglXoF::Tn5 was attenuated. But other cellulase genes were not associated with pathogenecity. The celXoB gene was overexpressed in pET11b vector and the overexpressed protein (65kDa) was purified. The fusion protein with CelxoB protein (His)6 tag was purified and the polyclonal antibodies were raised against the purified proteins.
Western hybridization band of 65kDa was detected on extracellular secretion fraction of wild type strain, but not in that of celXoB::Tn5 and xpsF::Tn5 mutant, suggesting secretion of CelxoB is dependent on TypeII secretion system. Interestingly, the secreted proteins were dramatically reduced in celXoB::Tn5 compared to wild type and other mutant strains. Furthermore, RT-PCR analysis showed Hrp X regulates transcriptional expression of celxoB. In addition, it was also speculated that celXoB::Tn5 and celbXoA::Tn5 are transcribed on the same mRNA as transcription unit. In pathogenicity test using transposon mutant, it was revealed that xoclp is related to pathogenicity. In addition, RT-PCR analyis showed Clp regulates transcriptional expressions of cellulase genes and diffusible signal factor (DSF) genes.
 표
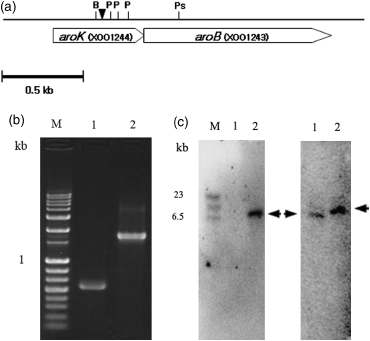
Molecular analysis and genetic mapping of the aroK and aroB genes in the mutant M11 strain. The solid triangle indicates the site of the Tn5 transposon insertion. The restriction sits for BamHI (B), Pvull (P) and PstI (Ps) are also indicated (a). PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroK gene. M, 1 kb ladder; lane 1 WT strain; lane 2, M11 (b, c).
표
Molecular analysis and genetic mapping of the aroK and aroB genes in the mutant M11 strain. The solid triangle indicates the site of the Tn5 transposon insertion. The restriction sits for BamHI (B), Pvull (P) and PstI (Ps) are also indicated (a). PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroK gene. M, 1 kb ladder; lane 1 WT strain; lane 2, M11 (b, c).
 표
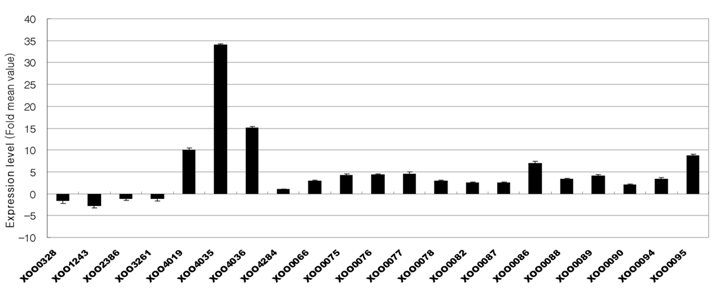
Expression levels of the 21 genes obtained by DNA microarray profiling of the M11 strain. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC and XOO0095, hpa1
표
Expression levels of the 21 genes obtained by DNA microarray profiling of the M11 strain. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC and XOO0095, hpa1
 표
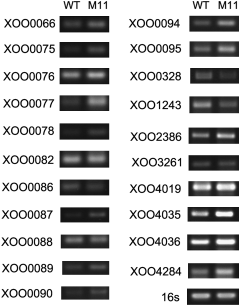
RT-PCR assay of 22 genes of the WT and M11 strains. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC XOO0095, hpa1 and 16S rRNA gene.
표
RT-PCR assay of 22 genes of the WT and M11 strains. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC XOO0095, hpa1 and 16S rRNA gene.
 표
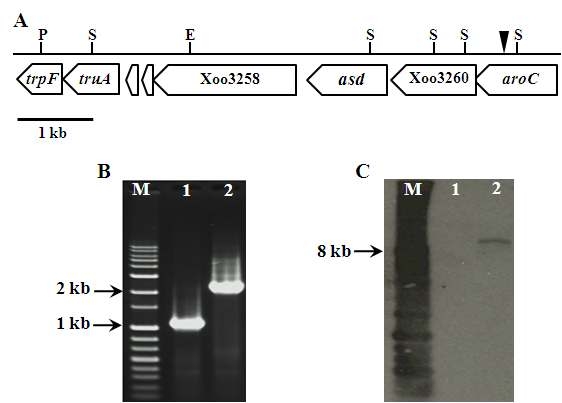
Molecular analysis of the KXOM9 mutant strain. (A) The aroC gene flanking region of the KXOM9 mutant strain. The solid triangle indicates the site of the Tn5 transposon insertion. E, EcoRI; S, SphI; P, PstI. PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroC gene: M, 1-kb ladder; lane 1, wild-type; lane 2, KXOM9 (B, C).
표
Molecular analysis of the KXOM9 mutant strain. (A) The aroC gene flanking region of the KXOM9 mutant strain. The solid triangle indicates the site of the Tn5 transposon insertion. E, EcoRI; S, SphI; P, PstI. PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroC gene: M, 1-kb ladder; lane 1, wild-type; lane 2, KXOM9 (B, C).
 표
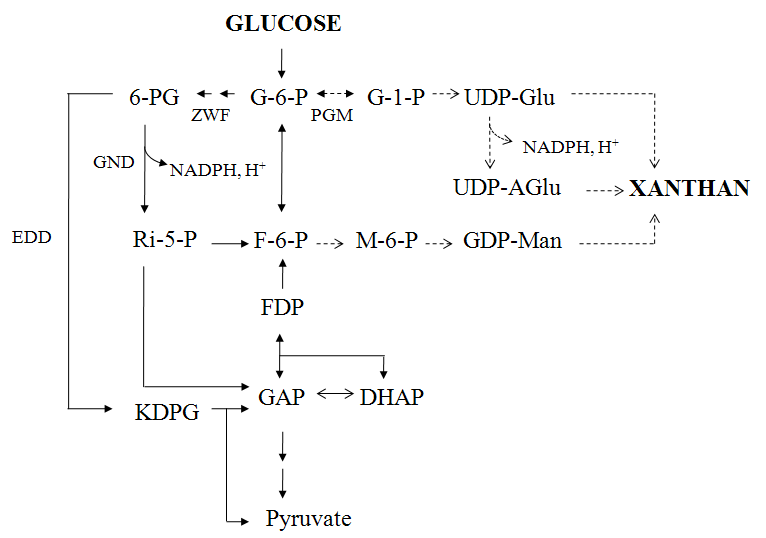
Proposed pathway for xanthan biosynthesis in X .oryzae. Straight and dotted arrowsre present the catabolic and anabolic pathways, respectively. Abbreviations: G-6-P, glucose-6-phosphate; F-6-P, fructose-6-phosphate; FDP, fructose-1,6-bisphosphate; DHAP, dihydroxyacetone-phosphate; GAP, glyceraldehydes-3-phosphate; 6-PG, 6-phosphogluconate; Ri-5-P, ribose-5-phosphate; KDPG, 2-keto-3-deoxy-6-phosphogluconate; G-1-P, glucose-1-phosphate; M-6-P, mannose-6-phosphate; UDP-Glu, UDP-glucose; UDP-AGlu, UDP-gluconate; GDP-Man, GDP-mannose; PGM, phosphoglucomutase; ZWF, glucose-6-phosphate dehydrogenase; GND, 6-phosphogluconate dehydrogenase; EDD, 6-phosphogluconate dehydratase.
표
Proposed pathway for xanthan biosynthesis in X .oryzae. Straight and dotted arrowsre present the catabolic and anabolic pathways, respectively. Abbreviations: G-6-P, glucose-6-phosphate; F-6-P, fructose-6-phosphate; FDP, fructose-1,6-bisphosphate; DHAP, dihydroxyacetone-phosphate; GAP, glyceraldehydes-3-phosphate; 6-PG, 6-phosphogluconate; Ri-5-P, ribose-5-phosphate; KDPG, 2-keto-3-deoxy-6-phosphogluconate; G-1-P, glucose-1-phosphate; M-6-P, mannose-6-phosphate; UDP-Glu, UDP-glucose; UDP-AGlu, UDP-gluconate; GDP-Man, GDP-mannose; PGM, phosphoglucomutase; ZWF, glucose-6-phosphate dehydrogenase; GND, 6-phosphogluconate dehydrogenase; EDD, 6-phosphogluconate dehydratase.
 표
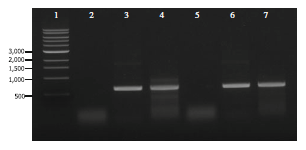
RT-PCR analysis of the pfk gene transcript produced by the wild-type strain. For the positive control, the presence of the expected amplicon when genomic DNA was included in the control sample demonstrated the reliability of the primer pair, PFKF-PFKR (lane 2). For the negative control, no amplicon was detected when total RNA that was treated with DNase I but was not reverse-transcribed served as the template, ensuring that residual genomic DNA had not contaminated the total RNA preparation (lane 3). The cDNA fraction obtained with the RT primer was used for subsequent PCR reactions with primer pair, PFKF-PFKR (lanes 4). DNA size markers in base pairs are indicated (lane 1).
표
RT-PCR analysis of the pfk gene transcript produced by the wild-type strain. For the positive control, the presence of the expected amplicon when genomic DNA was included in the control sample demonstrated the reliability of the primer pair, PFKF-PFKR (lane 2). For the negative control, no amplicon was detected when total RNA that was treated with DNase I but was not reverse-transcribed served as the template, ensuring that residual genomic DNA had not contaminated the total RNA preparation (lane 3). The cDNA fraction obtained with the RT primer was used for subsequent PCR reactions with primer pair, PFKF-PFKR (lanes 4). DNA size markers in base pairs are indicated (lane 1).
 표
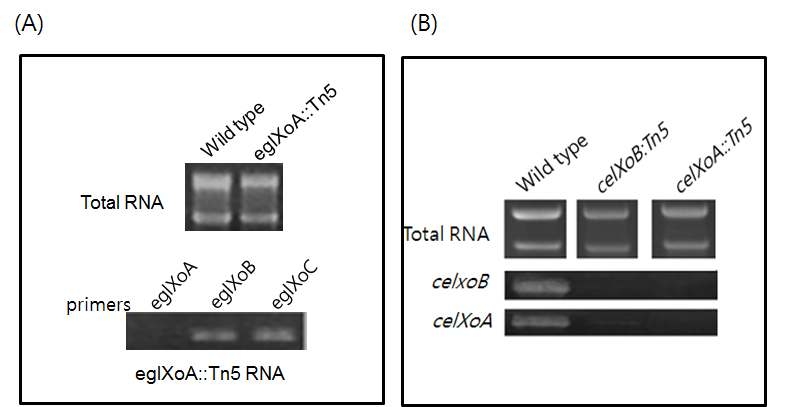
RT-PCR analysis of cellulase gene cluster. Total RNA was exracted from Xoo KACC10859, eglxoA::Tn5, celX oB::Tn5 and celX oA::Tn5 The cDNA samples was synthesized from each total RNA. Panel A: RT-PCR bands amplified by each eglxoA, eglxoB and eglxoC primer. Panel B: RT-PCR bands amplified by celX oA and celX oB primers.
표
RT-PCR analysis of cellulase gene cluster. Total RNA was exracted from Xoo KACC10859, eglxoA::Tn5, celX oB::Tn5 and celX oA::Tn5 The cDNA samples was synthesized from each total RNA. Panel A: RT-PCR bands amplified by each eglxoA, eglxoB and eglxoC primer. Panel B: RT-PCR bands amplified by celX oA and celX oB primers.
 표
Cellulase activity of transposon mutant strains on carboxymethylcellulose(CMC) media under different conditions. A: Cell grown on NB medium, B: culture filtrate from NB medium, C: Cell grown on NB medium, D: culture filtrate from XOM2 medium, Lane 1; Xoo KACC10859 Lane 2; eglxoA::Tn5 Lane 3; eglxoB::Tn5 Lane 4; eglxoC::Tn5; Lane 5; hrpX::Tn5, Lane 6; xpsF::Tn5.
표
Cellulase activity of transposon mutant strains on carboxymethylcellulose(CMC) media under different conditions. A: Cell grown on NB medium, B: culture filtrate from NB medium, C: Cell grown on NB medium, D: culture filtrate from XOM2 medium, Lane 1; Xoo KACC10859 Lane 2; eglxoA::Tn5 Lane 3; eglxoB::Tn5 Lane 4; eglxoC::Tn5; Lane 5; hrpX::Tn5, Lane 6; xpsF::Tn5.
 표
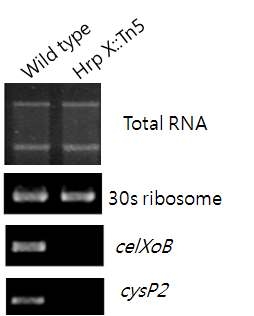
Transcriptional regulatory analysis of xocel5 gene by hrpX gene. Total RNA was extracted from X . oryzae pv. oryzae KACC10859 (WT) and hrpX ::Tn5 and used for cDNA synthesis. Subsequently, the cDNA samples were amplified by RT-PCR primers with 30s ribosomal primer (positive contro) and cysP2 gene (negative control).
표
Transcriptional regulatory analysis of xocel5 gene by hrpX gene. Total RNA was extracted from X . oryzae pv. oryzae KACC10859 (WT) and hrpX ::Tn5 and used for cDNA synthesis. Subsequently, the cDNA samples were amplified by RT-PCR primers with 30s ribosomal primer (positive contro) and cysP2 gene (negative control).
 표
Molecular analysis and genetic mapping of the aroK and aroB genes in the mutant M11 strain. The solid triangle indicates the site of the Tn5 transposon insertion. The restriction sits for BamHI (B), Pvull (P) and PstI (Ps) are also indicated (a). PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroK gene. M, 1 kb ladder; lane 1 WT strain; lane 2, M11 (b, c).
표
Molecular analysis and genetic mapping of the aroK and aroB genes in the mutant M11 strain. The solid triangle indicates the site of the Tn5 transposon insertion. The restriction sits for BamHI (B), Pvull (P) and PstI (Ps) are also indicated (a). PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroK gene. M, 1 kb ladder; lane 1 WT strain; lane 2, M11 (b, c).
 표
Expression levels of the 21 genes obtained by DNA microarray profiling of the M11 strain. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC and XOO0095, hpa1
표
Expression levels of the 21 genes obtained by DNA microarray profiling of the M11 strain. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC and XOO0095, hpa1
 표
RT-PCR assay of 22 genes of the WT and M11 strains. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC XOO0095, hpa1 and 16S rRNA gene.
표
RT-PCR assay of 22 genes of the WT and M11 strains. XOO0328, aroD XOO1243, aroB XOO2386, aroA XOO3261, aroC XOO4019, engX CA (cellulase); XOO4035, cbsA (1,4-b-cellobiosidase); XOO4036, cellulase; XOO4284, aroG XOO0066, hrpF XOO0075, hpaB XOO0076, hrpE XOO0077, hrpD6 XOO0078, hrpD5 XOO0082, hrcQ XOO0087, hrpB2 XOO0086, hrpB1 XOO0088, hrpB3 XOO0089, hrpB4 XOO0090, hrpB5 XOO0094, hrcC XOO0095, hpa1 and 16S rRNA gene.
 표
Molecular analysis of the KXOM9 mutant strain. (A) The aroC gene flanking region of the KXOM9 mutant strain. The solid triangle indicates the site of the Tn5 transposon insertion. E, EcoRI; S, SphI; P, PstI. PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroC gene: M, 1-kb ladder; lane 1, wild-type; lane 2, KXOM9 (B, C).
표
Molecular analysis of the KXOM9 mutant strain. (A) The aroC gene flanking region of the KXOM9 mutant strain. The solid triangle indicates the site of the Tn5 transposon insertion. E, EcoRI; S, SphI; P, PstI. PCR assay and Southern hybridization analysis for reaffirmation of transposon insertion in the aroC gene: M, 1-kb ladder; lane 1, wild-type; lane 2, KXOM9 (B, C).
 표
Proposed pathway for xanthan biosynthesis in X .oryzae. Straight and dotted arrowsre present the catabolic and anabolic pathways, respectively. Abbreviations: G-6-P, glucose-6-phosphate; F-6-P, fructose-6-phosphate; FDP, fructose-1,6-bisphosphate; DHAP, dihydroxyacetone-phosphate; GAP, glyceraldehydes-3-phosphate; 6-PG, 6-phosphogluconate; Ri-5-P, ribose-5-phosphate; KDPG, 2-keto-3-deoxy-6-phosphogluconate; G-1-P, glucose-1-phosphate; M-6-P, mannose-6-phosphate; UDP-Glu, UDP-glucose; UDP-AGlu, UDP-gluconate; GDP-Man, GDP-mannose; PGM, phosphoglucomutase; ZWF, glucose-6-phosphate dehydrogenase; GND, 6-phosphogluconate dehydrogenase; EDD, 6-phosphogluconate dehydratase.
표
Proposed pathway for xanthan biosynthesis in X .oryzae. Straight and dotted arrowsre present the catabolic and anabolic pathways, respectively. Abbreviations: G-6-P, glucose-6-phosphate; F-6-P, fructose-6-phosphate; FDP, fructose-1,6-bisphosphate; DHAP, dihydroxyacetone-phosphate; GAP, glyceraldehydes-3-phosphate; 6-PG, 6-phosphogluconate; Ri-5-P, ribose-5-phosphate; KDPG, 2-keto-3-deoxy-6-phosphogluconate; G-1-P, glucose-1-phosphate; M-6-P, mannose-6-phosphate; UDP-Glu, UDP-glucose; UDP-AGlu, UDP-gluconate; GDP-Man, GDP-mannose; PGM, phosphoglucomutase; ZWF, glucose-6-phosphate dehydrogenase; GND, 6-phosphogluconate dehydrogenase; EDD, 6-phosphogluconate dehydratase.
 표
RT-PCR analysis of the pfk gene transcript produced by the wild-type strain. For the positive control, the presence of the expected amplicon when genomic DNA was included in the control sample demonstrated the reliability of the primer pair, PFKF-PFKR (lane 2). For the negative control, no amplicon was detected when total RNA that was treated with DNase I but was not reverse-transcribed served as the template, ensuring that residual genomic DNA had not contaminated the total RNA preparation (lane 3). The cDNA fraction obtained with the RT primer was used for subsequent PCR reactions with primer pair, PFKF-PFKR (lanes 4). DNA size markers in base pairs are indicated (lane 1).
표
RT-PCR analysis of the pfk gene transcript produced by the wild-type strain. For the positive control, the presence of the expected amplicon when genomic DNA was included in the control sample demonstrated the reliability of the primer pair, PFKF-PFKR (lane 2). For the negative control, no amplicon was detected when total RNA that was treated with DNase I but was not reverse-transcribed served as the template, ensuring that residual genomic DNA had not contaminated the total RNA preparation (lane 3). The cDNA fraction obtained with the RT primer was used for subsequent PCR reactions with primer pair, PFKF-PFKR (lanes 4). DNA size markers in base pairs are indicated (lane 1).
 표
RT-PCR analysis of cellulase gene cluster. Total RNA was exracted from Xoo KACC10859, eglxoA::Tn5, celX oB::Tn5 and celX oA::Tn5 The cDNA samples was synthesized from each total RNA. Panel A: RT-PCR bands amplified by each eglxoA, eglxoB and eglxoC primer. Panel B: RT-PCR bands amplified by celX oA and celX oB primers.
표
RT-PCR analysis of cellulase gene cluster. Total RNA was exracted from Xoo KACC10859, eglxoA::Tn5, celX oB::Tn5 and celX oA::Tn5 The cDNA samples was synthesized from each total RNA. Panel A: RT-PCR bands amplified by each eglxoA, eglxoB and eglxoC primer. Panel B: RT-PCR bands amplified by celX oA and celX oB primers.
 표
Cellulase activity of transposon mutant strains on carboxymethylcellulose(CMC) media under different conditions. A: Cell grown on NB medium, B: culture filtrate from NB medium, C: Cell grown on NB medium, D: culture filtrate from XOM2 medium, Lane 1; Xoo KACC10859 Lane 2; eglxoA::Tn5 Lane 3; eglxoB::Tn5 Lane 4; eglxoC::Tn5; Lane 5; hrpX::Tn5, Lane 6; xpsF::Tn5.
표
Cellulase activity of transposon mutant strains on carboxymethylcellulose(CMC) media under different conditions. A: Cell grown on NB medium, B: culture filtrate from NB medium, C: Cell grown on NB medium, D: culture filtrate from XOM2 medium, Lane 1; Xoo KACC10859 Lane 2; eglxoA::Tn5 Lane 3; eglxoB::Tn5 Lane 4; eglxoC::Tn5; Lane 5; hrpX::Tn5, Lane 6; xpsF::Tn5.
 표
Transcriptional regulatory analysis of xocel5 gene by hrpX gene. Total RNA was extracted from X . oryzae pv. oryzae KACC10859 (WT) and hrpX ::Tn5 and used for cDNA synthesis. Subsequently, the cDNA samples were amplified by RT-PCR primers with 30s ribosomal primer (positive contro) and cysP2 gene (negative control).
표
Transcriptional regulatory analysis of xocel5 gene by hrpX gene. Total RNA was extracted from X . oryzae pv. oryzae KACC10859 (WT) and hrpX ::Tn5 and used for cDNA synthesis. Subsequently, the cDNA samples were amplified by RT-PCR primers with 30s ribosomal primer (positive contro) and cysP2 gene (negative control).
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.