최소 단어 이상 선택하여야 합니다.
최대 10 단어까지만 선택 가능합니다.
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
NTIS 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
DataON 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Edison 바로가기
다음과 같은 기능을 한번의 로그인으로 사용 할 수 있습니다.
Kafe 바로가기
| 주관연구기관 | 식품의약품안전평가원 National Institute of Food and Drug Safety Evaluation |
|---|---|
| 연구책임자 | 곽효선 |
| 참여연구자 | 김순한 , 주인선 , 허은정 , 이정수 , 서수환 , 정경태 , 한정아 , 김용훈 , 김석환 , 이우정 |
| 보고서유형 | 최종보고서 |
| 발행국가 | 대한민국 |
| 언어 | 한국어 |
| 발행년월 | 2017-12 |
| 과제시작연도 | 2017 |
| 주관부처 | 식품의약품안전처 Ministry of Food and Drug Safety |
| 등록번호 | TRKO201800038118 |
| 과제고유번호 | 1475009838 |
| 사업명 | 식품등안전관리 |
| DB 구축일자 | 2018-12-01 |
| 키워드 | 식중독균.유전자검출기술.개선.Foodborne pathogens.detection method.advance. |
| DOI | https://doi.org/10.23000/TRKO201800038118 |
식중독균의 신속검출은 식품안전을 위해 중요하다. 식중독균을 빠르고 정확하게 검출할 수 있는 기술로 병원성 유전자를 검출하는 real-time PCR에 기반한 시험법이 알려져 왔다. 우리나라 식약처에서는 국내 주요 식중독균 17종에 대해 35종의 병원성 유전자를 검출할 수 있는 real-time PCR법을 개발하였다. 본 연구에서는 현행 식중독균 검출법을 개선하고자 하였다.
S. aureus의 8개 병원성 유전자 (sea, seb, sec, sed, see, seg, seh, sei)를 동시에 신속 검출할 수 있는 시험법
식중독균의 신속검출은 식품안전을 위해 중요하다. 식중독균을 빠르고 정확하게 검출할 수 있는 기술로 병원성 유전자를 검출하는 real-time PCR에 기반한 시험법이 알려져 왔다. 우리나라 식약처에서는 국내 주요 식중독균 17종에 대해 35종의 병원성 유전자를 검출할 수 있는 real-time PCR법을 개발하였다. 본 연구에서는 현행 식중독균 검출법을 개선하고자 하였다.
S. aureus의 8개 병원성 유전자 (sea, seb, sec, sed, see, seg, seh, sei)를 동시에 신속 검출할 수 있는 시험법을 개발하였다. 검출한계는 1~10 copies/uL였다. 또한 Real-time PCR의 특이도는 50개의 S.aureus 균주와 S. aureus 이외의 37개 균주에서 평가되었고, 100 % 특이도를 만족하였다. B. cereus의 6개 병원성 유전자 (bceT, CER, hblC, nheA, cytK, entFM)를 동시에 신속 검출할 수 있는 시험법 또한 개발되었다. 검출한계는 10 copies/uL였다. Real-time PCR의 특이도는 50개의 B. cereus 균주와 B.cereus 이외의 29개 균주에서 평가되었고, 100 % 특이도를 만족하였다. V. parahaemolyticus.의 3개 병원성 유전자 (tlh, trh, tdh)를 동시에 신속 검출할 수 있는 시험법을 개발하였다. 검출한계는 10 copies/uL이었다. 또한 Real-time PCR의 특이도는 50개의 V. parahaemolyticus. 균주와 이외의 32개 균주에서 평가되었고, 100 % 특이도를 만족하였다. Y. enterocolitica의 3개 병원성 유전자 (ail, ystA, ystB)를 동시에 신속 검출할 수 있는 시험법을 개발하였다. 검출한계는 1 copy/uL였다. 또한 Real-time PCR의 특이도는 50개의 Y.enterocolitica 균주와 S. aureus 이외의 36개 균주에서 평가되었고, 100 % 특이도를 만족하였다.
본 연구에서는 개발된 시험법을 검증하기 위해 두 시험법 (Real-time PCR과 Conventional PCR)에 따라 배양액과 식품에서 민감도를 평가하였다. 배양액에서 최대 검출한계는 식약처 개선시험법인 multiplex real-time PCR의 경우 황색포도상구균 (102), 바실러스 세레우스는 (101), 장염비브리오 (101), 여시니아 엔테로콜리티카 (101 CFU/ml)까지 검출할 수 있음을 확인하였다. PCR 시험법에 대해서는 황색포도상구균 (104) 바실러스 세레우스 (103), 장염비브리오 (103), 여시니아 엔테로콜리티카 105 CFU/ml의 검출한계 수준을 나타냈다. 또한 식품에 인위적으로 균을 접종한 결과 RT PCR법의 검출한계는 S.aureus (102 CFU/mL), B. cereus (101 CFU/mL), V. parahaemolyticus (102 CFU/mL), Y.enterocolitica (101 CFU/mL) 였으나, PCR법은 황색포도상구균 (104) 바실러스 세레우스 (103), 장염비브리오 (104), 여시니아 엔테로콜리티카 (106 CFU/mL) 수준까지 검출이 가능하였다. 본 연구에서 개선한 식중독 원인조사 시험법을 이용하여 향후 식중독원인조사에 활용할 수 있을 것으로 기대된다.
Y. pseudotuberculosis 검사를 위한 real-time PCR 시험법은 ISO/TS 18867:2015(E)를 참고하여 개발되었다. 시험법에 대한 특이도는 Y. pseudotuberculosis 1개 균주와 Y. pseudotuberculosis 이외 51개 균주에 대해 평가되었고, 100% 특이도를 만족하였다. 민감도 시험을 통한 검출한계는 101 CFU/mL 수준으로 확인되었다.
식중독균에서 Real-time PCR의 효과적인 수행을 위해 보다 효율적인 DNA 추출법이 필요하다. 유전자 추출 자동화 장비 3종을 대상으로 배양액과 즉석섭취식품에 균을 인위적으로 접종하여 real-time PCR을 통해 유전자 검출능을 확인하였다.
병원성 세균에 대한 항생제 내성 유전자를 검출하기 PNA (peptide nucleic acid) probe에 기반한 real-time PCR법을 개발하였다. 검출한계는 10~100 copies/uL였다. 특이도는 MRSA mecA, ESBL CTX-M1 유전자에 대해 평가되었으며, S. aureus 69균주, E. coli 43균주에 대해 시험되었고 100% 특이도를 만족하였다.
(출처 : 국문 요약문 3p)
The rapid detection of food-borne pathogens is an important food safety tool. Molecular detection methods based on the real-time polymerase chain reaction (PCR) to detect virulent target genes have become a well-developed method for rapid and accurate detection of pathogens. The ministry of food and
The rapid detection of food-borne pathogens is an important food safety tool. Molecular detection methods based on the real-time polymerase chain reaction (PCR) to detect virulent target genes have become a well-developed method for rapid and accurate detection of pathogens. The ministry of food and drug safety (MFDS) has developed real-time PCR assay to detect the thirty-five virulent genes of seventeen major foodborne pathogens in Korea. The purpose of this study is to improve the current assay methods of foodborne pathogens.
The fast multiplex real-time PCR assays for detecting 8 virulent genes (sea, seb, sec, sed, see, seg, seh, sei) of S. aureus was developed. The Limit of detection was 1~10 copies/uL. Specificity of real-time PCR was tested on 50 target starins and 37 non-target strains, 100% specificity was obtained. The fast multiplex real-time PCR assays for detecting 6 virulent genes (bceT, CER, hblC, nheA, cytK, entFM) of B. cereus was developed. The limit of detection was 10 copies/uL. Specificity of real-time PCR was tested on 50 target starins and 29 non-target strains, 100% specificity was obtained. The fast multiplex real-time PCR assays for detecting 3 virulent genes (tlh, trh, tdh) of V. parahaemolyticus. was developed. The limit of detection was 1~10 copies/uL. Specificity of real-time PCR was tested on 50 target starins and 32 non-target strains, 100% specificity was obtained. The fast multiplex real-time PCR assays for detecting 3 virulent genes (ail, ystA, ystB) of Y.enterocolitica was developed. The limit of detection was 1 copy/uL.
Specificity of real-time PCR was tested on 50 target starins and 36 non-target strains, 100% specificity was obtained.
We evaluated the detection of S. aureus, B. cereus, V. parahaemolyticus and Y. enterocolitica virulent genes from bacterial cultures and artificially inoculated foods using a multiplex real-time PCR assay. Sensitivity of multiplex real-time PCR method was compared to that of conventional PCR. Sensitivity of multiplex real-time PCR assay for five pathogens was able to detect a minimum of 102, 101, 101, 101, 101 CFU/mL for the S. aureus, B. cereus, V. parahaemolyticus and Y. enterocolitica target gene, respectively. However, The PCR assay was a detection limit of 104, 103, 103, 105 CFU/mL. The multiplex real-time PCR was able to detect up to 103 CFU/mL for S. aureus, 101 CFU/ml for B. cereus, 102 CFU/mL for V. parahaemolyticus and 102 CFU/mL for Y. enterocolitica of artificially inoculated foods, while that of PCR was 104 CFU/mL for S.aureus, 103 CFU/ml for B. cereus, 104 CFU/mL for V. parahaemolyticus, 106 CFU/mL and for Y. enterocolitica. In conclusion, the multiplex real-time PCR assay would be useful for detection of food-borne pathogens in the outbreak investigation.
The real-time PCR assay method for the detection of Y. pseudotuberculosis was developed with reference to ISO/TS 18867:2015(E). The specificity of the real time PCR was tested on 1 target strain and 51 non-target strains, 100% specificity was obtained. The limit of detection for Y. pseudotuberculosis genomic DNA was shown at the level of 101 CFU/mL.
The automated pre-treatment methods for PCR were evaluated in order to work out an effective method of extraction of DNA from foodborne pathogens. We evaluated three commercially automated DNA purification system on the A, B and C corporation for their ability to recover DNA from bacterial cultures and artificially inoculated read-to-eat foods through real-time PCR.
The real-time PCR assay based on PNA (peptide nucleic acid) probe was developed to detect antibiotic resistant genes of pathogenic bacteria. The limit of detection was 10~100 copies/uL. The specificity of real-time PCR (MRSA mecA, ESBL CTX-M1) was tested on 69 strains of S. aureus, 43 strains of E. coli, 100% specificity was obtained.
(출처 : Summary 4p)
 표
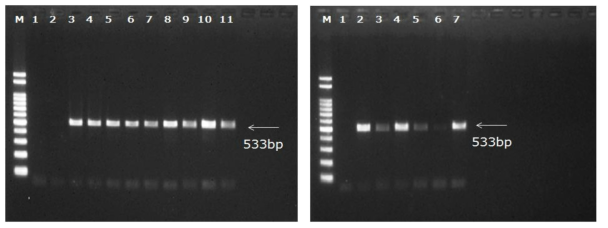
MRSA(mecA) 유전자 conventional PCR 결과 (a) Lanes: M, 100 bp DNA ladder; lane 1 to 2, negative; lane 3, strain 985; lane 4, 399; lane 5, 646; lane 6, 846; lane 7, 639; lane 8, 67; lane 9, 326; lane 10, 1245; lane 11, 325 (b)Lanes: M, 100 bp DNA ladder; lane 1, negative; lane 2, strain 1008; lane 3, 847; lane 4, 481; lane 5, 400; lane 6, 838; lane 7, 363
표
MRSA(mecA) 유전자 conventional PCR 결과 (a) Lanes: M, 100 bp DNA ladder; lane 1 to 2, negative; lane 3, strain 985; lane 4, 399; lane 5, 646; lane 6, 846; lane 7, 639; lane 8, 67; lane 9, 326; lane 10, 1245; lane 11, 325 (b)Lanes: M, 100 bp DNA ladder; lane 1, negative; lane 2, strain 1008; lane 3, 847; lane 4, 481; lane 5, 400; lane 6, 838; lane 7, 363
 표
MRSA(mecA) 유전자 conventional PCR 결과 (a) Lanes: M, 100 bp DNA ladder; lane 1 to 2, negative; lane 3, strain 985; lane 4, 399; lane 5, 646; lane 6, 846; lane 7, 639; lane 8, 67; lane 9, 326; lane 10, 1245; lane 11, 325 (b)Lanes: M, 100 bp DNA ladder; lane 1, negative; lane 2, strain 1008; lane 3, 847; lane 4, 481; lane 5, 400; lane 6, 838; lane 7, 363
표
MRSA(mecA) 유전자 conventional PCR 결과 (a) Lanes: M, 100 bp DNA ladder; lane 1 to 2, negative; lane 3, strain 985; lane 4, 399; lane 5, 646; lane 6, 846; lane 7, 639; lane 8, 67; lane 9, 326; lane 10, 1245; lane 11, 325 (b)Lanes: M, 100 bp DNA ladder; lane 1, negative; lane 2, strain 1008; lane 3, 847; lane 4, 481; lane 5, 400; lane 6, 838; lane 7, 363
| 과제명(ProjectTitle) : | - |
|---|---|
| 연구책임자(Manager) : | - |
| 과제기간(DetailSeriesProject) : | - |
| 총연구비 (DetailSeriesProject) : | - |
| 키워드(keyword) : | - |
| 과제수행기간(LeadAgency) : | - |
| 연구목표(Goal) : | - |
| 연구내용(Abstract) : | - |
| 기대효과(Effect) : | - |
Copyright KISTI. All Rights Reserved.

※ AI-Helper는 부적절한 답변을 할 수 있습니다.